+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Drosophila melanogaster complex I in the Cracked state (Dm3) | |||||||||
 マップデータ マップデータ | Globally sharpened consensus map generated using RELION Postprocess | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  | |||||||||
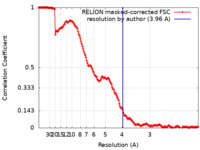
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.96 Å | |||||||||
 データ登録者 データ登録者 | Agip AA / Chung I / Sanchez-Martinez A / Whitworth AJ / Hirst J | |||||||||
| 資金援助 |  英国, 2件 英国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2023 ジャーナル: Elife / 年: 2023タイトル: Cryo-EM structures of mitochondrial respiratory complex I from . 著者: Ahmed-Noor A Agip / Injae Chung / Alvaro Sanchez-Martinez / Alexander J Whitworth / Judy Hirst /  要旨: Respiratory complex I powers ATP synthesis by oxidative phosphorylation, exploiting the energy from NADH oxidation by ubiquinone to drive protons across an energy-transducing membrane. is a ...Respiratory complex I powers ATP synthesis by oxidative phosphorylation, exploiting the energy from NADH oxidation by ubiquinone to drive protons across an energy-transducing membrane. is a candidate model organism for complex I due to its high evolutionary conservation with the mammalian enzyme, well-developed genetic toolkit, and complex physiology for studies in specific cell types and tissues. Here, we isolate complex I from and determine its structure, revealing a 43-subunit assembly with high structural homology to its 45-subunit mammalian counterpart, including a hitherto unknown homologue to subunit NDUFA3. The major conformational state of the enzyme is the mammalian-type 'ready-to-go' active resting state, with a fully ordered and enclosed ubiquinone-binding site, but a subtly altered global conformation related to changes in subunit ND6. The mammalian-type 'deactive' pronounced resting state is not observed: in two minor states, the ubiquinone-binding site is unchanged, but a deactive-type π-bulge is present in ND6-TMH3. Our detailed structural knowledge of complex I provides a foundation for new approaches to disentangle mechanisms of complex I catalysis and regulation in bioenergetics and physiology. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15938.map.gz emd_15938.map.gz | 317.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15938-v30.xml emd-15938-v30.xml emd-15938.xml emd-15938.xml | 24.5 KB 24.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
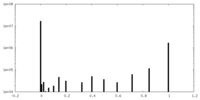
| FSC (解像度算出) |  emd_15938_fsc.xml emd_15938_fsc.xml | 15.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_15938.png emd_15938.png | 84 KB | ||
| マスクデータ |  emd_15938_msk_1.map emd_15938_msk_1.map | 347.6 MB |  マスクマップ マスクマップ | |
| その他 |  emd_15938_additional_1.map.gz emd_15938_additional_1.map.gz emd_15938_half_map_1.map.gz emd_15938_half_map_1.map.gz emd_15938_half_map_2.map.gz emd_15938_half_map_2.map.gz | 287.4 MB 279.6 MB 279.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15938 http://ftp.pdbj.org/pub/emdb/structures/EMD-15938 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15938 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15938 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_15938_validation.pdf.gz emd_15938_validation.pdf.gz | 1003 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_15938_full_validation.pdf.gz emd_15938_full_validation.pdf.gz | 1002.6 KB | 表示 | |
| XML形式データ |  emd_15938_validation.xml.gz emd_15938_validation.xml.gz | 23.3 KB | 表示 | |
| CIF形式データ |  emd_15938_validation.cif.gz emd_15938_validation.cif.gz | 31 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15938 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15938 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15938 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15938 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15938.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15938.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Globally sharpened consensus map generated using RELION Postprocess | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.048 Å | ||||||||||||||||||||||||||||||||||||
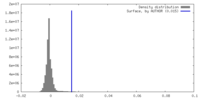
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_15938_msk_1.map emd_15938_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
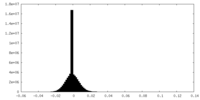
| 密度ヒストグラム |
-追加マップ: Unsharpened and unfiltered consensus map generated using RELION...
| ファイル | emd_15938_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened and unfiltered consensus map generated using RELION Postprocess | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
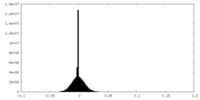
| 密度ヒストグラム |
-ハーフマップ: Half map 2 generated using RELION Postprocess (unsharpened...
| ファイル | emd_15938_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 generated using RELION Postprocess (unsharpened and unfiltered) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1 generated using RELION Postprocess (unsharpened...
| ファイル | emd_15938_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 generated using RELION Postprocess (unsharpened and unfiltered) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Mitochondrial respiratory complex I
| 全体 | 名称: Mitochondrial respiratory complex I |
|---|---|
| 要素 |
|
-超分子 #1: Mitochondrial respiratory complex I
| 超分子 | 名称: Mitochondrial respiratory complex I / タイプ: complex / ID: 1 / キメラ: Yes / 親要素: 0 / 含まれる分子: #1-#43 詳細: Native purification of mitochondrial complex I from Drosophila melanogaster (fruit fly) W1118. |
|---|---|
| 由来(天然) | 生物種:  株: W1118 |
| 分子量 | 理論値: 1 MDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.4 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.8 構成要素:
| ||||||||||||
| グリッド | モデル: UltrAuFoil / 材質: GOLD / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 90 sec. 詳細: Following glow discharge for 90 s at 20 mA, the grid was treated for 7 days in an anaerobic glovebox in ethanol containing 5 mM 11-mercaptoundecyl hexaethyleneglycol, washed three times in ...詳細: Following glow discharge for 90 s at 20 mA, the grid was treated for 7 days in an anaerobic glovebox in ethanol containing 5 mM 11-mercaptoundecyl hexaethyleneglycol, washed three times in ethanol and dried prior to blotting | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: blot for 10 seconds before plunging. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 検出モード: COUNTING / 撮影したグリッド数: 1 / 実像数: 3082 / 平均露光時間: 10.0 sec. / 平均電子線量: 41.88 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| 精密化 | 空間: REAL |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)