+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8gz2 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human NaV1.6/beta1/beta2-4,9-anhydro-tetrodotoxin | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | MEMBRANE PROTEIN / ion channal | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報corticospinal neuron axon guidance / positive regulation of voltage-gated sodium channel activity / response to pyrethroid / voltage-gated sodium channel activity involved in Purkinje myocyte action potential / glutamine synthetase / glutamine biosynthetic process / regulation of sodium ion transmembrane transporter activity / voltage-gated sodium channel activity involved in cardiac muscle cell action potential / glutamine synthetase activity / membrane depolarization during Purkinje myocyte cell action potential ...corticospinal neuron axon guidance / positive regulation of voltage-gated sodium channel activity / response to pyrethroid / voltage-gated sodium channel activity involved in Purkinje myocyte action potential / glutamine synthetase / glutamine biosynthetic process / regulation of sodium ion transmembrane transporter activity / voltage-gated sodium channel activity involved in cardiac muscle cell action potential / glutamine synthetase activity / membrane depolarization during Purkinje myocyte cell action potential / voltage-gated potassium channel activity involved in ventricular cardiac muscle cell action potential repolarization / regulation of atrial cardiac muscle cell membrane depolarization / cardiac conduction / membrane depolarization during cardiac muscle cell action potential / positive regulation of sodium ion transport / node of Ranvier / cardiac muscle cell action potential involved in contraction / locomotion / voltage-gated sodium channel complex / regulation of ventricular cardiac muscle cell membrane repolarization / sodium channel inhibitor activity / neuronal action potential propagation / Interaction between L1 and Ankyrins / voltage-gated sodium channel activity / Phase 0 - rapid depolarisation / regulation of heart rate by cardiac conduction / membrane depolarization / intercalated disc / sodium channel regulator activity / sodium ion transmembrane transport / cardiac muscle contraction / T-tubule / axon guidance / positive regulation of neuron projection development / Sensory perception of sweet, bitter, and umami (glutamate) taste / nervous system development / gene expression / response to heat / chemical synaptic transmission / perikaryon / transmembrane transporter binding / cell adhesion / synapse / extracellular region / ATP binding / metal ion binding / plasma membrane / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.3 Å | ||||||
 データ登録者 データ登録者 | Li, Y. / Jiang, D. | ||||||
| 資金援助 |  中国, 1件 中国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: Structure of human Na1.6 channel reveals Na selectivity and pore blockade by 4,9-anhydro-tetrodotoxin. 著者: Yue Li / Tian Yuan / Bo Huang / Feng Zhou / Chao Peng / Xiaojing Li / Yunlong Qiu / Bei Yang / Yan Zhao / Zhuo Huang / Daohua Jiang /  要旨: The sodium channel Na1.6 is widely expressed in neurons of the central and peripheral nervous systems, which plays a critical role in regulating neuronal excitability. Dysfunction of Na1.6 has been ...The sodium channel Na1.6 is widely expressed in neurons of the central and peripheral nervous systems, which plays a critical role in regulating neuronal excitability. Dysfunction of Na1.6 has been linked to epileptic encephalopathy, intellectual disability and movement disorders. Here we present cryo-EM structures of human Na1.6/β1/β2 alone and complexed with a guanidinium neurotoxin 4,9-anhydro-tetrodotoxin (4,9-ah-TTX), revealing molecular mechanism of Na1.6 inhibition by the blocker. The apo-form structure reveals two potential Na binding sites within the selectivity filter, suggesting a possible mechanism for Na selectivity and conductance. In the 4,9-ah-TTX bound structure, 4,9-ah-TTX binds to a pocket similar to the tetrodotoxin (TTX) binding site, which occupies the Na binding sites and completely blocks the channel. Molecular dynamics simulation results show that subtle conformational differences in the selectivity filter affect the affinity of TTX analogues. Taken together, our results provide important insights into Na1.6 structure, ion conductance, and inhibition. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8gz2.cif.gz 8gz2.cif.gz | 298.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8gz2.ent.gz pdb8gz2.ent.gz | 230.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8gz2.json.gz 8gz2.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8gz2_validation.pdf.gz 8gz2_validation.pdf.gz | 1.5 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8gz2_full_validation.pdf.gz 8gz2_full_validation.pdf.gz | 1.5 MB | 表示 | |
| XML形式データ |  8gz2_validation.xml.gz 8gz2_validation.xml.gz | 52.5 KB | 表示 | |
| CIF形式データ |  8gz2_validation.cif.gz 8gz2_validation.cif.gz | 76.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/gz/8gz2 https://data.pdbj.org/pub/pdb/validation_reports/gz/8gz2 ftp://data.pdbj.org/pub/pdb/validation_reports/gz/8gz2 ftp://data.pdbj.org/pub/pdb/validation_reports/gz/8gz2 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  34388MC  8gz1C M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-Sodium channel subunit beta- ... , 2種, 2分子 DC
| #1: タンパク質 | 分子量: 24732.115 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SCN1B / 細胞株 (発現宿主): HEK293 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SCN1B / 細胞株 (発現宿主): HEK293 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q07699 Homo sapiens (ヒト) / 参照: UniProt: Q07699 |
|---|---|
| #3: タンパク質 | 分子量: 24355.859 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SCN2B, UNQ326/PRO386 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SCN2B, UNQ326/PRO386 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: O60939 Homo sapiens (ヒト) / 参照: UniProt: O60939 |
-タンパク質 / 非ポリマー , 2種, 2分子 B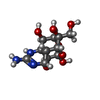

| #2: タンパク質 | 分子量: 225520.609 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SCN8A, MED / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SCN8A, MED / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q9UQD0 Homo sapiens (ヒト) / 参照: UniProt: Q9UQD0 |
|---|---|
| #6: 化合物 | ChemComp-WMK / ( |
-糖 , 2種, 7分子 
| #4: 多糖 | beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta- ...beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose #5: 糖 | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Structure of human voltage-gated sodium channel Nav1.6 in complex with auxiliary beta subunits タイプ: COMPLEX / Entity ID: #1-#3 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2200 nm / 最小 デフォーカス(公称値): 1200 nm / Cs: 2.7 mm |
| 撮影 | 電子線照射量: 9.2 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.18.2_3874: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING ONLY | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 76448 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj






