+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6el1 | ||||||
|---|---|---|---|---|---|---|---|
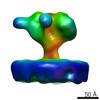
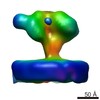
| タイトル | YaxAB pore complex | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | MEMBRANE PROTEIN / Pore-forming toxin / Pathogens / Two-component toxin | ||||||
| 機能・相同性 | : / membrane => GO:0016020 / membrane / Uncharacterized protein / Membrane protein / Alpha-xenorhabdolysin family binary toxin subunit B 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Yersinia enterocolitica (腸炎エルシニア) Yersinia enterocolitica (腸炎エルシニア) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.1 Å | ||||||
 データ登録者 データ登録者 | Braeuning, B. / Bertosin, E. / Dietz, H. / Groll, M. | ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2018 ジャーナル: Nat Commun / 年: 2018タイトル: Structure and mechanism of the two-component α-helical pore-forming toxin YaxAB. 著者: Bastian Bräuning / Eva Bertosin / Florian Praetorius / Christian Ihling / Alexandra Schatt / Agnes Adler / Klaus Richter / Andrea Sinz / Hendrik Dietz / Michael Groll /  要旨: Pore-forming toxins (PFT) are virulence factors that transform from soluble to membrane-bound states. The Yersinia YaxAB system represents a family of binary α-PFTs with orthologues in human, ...Pore-forming toxins (PFT) are virulence factors that transform from soluble to membrane-bound states. The Yersinia YaxAB system represents a family of binary α-PFTs with orthologues in human, insect, and plant pathogens, with unknown structures. YaxAB was shown to be cytotoxic and likely involved in pathogenesis, though the molecular basis for its two-component lytic mechanism remains elusive. Here, we present crystal structures of YaxA and YaxB, together with a cryo-electron microscopy map of the YaxAB complex. Our structures reveal a pore predominantly composed of decamers of YaxA-YaxB heterodimers. Both subunits bear membrane-active moieties, but only YaxA is capable of binding to membranes by itself. YaxB can subsequently be recruited to membrane-associated YaxA and induced to present its lytic transmembrane helices. Pore formation can progress by further oligomerization of YaxA-YaxB dimers. Our results allow for a comparison between pore assemblies belonging to the wider ClyA-like family of α-PFTs, highlighting diverse pore architectures. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6el1.cif.gz 6el1.cif.gz | 1.1 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6el1.ent.gz pdb6el1.ent.gz | 977.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6el1.json.gz 6el1.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6el1_validation.pdf.gz 6el1_validation.pdf.gz | 1000.1 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6el1_full_validation.pdf.gz 6el1_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  6el1_validation.xml.gz 6el1_validation.xml.gz | 176.6 KB | 表示 | |
| CIF形式データ |  6el1_validation.cif.gz 6el1_validation.cif.gz | 269.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/el/6el1 https://data.pdbj.org/pub/pdb/validation_reports/el/6el1 ftp://data.pdbj.org/pub/pdb/validation_reports/el/6el1 ftp://data.pdbj.org/pub/pdb/validation_reports/el/6el1 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 45877.156 Da / 分子数: 10 / 由来タイプ: 組換発現 由来: (組換発現)  Yersinia enterocolitica (腸炎エルシニア) Yersinia enterocolitica (腸炎エルシニア)遺伝子: ERS137951_00706 / 発現宿主:  #2: タンパク質 | 分子量: 39248.836 Da / 分子数: 10 / 由来タイプ: 組換発現 由来: (組換発現)  Yersinia enterocolitica (腸炎エルシニア) Yersinia enterocolitica (腸炎エルシニア)遺伝子: YE1985 / 発現宿主:  |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: YaxAB complex (10x YaxA + 10x YaxB) / タイプ: COMPLEX 詳細: Purified with Cymal-6 detergent and reconstituted in amphipol prior to Cryo-EM. Entity ID: all / 由来: RECOMBINANT | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 0.85 MDa / 実験値: YES | |||||||||||||||
| 由来(天然) | 生物種:  Yersinia enterocolitica (腸炎エルシニア) Yersinia enterocolitica (腸炎エルシニア) | |||||||||||||||
| 由来(組換発現) | 生物種:  | |||||||||||||||
| 緩衝液 | pH: 7 | |||||||||||||||
| 緩衝液成分 |
| |||||||||||||||
| 試料 | 濃度: 2 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: Sample exchanged to amphibole A8-35 and run in final round of gel filtration (buffer: 20 mM HEPES pH 7.0, 100 mM NaCl) prior to Cryo-EM. | |||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 400 divisions/in. / グリッドのタイプ: C-flat-2/1 | |||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 20 K 詳細: 3 mM F-FOS Choline 8 just before vitrification blot for 3 to 4 s blot distance -2 to -1 mm |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 60 e/Å2 / 検出モード: INTEGRATING フィルム・検出器のモデル: FEI FALCON III (4k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.12_2829: / 分類: 精密化 | ||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: NONE | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 178000 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C10 (10回回転対称) | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 6.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 25000 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー









 PDBj
PDBj