[English] 日本語
 Yorodumi
Yorodumi- PDB-6wij: The crystal structure of the 2009/H1N1/California PA endonuclease... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6wij | ||||||
|---|---|---|---|---|---|---|---|
| Title | The crystal structure of the 2009/H1N1/California PA endonuclease mutant I38T in complex with SJ000986448 | ||||||
 Components Components | Polymerase acidic protein | ||||||
 Keywords Keywords | VIRAL PROTEIN / NUCLEASE / INFLUENZA / INHIBITOR RESISTANCE | ||||||
| Function / homology |  Function and homology information Function and homology informationsymbiont-mediated suppression of host gene expression / viral translational frameshifting / viral RNA genome replication / RNA binding / metal ion binding Similarity search - Function | ||||||
| Biological species |   Influenza A virus Influenza A virus | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.44 Å MOLECULAR REPLACEMENT / Resolution: 2.44 Å | ||||||
 Authors Authors | Cuypers, M.G. / Slavish, P.J. / Rankovic, Z. / White, S.W. | ||||||
 Citation Citation |  Journal: Eur.J.Med.Chem. / Year: 2023 Journal: Eur.J.Med.Chem. / Year: 2023Title: Chemical scaffold recycling: Structure-guided conversion of an HIV integrase inhibitor into a potent influenza virus RNA-dependent RNA polymerase inhibitor designed to minimize resistance potential. Authors: Slavish, P.J. / Cuypers, M.G. / Rimmer, M.A. / Abdolvahabi, A. / Jeevan, T. / Kumar, G. / Jarusiewicz, J.A. / Vaithiyalingam, S. / Jones, J.C. / Bowling, J.J. / Price, J.E. / DuBois, R.M. / ...Authors: Slavish, P.J. / Cuypers, M.G. / Rimmer, M.A. / Abdolvahabi, A. / Jeevan, T. / Kumar, G. / Jarusiewicz, J.A. / Vaithiyalingam, S. / Jones, J.C. / Bowling, J.J. / Price, J.E. / DuBois, R.M. / Min, J. / Webby, R.J. / Rankovic, Z. / White, S.W. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6wij.cif.gz 6wij.cif.gz | 96.3 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6wij.ent.gz pdb6wij.ent.gz | 71 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6wij.json.gz 6wij.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/wi/6wij https://data.pdbj.org/pub/pdb/validation_reports/wi/6wij ftp://data.pdbj.org/pub/pdb/validation_reports/wi/6wij ftp://data.pdbj.org/pub/pdb/validation_reports/wi/6wij | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  6v6xC  6v9eC  6vbrC  6vg9C  6vivC  6vjhC  6vl3C  6wj4C  7k87C  7lm4C  7lw6C  7m0nC  7mpfC  7mtyC  7n47C  7n55C  7n68C  7n8fC  7rkpC  7umrC  7uuhC  8dipC  8dpjC  8dtwC  8e4sC  5vptS S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 23136.289 Da / Num. of mol.: 1 / Mutation: I38T Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Influenza A virus, (gene. exp.) Influenza A virus, (gene. exp.)  Influenza A virus (A/Luxembourg/43/2009(H1N1)) Influenza A virus (A/Luxembourg/43/2009(H1N1))Gene: PA-X, PA / Strain: A/Luxembourg/43/2009(H1N1) / Production host:  |
|---|
-Non-polymers , 5 types, 29 molecules 
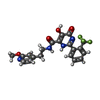
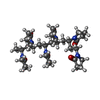






| #2: Chemical | | #3: Chemical | ChemComp-U3A / | #4: Chemical | ChemComp-QQ4 / | #5: Chemical | #6: Water | ChemComp-HOH / | |
|---|
-Details
| Has ligand of interest | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.15 Å3/Da / Density % sol: 60.94 % / Description: elongated rod. |
|---|---|
| Crystal grow | Temperature: 291 K / Method: vapor diffusion, hanging drop Details: 0.1 M HEPES PH 7.8, 1 M AMMONIUM SULFATE, 10 MM MNCL2, 10 MM MGCL2, 0.5% PVP K15 |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 22-ID / Wavelength: 1.7 Å / Beamline: 22-ID / Wavelength: 1.7 Å |
| Detector | Type: DECTRIS EIGER X 16M / Detector: PIXEL / Date: Mar 5, 2020 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.7 Å / Relative weight: 1 |
| Reflection | Resolution: 2.44→74.27 Å / Num. obs: 10430 / % possible obs: 100 % / Redundancy: 20.9 % / Biso Wilson estimate: 67.5 Å2 / CC1/2: 0.995 / Rmerge(I) obs: 0.208 / Rpim(I) all: 0.047 / Rrim(I) all: 0.213 / Χ2: 0.95 / Net I/σ(I): 7.5 |
| Reflection shell | Resolution: 2.44→2.54 Å / Redundancy: 21.6 % / Rmerge(I) obs: 1.464 / Mean I/σ(I) obs: 1.9 / Num. unique obs: 1156 / CC1/2: 0.866 / Rpim(I) all: 0.319 / Rrim(I) all: 1.499 / Χ2: 0.56 / % possible all: 100 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 5vpt Resolution: 2.44→74.27 Å / SU ML: 0.3 / Cross valid method: THROUGHOUT / σ(F): 1.36 / Phase error: 28.51 Details: data merged from 4 independant crystals with CCP4/BLEND then scaled with AIMLESS.
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 154.25 Å2 / Biso mean: 86.8367 Å2 / Biso min: 45.58 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 2.44→74.27 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0 / Total num. of bins used: 4 / % reflection obs: 100 %
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller











 PDBj
PDBj



