+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5fj7 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of the P2 polymerase inside in vitro assembled bacteriophage phi6 polymerase complex, with P1 included | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | VIRAL PROTEIN / BACTERIOPHAGE PHI6 / POLYMERASE COMPLEX / P2 / POLYMERASE / P1 | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報T=2 icosahedral viral capsid / RNA uridylyltransferase activity / viral inner capsid / virion component / viral nucleocapsid / RNA-directed RNA polymerase / viral RNA genome replication / RNA-dependent RNA polymerase activity / nucleotide binding / DNA-templated transcription ...T=2 icosahedral viral capsid / RNA uridylyltransferase activity / viral inner capsid / virion component / viral nucleocapsid / RNA-directed RNA polymerase / viral RNA genome replication / RNA-dependent RNA polymerase activity / nucleotide binding / DNA-templated transcription / RNA binding / identical protein binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  PSEUDOMONAS PHAGE PHI6 (ファージ) PSEUDOMONAS PHAGE PHI6 (ファージ) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.9 Å | ||||||
 データ登録者 データ登録者 | Ilca, S. / Kotecha, A. / Sun, X. / Poranen, M.P. / Stuart, D.I. / Huiskonen, J.T. | ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2015 ジャーナル: Nat Commun / 年: 2015タイトル: Localized reconstruction of subunits from electron cryomicroscopy images of macromolecular complexes. 著者: Serban L Ilca / Abhay Kotecha / Xiaoyu Sun / Minna M Poranen / David I Stuart / Juha T Huiskonen /   要旨: Electron cryomicroscopy can yield near-atomic resolution structures of highly ordered macromolecular complexes. Often however some subunits bind in a flexible manner, have different symmetry from the ...Electron cryomicroscopy can yield near-atomic resolution structures of highly ordered macromolecular complexes. Often however some subunits bind in a flexible manner, have different symmetry from the rest of the complex, or are present in sub-stoichiometric amounts, limiting the attainable resolution. Here we report a general method for the localized three-dimensional reconstruction of such subunits. After determining the particle orientations, local areas corresponding to the subunits can be extracted and treated as single particles. We demonstrate the method using three examples including a flexible assembly and complexes harbouring subunits with either partial occupancy or mismatched symmetry. Most notably, the method allows accurate fitting of the monomeric RNA-dependent RNA polymerase bound at the threefold axis of symmetry inside a viral capsid, revealing for the first time its exact orientation and interactions with the capsid proteins. Localized reconstruction is expected to provide novel biological insights in a range of challenging biological systems. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5fj7.cif.gz 5fj7.cif.gz | 407.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5fj7.ent.gz pdb5fj7.ent.gz | 332.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5fj7.json.gz 5fj7.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  5fj7_validation.pdf.gz 5fj7_validation.pdf.gz | 913.1 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  5fj7_full_validation.pdf.gz 5fj7_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  5fj7_validation.xml.gz 5fj7_validation.xml.gz | 80 KB | 表示 | |
| CIF形式データ |  5fj7_validation.cif.gz 5fj7_validation.cif.gz | 116.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/fj/5fj7 https://data.pdbj.org/pub/pdb/validation_reports/fj/5fj7 ftp://data.pdbj.org/pub/pdb/validation_reports/fj/5fj7 ftp://data.pdbj.org/pub/pdb/validation_reports/fj/5fj7 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  3187MC 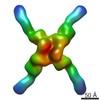 3183C  3184C  3185C  3186C  5fj5C  5fj6C C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10044 (タイトル: In vitro assembled bacteriophage phi6 polymerase complex EMPIAR-10044 (タイトル: In vitro assembled bacteriophage phi6 polymerase complexData size: 8.1 Data #1: Extracted particle stacks of bacteriophage phi6 polymerase complex [picked particles - multiframe - processed]) |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 84163.672 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現)  PSEUDOMONAS PHAGE PHI6 (ファージ) PSEUDOMONAS PHAGE PHI6 (ファージ)プラスミド: PLM358 / 発現宿主:  PSEUDOMONAS SYRINGAE (バクテリア) / 参照: UniProt: P11126 PSEUDOMONAS SYRINGAE (バクテリア) / 参照: UniProt: P11126#2: タンパク質 | | 分子量: 74903.203 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  PSEUDOMONAS PHAGE PHI6 (ファージ) PSEUDOMONAS PHAGE PHI6 (ファージ)プラスミド: PLM358 / 発現宿主:  PSEUDOMONAS SYRINGAE (バクテリア) / 参照: UniProt: P11124 PSEUDOMONAS SYRINGAE (バクテリア) / 参照: UniProt: P11124#3: 化合物 | ChemComp-MN / | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: BACTERIOPHAGE PHI6 POLYMERASE COMPLEX ASSEMBLED IN VITRO タイプ: COMPLEX |
|---|---|
| 緩衝液 | 名称: 50 MM TRIS / pH: 8 / 詳細: 50 MM TRIS |
| 試料 | 濃度: 2.4 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | 詳細: HOLEY CARBON |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE 詳細: VITRIFICATION 1 -- CRYOGEN- ETHANE, TEMPERATURE- 120, INSTRUMENT- FEI VITROBOT MARK IV, METHOD- BLOT 4 SECONDS BEFORE PLUNGING, |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Tecnai F30 / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TECNAI F30 / 日付: 2014年6月12日 / 詳細: DOSE RATE 6-8 E- PER PIX PER S |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 160000 X / 倍率(補正後): 37037 X / 最大 デフォーカス(公称値): 2600 nm / 最小 デフォーカス(公称値): 1100 nm / Cs: 2 mm |
| 試料ホルダ | 温度: 81 K |
| 撮影 | 電子線照射量: 0.16 e/Å2 / フィルム・検出器のモデル: GATAN K2 (4k x 4k) |
| 画像スキャン | デジタル画像の数: 834 |
- 解析
解析
| EMソフトウェア |
| |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | 詳細: EACH PARTICLE | |||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | |||||||||||||||||||||
| 3次元再構成 | 手法: LOCALIZED RECONSTRUCTION / 解像度: 7.9 Å / 粒子像の数: 43216 / ピクセルサイズ(公称値): 1.3 Å / ピクセルサイズ(実測値): 1.35 Å / 倍率補正: ATOMIC MODEL 詳細: SUBMISSION BASED ON EXPERIMENTAL DATA FROM EMDB EMD-3187. (DEPOSITION ID: 13864). 対称性のタイプ: POINT | |||||||||||||||||||||
| 原子モデル構築 | プロトコル: OTHER / 空間: REAL / Target criteria: Cross-correlation coefficient 詳細: METHOD--LOCAL CORRELATION REFINEMENT PROTOCOL--X-RAY | |||||||||||||||||||||
| 原子モデル構築 |
| |||||||||||||||||||||
| 精密化 | 最高解像度: 7.9 Å | |||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 最高解像度: 7.9 Å
|
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj




