| 登録情報 | データベース: PDB / ID: 4yaz
|
|---|
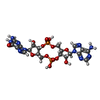
| タイトル | 3',3'-cGAMP riboswitch bound with 3',3'-cGAMP |
|---|
 要素 要素 | RNA (84-MER) |
|---|
 キーワード キーワード |  RNA (リボ核酸) / RNA (リボ核酸) /  riboswitch (リボスイッチ) / 3' / 3'-cGAMP / riboswitch (リボスイッチ) / 3' / 3'-cGAMP /  spinach (ホウレンソウ) / spinach (ホウレンソウ) /  RNA structure (核酸構造) / RNA structure (核酸構造) /  c-di-GMP c-di-GMP |
|---|
| 機能・相同性 | Chem-4BW / : /  リボ核酸 / RNA (> 10) リボ核酸 / RNA (> 10) 機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |   Geobacter (ゲオバクター属) Geobacter (ゲオバクター属) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2 Å 分子置換 / 解像度: 2 Å |
|---|
 データ登録者 データ登録者 | Ren, A.M. / Patel, D.J. / Rajashankar, R.K. |
|---|
| 資金援助 |  米国, 1件 米国, 1件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Cancer Institute (NIH/NCI) | 1 U19 CA179564 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Cell Rep / 年: 2015 ジャーナル: Cell Rep / 年: 2015
タイトル: Structural Basis for Molecular Discrimination by a 3',3'-cGAMP Sensing Riboswitch.
著者: Ren, A. / Wang, X.C. / Kellenberger, C.A. / Rajashankar, K.R. / Jones, R.A. / Hammond, M.C. / Patel, D.J. |
|---|
| 履歴 | | 登録 | 2015年2月18日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2015年4月15日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2015年4月22日 | Group: Database references |
|---|
| 改定 1.2 | 2015年7月22日 | Group: Non-polymer description |
|---|
| 改定 1.3 | 2017年9月27日 | Group: Author supporting evidence / Derived calculations / Source and taxonomy
カテゴリ: entity_src_gen / pdbx_audit_support / pdbx_struct_oper_list
Item: _entity_src_gen.pdbx_alt_source_flag / _pdbx_audit_support.funding_organization / _pdbx_struct_oper_list.symmetry_operation |
|---|
| 改定 1.4 | 2019年12月4日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.5 | 2023年9月27日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description / Structure summary
カテゴリ: chem_comp / chem_comp_atom ...chem_comp / chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI ..._chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_asym_id / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_asym_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード RNA (リボ核酸) /
RNA (リボ核酸) /  riboswitch (リボスイッチ) / 3' / 3'-cGAMP /
riboswitch (リボスイッチ) / 3' / 3'-cGAMP /  spinach (ホウレンソウ) /
spinach (ホウレンソウ) /  RNA structure (核酸構造) /
RNA structure (核酸構造) /  c-di-GMP
c-di-GMP リボ核酸 / RNA (> 10)
リボ核酸 / RNA (> 10) 機能・相同性情報
機能・相同性情報
 Geobacter (ゲオバクター属)
Geobacter (ゲオバクター属) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2 Å
分子置換 / 解像度: 2 Å  データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: Cell Rep / 年: 2015
ジャーナル: Cell Rep / 年: 2015 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4yaz.cif.gz
4yaz.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4yaz.ent.gz
pdb4yaz.ent.gz PDB形式
PDB形式 4yaz.json.gz
4yaz.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ya/4yaz
https://data.pdbj.org/pub/pdb/validation_reports/ya/4yaz ftp://data.pdbj.org/pub/pdb/validation_reports/ya/4yaz
ftp://data.pdbj.org/pub/pdb/validation_reports/ya/4yaz リンク
リンク 集合体
集合体

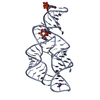
 要素
要素
 Geobacter (ゲオバクター属)
Geobacter (ゲオバクター属) in vitro transcription vector pT7-Fluc(deltai) (In vitro)
in vitro transcription vector pT7-Fluc(deltai) (In vitro) 水
水 X線回折
X線回折 試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 24-ID-C / 波長: 0.9792 Å
/ ビームライン: 24-ID-C / 波長: 0.9792 Å : 0.9792 Å / 相対比: 1
: 0.9792 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj