+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human metHb (C2 symmetry) obtained using the SPT Labtech chameleon | ||||||||||||
 マップデータ マップデータ | Sharpened EM map of metHb without Al's oil; C2 symmetry | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | Hemoglobin / anaerobic / oxygen / heme / OXYGEN BINDING | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nitric oxide transport / hemoglobin alpha binding / cellular oxidant detoxification / hemoglobin binding / organic acid binding / renal absorption / haptoglobin-hemoglobin complex / hemoglobin complex / oxygen transport / Scavenging of heme from plasma ...nitric oxide transport / hemoglobin alpha binding / cellular oxidant detoxification / hemoglobin binding / organic acid binding / renal absorption / haptoglobin-hemoglobin complex / hemoglobin complex / oxygen transport / Scavenging of heme from plasma / endocytic vesicle lumen / blood vessel diameter maintenance / hydrogen peroxide catabolic process / oxygen carrier activity / carbon dioxide transport / Heme signaling / Erythrocytes take up oxygen and release carbon dioxide / Erythrocytes take up carbon dioxide and release oxygen / Late endosomal microautophagy / Cytoprotection by HMOX1 / response to hydrogen peroxide / oxygen binding / regulation of blood pressure / platelet aggregation / Chaperone Mediated Autophagy / positive regulation of nitric oxide biosynthetic process / tertiary granule lumen / Factors involved in megakaryocyte development and platelet production / blood microparticle / ficolin-1-rich granule lumen / iron ion binding / heme binding / Neutrophil degranulation / extracellular space / extracellular exosome / extracellular region / metal ion binding / membrane / cytosol 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
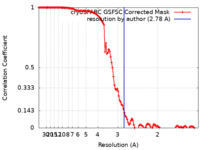
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.78 Å | ||||||||||||
 データ登録者 データ登録者 | Cook BD / Narehood SM / McGuire KL / Li Y / Tezcan FA / Herzik MA | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2025 ジャーナル: Nat Commun / 年: 2025タイトル: Preparation of oxygen-sensitive proteins for high-resolution cryoEM structure determination using blot-free vitrification. 著者: Brian D Cook / Sarah M Narehood / Kelly L McGuire / Yizhou Li / F Akif Tezcan / Mark A Herzik /  要旨: High-quality grid preparation for single-particle cryogenic electron microscopy (cryoEM) remains a bottleneck for routinely obtaining high-resolution structures. The issues that arise from ...High-quality grid preparation for single-particle cryogenic electron microscopy (cryoEM) remains a bottleneck for routinely obtaining high-resolution structures. The issues that arise from traditional grid preparation workflows are particularly exacerbated for oxygen-sensitive proteins, including metalloproteins, whereby oxygen-induced damage and alteration of oxidation states can result in protein inactivation, denaturation, and/or aggregation. Indeed, 99% of the current structures in the EMBD were prepared aerobically and limited successes for anaerobic cryoEM grid preparation exist. Current practices for anaerobic grid preparation involve a vitrification device located in an anoxic chamber, which presents significant challenges including temperature and humidity control, optimization of freezing conditions, costs for purchase and operation, as well as accessibility. Here, we present a streamlined approach that allows for the vitrification of oxygen-sensitive proteins in reduced states using an automated blot-free grid vitrification device - the SPT Labtech chameleon. This robust workflow allows for high-resolution structure determination of dynamic, oxygen-sensitive proteins, of varying complexity and molecular weight. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_45818.map.gz emd_45818.map.gz | 156.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-45818-v30.xml emd-45818-v30.xml emd-45818.xml emd-45818.xml | 24.4 KB 24.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_45818_fsc.xml emd_45818_fsc.xml | 11.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_45818.png emd_45818.png | 43.3 KB | ||
| マスクデータ |  emd_45818_msk_1.map emd_45818_msk_1.map | 166.4 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-45818.cif.gz emd-45818.cif.gz | 6.6 KB | ||
| その他 |  emd_45818_additional_1.map.gz emd_45818_additional_1.map.gz emd_45818_additional_2.map.gz emd_45818_additional_2.map.gz emd_45818_half_map_1.map.gz emd_45818_half_map_1.map.gz emd_45818_half_map_2.map.gz emd_45818_half_map_2.map.gz | 83.1 MB 2.3 MB 154.4 MB 154.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-45818 http://ftp.pdbj.org/pub/emdb/structures/EMD-45818 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-45818 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-45818 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_45818_validation.pdf.gz emd_45818_validation.pdf.gz | 870.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_45818_full_validation.pdf.gz emd_45818_full_validation.pdf.gz | 870.4 KB | 表示 | |
| XML形式データ |  emd_45818_validation.xml.gz emd_45818_validation.xml.gz | 20.3 KB | 表示 | |
| CIF形式データ |  emd_45818_validation.cif.gz emd_45818_validation.cif.gz | 26.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45818 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45818 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45818 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-45818 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9cqpMC  9cqmC  9cqnC  9cqoC  9cqqC  9cqrC  9cqsC  9cqtC  9cquC  9cqvC  9cqwC  9cqxC  9cqyC  9cqzC  9cr0C  9mlyC  9mlzC  9mm0C  9mm1C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_45818.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_45818.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened EM map of metHb without Al's oil; C2 symmetry | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.735 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_45818_msk_1.map emd_45818_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Unsharpened EM map of metHb without Al's oil; C2 symmetry
| ファイル | emd_45818_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened EM map of metHb without Al's oil; C2 symmetry | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: phenix RESOLVE modified EM map of metHb without Al's oil; C2 symmetry
| ファイル | emd_45818_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | phenix RESOLVE modified EM map of metHb without Al's oil; C2 symmetry | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map B of metHb without Al's oil; C2 symmetry
| ファイル | emd_45818_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map B of metHb without Al's oil; C2 symmetry | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map A of metHb without Al's oil; C2 symmetry
| ファイル | emd_45818_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map A of metHb without Al's oil; C2 symmetry | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human metHb (C2 symmetry) determined using the SPT Labtech chamel...
| 全体 | 名称: Human metHb (C2 symmetry) determined using the SPT Labtech chameleon without Al's oil |
|---|---|
| 要素 |
|
-超分子 #1: Human metHb (C2 symmetry) determined using the SPT Labtech chamel...
| 超分子 | 名称: Human metHb (C2 symmetry) determined using the SPT Labtech chameleon without Al's oil タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 64 KDa |
-分子 #1: Hemoglobin subunit alpha
| 分子 | 名称: Hemoglobin subunit alpha / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 14.993159 KDa |
| 配列 | 文字列: VLSPADKTNV KAAWGKVGAH AGEYGAEALE RMFLSFPTTK TYFPHFDLSH GSAQVKGHGK KVADALTNAV AHVDDMPNAL SALSDLHAH KLRVDPVNFK LLSHCLLVTL AAHLPAEFTP AVHASLDKFL ASVSTVLTSK Y UniProtKB: Hemoglobin subunit alpha |
-分子 #2: Hemoglobin subunit beta
| 分子 | 名称: Hemoglobin subunit beta / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 15.890198 KDa |
| 配列 | 文字列: VHLTPEEKSA VTALWGKVNV DEVGGEALGR LLVVYPWTQR FFESFGDLST PDAVMGNPKV KAHGKKVLGA FSDGLAHLDN LKGTFATLS ELHCDKLHVD PENFRLLGNV LVCVLAHHFG KEFTPPVQAA YQKVVAGVAN ALAHKYH UniProtKB: Hemoglobin subunit beta |
-分子 #3: PROTOPORPHYRIN IX CONTAINING FE
| 分子 | 名称: PROTOPORPHYRIN IX CONTAINING FE / タイプ: ligand / ID: 3 / コピー数: 4 / 式: HEM |
|---|---|
| 分子量 | 理論値: 616.487 Da |
| Chemical component information |  ChemComp-HEM: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 8 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 75 % / チャンバー内温度: 298.15 K / 装置: SPOTITON 詳細: Samples were frozen with the SPT Labtech chameleon. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: TFS Selectris X / エネルギーフィルター - スリット幅: 10 eV |
| ソフトウェア | 名称: EPU (ver. 2) |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 2847 / 平均露光時間: 5.0 sec. / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 165000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー



































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)