+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | GluA2 flip Q in complex with TARPgamma2 at pH8, class12, structure of NTD | |||||||||||||||
 マップデータ マップデータ | GluA2 flip Q in complex with TARPgamma2 at pH8, class12, structure of NTD | |||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | AMPA receptor / ionotropic glutamate receptor / ion channel / auxiliary subunit / TRANSPORT PROTEIN | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報spine synapse / dendritic spine neck / dendritic spine head / Activation of AMPA receptors / perisynaptic space / AMPA glutamate receptor activity / ligand-gated monoatomic cation channel activity / Trafficking of GluR2-containing AMPA receptors / response to lithium ion / immunoglobulin binding ...spine synapse / dendritic spine neck / dendritic spine head / Activation of AMPA receptors / perisynaptic space / AMPA glutamate receptor activity / ligand-gated monoatomic cation channel activity / Trafficking of GluR2-containing AMPA receptors / response to lithium ion / immunoglobulin binding / AMPA glutamate receptor complex / kainate selective glutamate receptor activity / ionotropic glutamate receptor complex / extracellularly glutamate-gated ion channel activity / cellular response to glycine / asymmetric synapse / regulation of receptor recycling / Unblocking of NMDA receptors, glutamate binding and activation / positive regulation of synaptic transmission / glutamate receptor binding / extracellular ligand-gated monoatomic ion channel activity / glutamate-gated receptor activity / response to fungicide / glutamate-gated calcium ion channel activity / presynaptic active zone membrane / regulation of synaptic transmission, glutamatergic / somatodendritic compartment / dendrite membrane / cellular response to brain-derived neurotrophic factor stimulus / cytoskeletal protein binding / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / ionotropic glutamate receptor binding / dendrite cytoplasm / ionotropic glutamate receptor signaling pathway / SNARE binding / dendritic shaft / synaptic transmission, glutamatergic / synaptic membrane / PDZ domain binding / transmitter-gated monoatomic ion channel activity involved in regulation of postsynaptic membrane potential / protein tetramerization / postsynaptic density membrane / establishment of protein localization / modulation of chemical synaptic transmission / Schaffer collateral - CA1 synapse / terminal bouton / receptor internalization / cerebral cortex development / synaptic vesicle membrane / synaptic vesicle / presynapse / signaling receptor activity / presynaptic membrane / amyloid-beta binding / growth cone / scaffold protein binding / chemical synaptic transmission / perikaryon / postsynaptic membrane / dendritic spine / postsynaptic density / neuron projection / axon / neuronal cell body / glutamatergic synapse / dendrite / synapse / protein-containing complex binding / protein kinase binding / cell surface / endoplasmic reticulum / protein-containing complex / identical protein binding / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |   | |||||||||||||||
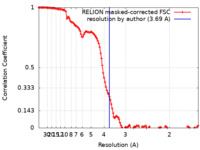
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.69 Å | |||||||||||||||
 データ登録者 データ登録者 | Nakagawa T / Greger IH | |||||||||||||||
| 資金援助 |  米国, 米国,  英国, 4件 英国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2024 ジャーナル: Nat Struct Mol Biol / 年: 2024タイトル: Proton-triggered rearrangement of the AMPA receptor N-terminal domains impacts receptor kinetics and synaptic localization. 著者: Josip Ivica / Nejc Kejzar / Hinze Ho / Imogen Stockwell / Viktor Kuchtiak / Alexander M Scrutton / Terunaga Nakagawa / Ingo H Greger /    要旨: AMPA glutamate receptors (AMPARs) are ion channel tetramers that mediate the majority of fast excitatory synaptic transmission. They are composed of four subunits (GluA1-GluA4); the GluA2 subunit ...AMPA glutamate receptors (AMPARs) are ion channel tetramers that mediate the majority of fast excitatory synaptic transmission. They are composed of four subunits (GluA1-GluA4); the GluA2 subunit dominates AMPAR function throughout the forebrain. Its extracellular N-terminal domain (NTD) determines receptor localization at the synapse, ensuring reliable synaptic transmission and plasticity. This synaptic anchoring function requires a compact NTD tier, stabilized by a GluA2-specific NTD interface. Here we show that low pH conditions, which accompany synaptic activity, rupture this interface. All-atom molecular dynamics simulations reveal that protonation of an interfacial histidine residue (H208) centrally contributes to NTD rearrangement. Moreover, in stark contrast to their canonical compact arrangement at neutral pH, GluA2 cryo-electron microscopy structures exhibit a wide spectrum of NTD conformations under acidic conditions. We show that the consequences of this pH-dependent conformational control are twofold: rupture of the NTD tier slows recovery from desensitized states and increases receptor mobility at mouse hippocampal synapses. Therefore, a proton-triggered NTD switch will shape both AMPAR location and kinetics, thereby impacting synaptic signal transmission. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_44250.map.gz emd_44250.map.gz | 166.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-44250-v30.xml emd-44250-v30.xml emd-44250.xml emd-44250.xml | 24 KB 24 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_44250_fsc.xml emd_44250_fsc.xml | 12.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_44250.png emd_44250.png | 118.7 KB | ||
| Filedesc metadata |  emd-44250.cif.gz emd-44250.cif.gz | 7.1 KB | ||
| その他 |  emd_44250_additional_1.map.gz emd_44250_additional_1.map.gz emd_44250_half_map_1.map.gz emd_44250_half_map_1.map.gz emd_44250_half_map_2.map.gz emd_44250_half_map_2.map.gz | 139.9 MB 140.7 MB 140.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-44250 http://ftp.pdbj.org/pub/emdb/structures/EMD-44250 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-44250 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-44250 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_44250_validation.pdf.gz emd_44250_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_44250_full_validation.pdf.gz emd_44250_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_44250_validation.xml.gz emd_44250_validation.xml.gz | 20 KB | 表示 | |
| CIF形式データ |  emd_44250_validation.cif.gz emd_44250_validation.cif.gz | 26.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-44250 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-44250 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-44250 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-44250 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9b69MC  9b5zC  9b60C  9b61C  9b63C  9b64C  9b67C  9b68C  9b6aC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_44250.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_44250.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | GluA2 flip Q in complex with TARPgamma2 at pH8, class12, structure of NTD | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||
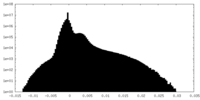
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Un-sharpened map: Half2 map: GluA2 flip Q in...
| ファイル | emd_44250_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Un-sharpened map: Half2 map: GluA2 flip Q in complex with TARPgamma2 at pH8, class12, structure of NTD | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
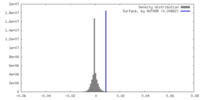
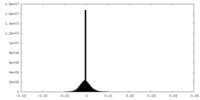
| 密度ヒストグラム |
-ハーフマップ: Half1 map: GluA2 flip Q in complex with...
| ファイル | emd_44250_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half1 map: GluA2 flip Q in complex with TARPgamma2 at pH8, class12, structure of NTD | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
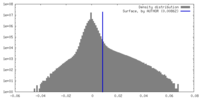
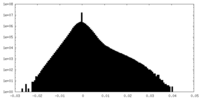
| 密度ヒストグラム |
-ハーフマップ: Half2 map: GluA2 flip Q in complex with...
| ファイル | emd_44250_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half2 map: GluA2 flip Q in complex with TARPgamma2 at pH8, class12, structure of NTD | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
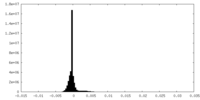
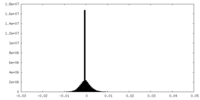
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : GluA2 (flip-Q isoform) in complex with TARPgamma2 at 4:4 stoichiometry
| 全体 | 名称: GluA2 (flip-Q isoform) in complex with TARPgamma2 at 4:4 stoichiometry |
|---|---|
| 要素 |
|
-超分子 #1: GluA2 (flip-Q isoform) in complex with TARPgamma2 at 4:4 stoichiometry
| 超分子 | 名称: GluA2 (flip-Q isoform) in complex with TARPgamma2 at 4:4 stoichiometry タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 分子量 | 理論値: 500 KDa |
-超分子 #2: GluA2 (flip-Q isoform)
| 超分子 | 名称: GluA2 (flip-Q isoform) / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: TARPgamma2
| 超分子 | 名称: TARPgamma2 / タイプ: complex / ID: 3 / 親要素: 1 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Isoform Flip of Glutamate receptor 2
| 分子 | 名称: Isoform Flip of Glutamate receptor 2 / タイプ: protein_or_peptide / ID: 1 / 詳細: A FLAG epitope tag is inserted near the C-terminus / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 99.617492 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MQKIMHISVL LSPVLWGLIF GVSSNSIQIG GLFPRGADQE YSAFRVGMVQ FSTSEFRLTP HIDNLEVANS FAVTNAFCSQ FSRGVYAIF GFYDKKSVNT ITSFCGTLHV SFITPSFPTD GTHPFVIQMR PDLKGALLSL IEYYQWDKFA YLYDSDRGLS T LQAVLDSA ...文字列: MQKIMHISVL LSPVLWGLIF GVSSNSIQIG GLFPRGADQE YSAFRVGMVQ FSTSEFRLTP HIDNLEVANS FAVTNAFCSQ FSRGVYAIF GFYDKKSVNT ITSFCGTLHV SFITPSFPTD GTHPFVIQMR PDLKGALLSL IEYYQWDKFA YLYDSDRGLS T LQAVLDSA AEKKWQVTAI NVGNINNDKK DETYRSLFQD LELKKERRVI LDCERDKVND IVDQVITIGK HVKGYHYIIA NL GFTDGDL LKIQFGGANV SGFQIVDYDD SLVSKFIERW STLEEKEYPG AHTATIKYTS ALTYDAVQVM TEAFRNLRKQ RIE ISRRGN AGDCLANPAV PWGQGVEIER ALKQVQVEGL SGNIKFDQNG KRINYTINIM ELKTNGPRKI GYWSEVDKMV VTLT ELPSG NDTSGLENKT VVVTTILESP YVMMKKNHEM LEGNERYEGY CVDLAAEIAK HCGFKYKLTI VGDGKYGARD ADTKI WNGM VGELVYGKAD IAIAPLTITL VREEVIDFSK PFMSLGISIM IKKPQKSKPG VFSFLDPLAY EIWMCIVFAY IGVSVV LFL VSRFSPYEWH TEEFEDGRET QSSESTNEFG IFNSLWFSLG AFMQQGCDIS PRSLSGRIVG GVWWFFTLII ISSYTAN LA AFLTVERMVS PIESAEDLSK QTEIAYGTLD SGSTKEFFRR SKIAVFDKMW TYMRSAEPSV FVRTTAEGVA RVRKSKGK Y AYLLESTMNE YIEQRKPCDT MKVGGNLDSK GYDIATPKGS SLGTPVNLAV LKLSEQGVLD KLKNKWWYDK GECGAKDSG SKEKTSALSL SNVAGVFYIL VGGLGLAMLV ALIEFCYKSR AEAKRMKVAK NPQNINPSSS QNSQNFATDY KDDDDKEGYN VYGIESVKI UniProtKB: Glutamate receptor 2 |
-分子 #4: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 4 / コピー数: 1 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 10 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: Tris adjusted to pH 8 using HCl | ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 21898 / 平均電子線量: 52.8 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)