登録情報 データベース : EMDB / ID : EMD-32056タイトル Cryo-EM structure of Xenopus laevis nuclear pore complex cytoplasmic ring subunit 複合体 : nuclear pore complex cytoplasmic ring / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
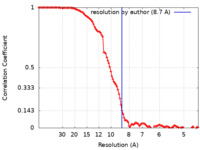
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Xenopus laevis (アフリカツメガエル)手法 / / 解像度 : 8.7 Å Tai L / Zhu Y 資金援助 1件 Organization Grant number 国 Not funded
ジャーナル : Protein Cell / 年 : 2022タイトル : 8 Å structure of the outer rings of the Xenopus laevis nuclear pore complex obtained by cryo-EM and AI.著者 : Linhua Tai / Yun Zhu / He Ren / Xiaojun Huang / Chuanmao Zhang / Fei Sun / 要旨 : The nuclear pore complex (NPC), one of the largest protein complexes in eukaryotes, serves as a physical gate to regulate nucleocytoplasmic transport. Here, we determined the 8 Å resolution cryo- ... The nuclear pore complex (NPC), one of the largest protein complexes in eukaryotes, serves as a physical gate to regulate nucleocytoplasmic transport. Here, we determined the 8 Å resolution cryo-electron microscopic (cryo-EM) structure of the outer rings containing nuclear ring (NR) and cytoplasmic ring (CR) from the Xenopus laevis NPC, with local resolutions reaching 4.9 Å. With the aid of AlphaFold2, we managed to build a pseudoatomic model of the outer rings, including the Y complexes and flanking components. In this most comprehensive and accurate model of outer rings to date, the almost complete Y complex structure exhibits much tighter interaction in the hub region. In addition to two copies of Y complexes, each asymmetric subunit in CR contains five copies of Nup358, two copies of the Nup214 complex, two copies of Nup205 and one copy of newly identified Nup93, while that in NR contains one copy of Nup205, one copy of ELYS and one copy of Nup93. These in-depth structural features represent a great advance in understanding the assembly of NPCs. 履歴 登録 2021年10月14日 - ヘッダ(付随情報) 公開 2022年2月2日 - マップ公開 2022年2月2日 - 更新 2024年6月19日 - 現状 2024年6月19日 処理サイト : PDBj / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報 データ登録者
データ登録者 引用
引用 ジャーナル: Protein Cell / 年: 2022
ジャーナル: Protein Cell / 年: 2022
 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_32056.map.gz
emd_32056.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-32056-v30.xml
emd-32056-v30.xml emd-32056.xml
emd-32056.xml EMDBヘッダ
EMDBヘッダ emd_32056_fsc.xml
emd_32056_fsc.xml FSCデータファイル
FSCデータファイル emd_32056.png
emd_32056.png emd_32056_msk_1.map
emd_32056_msk_1.map マスクマップ
マスクマップ emd-32056.cif.gz
emd-32056.cif.gz emd_32056_half_map_1.map.gz
emd_32056_half_map_1.map.gz emd_32056_half_map_2.map.gz
emd_32056_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-32056
http://ftp.pdbj.org/pub/emdb/structures/EMD-32056 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32056
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32056 emd_32056_validation.pdf.gz
emd_32056_validation.pdf.gz EMDB検証レポート
EMDB検証レポート emd_32056_full_validation.pdf.gz
emd_32056_full_validation.pdf.gz emd_32056_validation.xml.gz
emd_32056_validation.xml.gz emd_32056_validation.cif.gz
emd_32056_validation.cif.gz https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32056
https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32056 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32056
ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32056 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_32056.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_32056.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) emd_32056_msk_1.map
emd_32056_msk_1.map 試料の構成要素
試料の構成要素 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 ムービー
ムービー コントローラー
コントローラー























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)