+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-2853 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | 3BNC117 Fab in complex with BG505 SOSIP.664 Trimer | |||||||||
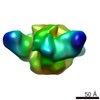
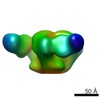
 マップデータ マップデータ | Single particle reconstruction (20 Angstrom resolution based on FSC 0.5) | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HIV / Fab / Env trimer | |||||||||
| 生物種 |   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / ネガティブ染色法 / 解像度: 20.0 Å | |||||||||
 データ登録者 データ登録者 | Ozorowski G / Derking R / Sanders RW / Ward AB | |||||||||
 引用 引用 |  ジャーナル: PLoS Pathog / 年: 2015 ジャーナル: PLoS Pathog / 年: 2015タイトル: Comprehensive antigenic map of a cleaved soluble HIV-1 envelope trimer. 著者: Ronald Derking / Gabriel Ozorowski / Kwinten Sliepen / Anila Yasmeen / Albert Cupo / Jonathan L Torres / Jean-Philippe Julien / Jeong Hyun Lee / Thijs van Montfort / Steven W de Taeye / Mark ...著者: Ronald Derking / Gabriel Ozorowski / Kwinten Sliepen / Anila Yasmeen / Albert Cupo / Jonathan L Torres / Jean-Philippe Julien / Jeong Hyun Lee / Thijs van Montfort / Steven W de Taeye / Mark Connors / Dennis R Burton / Ian A Wilson / Per-Johan Klasse / Andrew B Ward / John P Moore / Rogier W Sanders /    要旨: The trimeric envelope (Env) spike is the focus of vaccine design efforts aimed at generating broadly neutralizing antibodies (bNAbs) to protect against HIV-1 infection. Three recent developments have ...The trimeric envelope (Env) spike is the focus of vaccine design efforts aimed at generating broadly neutralizing antibodies (bNAbs) to protect against HIV-1 infection. Three recent developments have facilitated a thorough investigation of the antigenic structure of the Env trimer: 1) the isolation of many bNAbs against multiple different epitopes; 2) the generation of a soluble trimer mimic, BG505 SOSIP.664 gp140, that expresses most bNAb epitopes; 3) facile binding assays involving the oriented immobilization of tagged trimers. Using these tools, we generated an antigenic map of the trimer by antibody cross-competition. Our analysis delineates three well-defined epitope clusters (CD4 binding site, quaternary V1V2 and Asn332-centered oligomannose patch) and new epitopes at the gp120-gp41 interface. It also identifies the relationships among these clusters. In addition to epitope overlap, we defined three more ways in which antibodies can cross-compete: steric competition from binding to proximal but non-overlapping epitopes (e.g., PGT151 inhibition of 8ANC195 binding); allosteric inhibition (e.g., PGT145 inhibition of 1NC9, 8ANC195, PGT151 and CD4 binding); and competition by reorientation of glycans (e.g., PGT135 inhibition of CD4bs bNAbs, and CD4bs bNAb inhibition of 8ANC195). We further demonstrate that bNAb binding can be complex, often affecting several other areas of the trimer surface beyond the epitope. This extensive analysis of the antigenic structure and the epitope interrelationships of the Env trimer should aid in design of both bNAb-based therapies and vaccines intended to induce bNAbs. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_2853.map.gz emd_2853.map.gz | 14.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-2853-v30.xml emd-2853-v30.xml emd-2853.xml emd-2853.xml | 11.1 KB 11.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  EMD-2853_3BNC117_BG505.png EMD-2853_3BNC117_BG505.png | 29.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-2853 http://ftp.pdbj.org/pub/emdb/structures/EMD-2853 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2853 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2853 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_2853_validation.pdf.gz emd_2853_validation.pdf.gz | 198.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_2853_full_validation.pdf.gz emd_2853_full_validation.pdf.gz | 197.6 KB | 表示 | |
| XML形式データ |  emd_2853_validation.xml.gz emd_2853_validation.xml.gz | 6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2853 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2853 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2853 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2853 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_2853.map.gz / 形式: CCP4 / 大きさ: 15.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_2853.map.gz / 形式: CCP4 / 大きさ: 15.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Single particle reconstruction (20 Angstrom resolution based on FSC 0.5) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.05 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
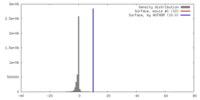
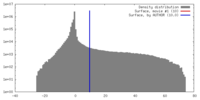
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Fab of 3BNC117 monoclonal antibody bound to recombinant HIV-1 Env...
| 全体 | 名称: Fab of 3BNC117 monoclonal antibody bound to recombinant HIV-1 Env gp140 BG505 SOSIP.664 trimer |
|---|---|
| 要素 |
|
-超分子 #1000: Fab of 3BNC117 monoclonal antibody bound to recombinant HIV-1 Env...
| 超分子 | 名称: Fab of 3BNC117 monoclonal antibody bound to recombinant HIV-1 Env gp140 BG505 SOSIP.664 trimer タイプ: sample / ID: 1000 詳細: Size-exclusion chromatography purified gp140 trimers were used 集合状態: One Fab molecule binds to one BG505 SOSIP.664 gp140 monomer Number unique components: 2 |
|---|---|
| 分子量 | 理論値: 570 KDa 手法: Theoretical MW of Fab based on primary sequence; MW of trimer estimated using published values |
-分子 #1: Soluble HIV-1 Envelope glycoprotein
| 分子 | 名称: Soluble HIV-1 Envelope glycoprotein / タイプ: protein_or_peptide / ID: 1 / Name.synonym: SOSIP 詳細: gp140 trimers were expressed recombinantly and purified using 2G12-affinity and size-exclusion chromatography コピー数: 1 / 集合状態: Trimer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス)株: BG505 / 別称: HIV-1 |
| 分子量 | 理論値: 420 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換細胞: HEK293F / 組換プラスミド: pPPI4 Homo sapiens (ヒト) / 組換細胞: HEK293F / 組換プラスミド: pPPI4 |
-分子 #2: Fab of 3BNC117 human monoclonal antibody
| 分子 | 名称: Fab of 3BNC117 human monoclonal antibody / タイプ: protein_or_peptide / ID: 2 詳細: Expressed recombinantly as IgG and cleaved into Fab using papain コピー数: 1 / 集合状態: Dimer composed of heavy and light chain / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 別称: Human Homo sapiens (ヒト) / 別称: Human |
| 分子量 | 理論値: 50 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換細胞: HEK293F Homo sapiens (ヒト) / 組換細胞: HEK293F |
-実験情報
-構造解析
| 手法 | ネガティブ染色法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.01 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 詳細: 50 mM Tris-HCl pH 7.4, 150 mM NaCl |
| 染色 | タイプ: NEGATIVE 詳細: 3 microliters of 2% w/v uranyl formate were added to grids adsorbed with protein for 45 seconds and blotted |
| グリッド | 詳細: 400 Cu mesh grid with carbon support, plasma cleaned |
| 凍結 | 凍結剤: NONE / 装置: OTHER |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI 12 |
|---|---|
| アライメント法 | Legacy - 非点収差: Objective lens astigmatism corrected at 52,000x mag |
| 日付 | 2014年9月29日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: TVIPS TEMCAM-F416 (4k x 4k) 実像数: 145 / 平均電子線量: 25 e/Å2 |
| Tilt angle max | 0 |
| 電子線 | 加速電圧: 120 kV / 電子線源: LAB6 |
| 電子光学系 | 倍率(補正後): 52000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 52000 |
| 試料ステージ | 試料ホルダーモデル: SIDE ENTRY, EUCENTRIC / Tilt angle min: -50 |
- 画像解析
画像解析
| 詳細 | Particles were selected using an automatic selection program. A substack was created containing particles with 3 Fab molecules per trimer. An initial common-lines model was created using class averages and further refined using projection matching and an unbinned stack of particles. |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C3 (3回回転対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 20.0 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: EMAN2, SPARX / 使用した粒子像数: 14956 |
 ムービー
ムービー コントローラー
コントローラー



 UCSF Chimera
UCSF Chimera









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)