+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-24001 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Thermotoga maritima encapsulin shell | |||||||||
 マップデータ マップデータ | Final cryo-EM map for the T maritima encapsulin shell | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Encapsulin / Ferritin-like protein / EncFLP / Thermotoga / FMN / Bacterial Nanocompartment / VIRUS LIKE PARTICLE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報encapsulin nanocompartment / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素 / peptidase activity / iron ion transport / intracellular iron ion homeostasis / proteolysis 類似検索 - 分子機能 | |||||||||
| 生物種 |   Thermotoga maritima (バクテリア) Thermotoga maritima (バクテリア) | |||||||||
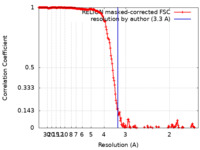
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.3 Å | |||||||||
 データ登録者 データ登録者 | LaFrance BJ / Nogales E | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Sci Rep / 年: 2021 ジャーナル: Sci Rep / 年: 2021タイトル: The encapsulin from Thermotoga maritima is a flavoprotein with a symmetry matched ferritin-like cargo protein. 著者: Benjamin J LaFrance / Caleb Cassidy-Amstutz / Robert J Nichols / Luke M Oltrogge / Eva Nogales / David F Savage /  要旨: Bacterial nanocompartments, also known as encapsulins, are an emerging class of protein-based 'organelles' found in bacteria and archaea. Encapsulins are virus-like icosahedral particles comprising a ...Bacterial nanocompartments, also known as encapsulins, are an emerging class of protein-based 'organelles' found in bacteria and archaea. Encapsulins are virus-like icosahedral particles comprising a ~ 25-50 nm shell surrounding a specific cargo enzyme. Compartmentalization is thought to create a unique chemical environment to facilitate catalysis and isolate toxic intermediates. Many questions regarding nanocompartment structure-function remain unanswered, including how shell symmetry dictates cargo loading and to what extent the shell facilitates enzymatic activity. Here, we explore these questions using the model Thermotoga maritima nanocompartment known to encapsulate a redox-active ferritin-like protein. Biochemical analysis revealed the encapsulin shell to possess a flavin binding site located at the interface between capsomere subunits, suggesting the shell may play a direct and active role in the function of the encapsulated cargo. Furthermore, we used cryo-EM to show that cargo proteins use a form of symmetry-matching to facilitate encapsulation and define stoichiometry. In the case of the Thermotoga maritima encapsulin, the decameric cargo protein with fivefold symmetry preferentially binds to the pentameric-axis of the icosahedral shell. Taken together, these observations suggest the shell is not simply a passive barrier-it also plays a significant role in the structure and function of the cargo enzyme. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_24001.map.gz emd_24001.map.gz | 46 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-24001-v30.xml emd-24001-v30.xml emd-24001.xml emd-24001.xml | 14.2 KB 14.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_24001_fsc.xml emd_24001_fsc.xml | 18.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_24001.png emd_24001.png | 261.3 KB | ||
| マスクデータ |  emd_24001_msk_1.map emd_24001_msk_1.map | 512 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-24001.cif.gz emd-24001.cif.gz | 6.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-24001 http://ftp.pdbj.org/pub/emdb/structures/EMD-24001 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24001 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24001 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_24001.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_24001.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Final cryo-EM map for the T maritima encapsulin shell | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_24001_msk_1.map emd_24001_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : 3.3A cryo-EM map of the T. maritima encapsulin shell
| 全体 | 名称: 3.3A cryo-EM map of the T. maritima encapsulin shell |
|---|---|
| 要素 |
|
-超分子 #1: 3.3A cryo-EM map of the T. maritima encapsulin shell
| 超分子 | 名称: 3.3A cryo-EM map of the T. maritima encapsulin shell タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Thermotoga maritima (バクテリア) Thermotoga maritima (バクテリア) |
| 分子量 | 理論値: 1.83 MDa |
-分子 #1: Maritimacin
| 分子 | 名称: Maritimacin / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO EC番号: 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素 |
|---|---|
| 由来(天然) | 生物種:   Thermotoga maritima (バクテリア) Thermotoga maritima (バクテリア) |
| 分子量 | 理論値: 30.369615 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MEFLKRSFAP LTEKQWQEID NRAREIFKTQ LYGRKFVDVE GPYGWEYAAH PLGEVEVLSD ENEVVKWGLR KSLPLIELRA TFTLDLWEL DNLERGKPNV DLSSLEETVR KVAEFEDEVI FRGCEKSGVK GLLSFEERKI ECGSTPKDLL EAIVRALSIF S KDGIEGPY ...文字列: MEFLKRSFAP LTEKQWQEID NRAREIFKTQ LYGRKFVDVE GPYGWEYAAH PLGEVEVLSD ENEVVKWGLR KSLPLIELRA TFTLDLWEL DNLERGKPNV DLSSLEETVR KVAEFEDEVI FRGCEKSGVK GLLSFEERKI ECGSTPKDLL EAIVRALSIF S KDGIEGPY TLVINTDRWI NFLKEEAGHY PLEKRVEECL RGGKIITTPR IEDALVVSER GGDFKLILGQ DLSIGYEDRE KD AVRLFIT ETFTFQVVNP EALILLK UniProtKB: Type 1 encapsulin shell protein |
-分子 #2: FLAVIN MONONUCLEOTIDE
| 分子 | 名称: FLAVIN MONONUCLEOTIDE / タイプ: ligand / ID: 2 / コピー数: 1 / 式: FMN |
|---|---|
| 分子量 | 理論値: 456.344 Da |
| Chemical component information |  ChemComp-FMN: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.0 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 詳細: 20 mM Tris-HCl, pH 7.4, 150 mM NaCl and 5 mM 2-mercaptoethanol |
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 400 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 20 sec. |
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: blot force. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3838 pixel / デジタル化 - サイズ - 縦: 3710 pixel / 撮影したグリッド数: 1 / 実像数: 1276 / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 1.5 µm |
| 試料ステージ | 試料ホルダーモデル: GATAN 626 SINGLE TILT LIQUID NITROGEN CRYO TRANSFER HOLDER ホルダー冷却材: NITROGEN |
 ムービー
ムービー コントローラー
コントローラー















 Z
Z Y
Y X
X