+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21583 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | +3 extended HIV-1 reverse transcriptase initiation complex core (pre-translocation state) | |||||||||
 マップデータ マップデータ | +3 extended HIV-1 reverse transcriptase initiation complex core (pre-translocation state) | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | reverse transcriptase / RNA / protein-RNA complex / tRNA / polymerase / VIRAL PROTEIN / VIRAL PROTEIN-RNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報integrase activity / Integration of viral DNA into host genomic DNA / Autointegration results in viral DNA circles / Minus-strand DNA synthesis / Plus-strand DNA synthesis / Uncoating of the HIV Virion / 2-LTR circle formation / Vpr-mediated nuclear import of PICs / Early Phase of HIV Life Cycle / Integration of provirus ...integrase activity / Integration of viral DNA into host genomic DNA / Autointegration results in viral DNA circles / Minus-strand DNA synthesis / Plus-strand DNA synthesis / Uncoating of the HIV Virion / 2-LTR circle formation / Vpr-mediated nuclear import of PICs / Early Phase of HIV Life Cycle / Integration of provirus / APOBEC3G mediated resistance to HIV-1 infection / Binding and entry of HIV virion / viral life cycle / HIV-1 retropepsin / symbiont-mediated activation of host apoptosis / retroviral ribonuclease H / exoribonuclease H / exoribonuclease H activity / Assembly Of The HIV Virion / Budding and maturation of HIV virion / DNA integration / protein processing / viral genome integration into host DNA / establishment of integrated proviral latency / RNA-directed DNA polymerase / RNA stem-loop binding / viral penetration into host nucleus / host multivesicular body / RNA-directed DNA polymerase activity / RNA-DNA hybrid ribonuclease activity / 転移酵素; リンを含む基を移すもの; 核酸を移すもの / peptidase activity / host cell / viral nucleocapsid / DNA recombination / DNA-directed DNA polymerase / aspartic-type endopeptidase activity / 加水分解酵素; エステル加水分解酵素 / DNA-directed DNA polymerase activity / symbiont-mediated suppression of host gene expression / viral translational frameshifting / symbiont entry into host cell / lipid binding / host cell plasma membrane / host cell nucleus / virion membrane / structural molecule activity / proteolysis / DNA binding / zinc ion binding / identical protein binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.2 Å | |||||||||
 データ登録者 データ登録者 | Larsen KP / Jackson LN | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: J Mol Biol / 年: 2020 ジャーナル: J Mol Biol / 年: 2020タイトル: Distinct Conformational States Underlie Pausing during Initiation of HIV-1 Reverse Transcription. 著者: Kevin P Larsen / Junhong Choi / Lynnette N Jackson / Kalli Kappel / Jingji Zhang / Betty Ha / Dong-Hua Chen / Elisabetta Viani Puglisi /  要旨: A hallmark of the initiation step of HIV-1 reverse transcription, in which viral RNA genome is converted into double-stranded DNA, is that it is slow and non-processive. Biochemical studies have ...A hallmark of the initiation step of HIV-1 reverse transcription, in which viral RNA genome is converted into double-stranded DNA, is that it is slow and non-processive. Biochemical studies have identified specific sites along the viral RNA genomic template in which reverse transcriptase (RT) stalls. These stalling points, which occur after the addition of three and five template dNTPs, may serve as checkpoints to regulate the precise timing of HIV-1 reverse transcription following viral entry. Structural studies of reverse transcriptase initiation complexes (RTICs) have revealed unique conformations that may explain the slow rate of incorporation; however, questions remain about the temporal evolution of the complex and features that contribute to strong pausing during initiation. Here we present cryo-electron microscopy and single-molecule characterization of an RTIC after three rounds of dNTP incorporation (+3), the first major pausing point during reverse transcription initiation. Cryo-electron microscopy structures of a +3 extended RTIC reveal conformational heterogeneity within the RTIC core. Three distinct conformations were identified, two of which adopt unique, likely off-pathway, intermediates in the canonical polymerization cycle. Single-molecule Förster resonance energy transfer experiments confirm that the +3 RTIC is more structurally dynamic than earlier-stage RTICs. These alternative conformations were selectively disrupted through structure-guided point mutations to shift single-molecule Förster resonance energy transfer populations back toward the on-pathway conformation. Our results support the hypothesis that conformational heterogeneity within the HIV-1 RTIC during pausing serves as an additional means of regulating HIV-1 replication. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21583.map.gz emd_21583.map.gz | 59.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21583-v30.xml emd-21583-v30.xml emd-21583.xml emd-21583.xml | 18.2 KB 18.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_21583.png emd_21583.png | 128.6 KB | ||
| Filedesc metadata |  emd-21583.cif.gz emd-21583.cif.gz | 6.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21583 http://ftp.pdbj.org/pub/emdb/structures/EMD-21583 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21583 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21583 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21583.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21583.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | +3 extended HIV-1 reverse transcriptase initiation complex core (pre-translocation state) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
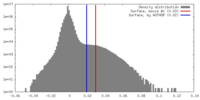
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : +3 extended HIV-1 reverse transcriptase initiation complex core (...
| 全体 | 名称: +3 extended HIV-1 reverse transcriptase initiation complex core (pre-translocation state) |
|---|---|
| 要素 |
|
-超分子 #1: +3 extended HIV-1 reverse transcriptase initiation complex core (...
| 超分子 | 名称: +3 extended HIV-1 reverse transcriptase initiation complex core (pre-translocation state) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Peripheral dynamic RNA elements belonging to the tRNA lysine 3 primer and the HIV-1 viral RNA genomic template have been masked out during cryo-EM data processing. |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 25 KDa |
-超分子 #2: HIV-1 reverse transcriptase
| 超分子 | 名称: HIV-1 reverse transcriptase / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#2 詳細: The C-terminus of p66 contains an unstructured linker and a six-histidine tag that was cleaved prior to full complex formation. |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
-超分子 #3: HIV-1 RNA genome fragment
| 超分子 | 名称: HIV-1 RNA genome fragment / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #3 詳細: A fragment of the HIV-1 RNA genome that is 101 nucleotides in length. |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
-超分子 #4: tRNA lysine 3
| 超分子 | 名称: tRNA lysine 3 / タイプ: complex / ID: 4 / 親要素: 1 / 含まれる分子: #4 詳細: Chemically synthesized and extended tRNA lysine 3. A modified dG containing an N2-cystamine was placed at position 71 and the sequence was extended on the 3' end by a dC, dT, and ddG to bring ...詳細: Chemically synthesized and extended tRNA lysine 3. A modified dG containing an N2-cystamine was placed at position 71 and the sequence was extended on the 3' end by a dC, dT, and ddG to bring its total length to 79 nucleotides. |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Reverse transcriptase/ribonuclease H
| 分子 | 名称: Reverse transcriptase/ribonuclease H / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: RNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 65.55832 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MVPISPIETV PVKLKPGMDG PKVKQWPLTE EKIKALVEIC TEMEKEGKIS KIGPENPYNT PVFAIKKKDS TKWRKLVDFR ELNKRTQDF WEVQLGIPHP AGLKKKKSVT VLDVGDAYFS VPLDEDFRKY TAFTIPSINN ETPGIRYQYN VLPQGWKGSP A IFQSSMTK ...文字列: MVPISPIETV PVKLKPGMDG PKVKQWPLTE EKIKALVEIC TEMEKEGKIS KIGPENPYNT PVFAIKKKDS TKWRKLVDFR ELNKRTQDF WEVQLGIPHP AGLKKKKSVT VLDVGDAYFS VPLDEDFRKY TAFTIPSINN ETPGIRYQYN VLPQGWKGSP A IFQSSMTK ILEPFKKQNP DIVIYQYMDD LYVGSDLEIG QHRTKIEELR QHLLRWGLTT PDKKHQKEPP FLWMGYELHP DK WTVQPIV LPEKDSWTVN DICKLVGKLN WASQIYPGIK VRQLSKLLRG TKALTEVIPL TEEAELELAE NREILKEPVH GVY YDPSKD LIAEIQKQGQ GQWTYQIYQE PFKNLKTGKY ARMRGAHTND VKQLTEAVQK ITTESIVIWG KTPKFKLPIQ KETW ETWWT EYWQATWIPE WEFVNTPPLV KLWYQLEKEP IVGAETFYVD GAANRETKLG KAGYVTNKGR QKVVPLTNTT NQKTQ LQAI YLALQDSGLE VNIVTDSQYA LGIIQAQPDK SESELVNQII EQLIKKEKVY LAWVPAHKGI GGNEQVDKLV SAGIRK ILD LGTLVPR UniProtKB: Gag-Pol polyprotein |
-分子 #2: reverse transcriptase p51 subunit
| 分子 | 名称: reverse transcriptase p51 subunit / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 51.585293 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MVPISPIETV PVKLKPGMDG PKVKQWPLTE EKIKALVEIC TEMEKEGKIS KIGPENPYNT PVFAIKKKDS TKWRKLVDFR ELNKRTQDF WEVQLGIPHP AGLKKKKSVT VLDVGDAYFS VPLDEDFRKY TAFTIPSINN ETPGIRYQYN VLPQGWKGSP A IFQSSMTK ...文字列: MVPISPIETV PVKLKPGMDG PKVKQWPLTE EKIKALVEIC TEMEKEGKIS KIGPENPYNT PVFAIKKKDS TKWRKLVDFR ELNKRTQDF WEVQLGIPHP AGLKKKKSVT VLDVGDAYFS VPLDEDFRKY TAFTIPSINN ETPGIRYQYN VLPQGWKGSP A IFQSSMTK ILEPFKKQNP DIVIYQYMDD LYVGSDLEIG QHRTKIEELR QHLLRWGLTT PDKKHQKEPP FLWMGYELHP DK WTVQPIV LPEKDSWTVN DIQKLVGKLN WASQIYPGIK VRQLSKLLRG TKALTEVIPL TEEAELELAE NREILKEPVH GVY YDPSKD LIAEIQKQGQ GQWTYQIYQE PFKNLKTGKY ARMRGAHTND VKQLTEAVQK ITTESIVIWG KTPKFKLPIQ KETW ETWWT EYWQATWIPE WEFVNTPPLV KLWYQLEKEP IVGAETF UniProtKB: Gag-Pol polyprotein |
-分子 #3: HIV-1 viral RNA genome fragment
| 分子 | 名称: HIV-1 viral RNA genome fragment / タイプ: rna / ID: 3 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 32.623477 KDa |
| 配列 | 文字列: GACUCUGGUA ACUAGAGAUC CCUCAGACCC UUUUAGUCAG UGUGGAAAAU CUCUAGCAGU GGCGCCCGAA CAGGGACUUG AAAGCGAAA GUAAAGCCAG AG GENBANK: GENBANK: AY835748.1 |
-分子 #4: tRNA lysine 3
| 分子 | 名称: tRNA lysine 3 / タイプ: other / ID: 4 / コピー数: 1 / 分類: polydeoxyribonucleotide/polyribonucleotide hybrid |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 25.354061 KDa |
| 配列 | 文字列: GCCCGGAUAG CUCAGUCGGU AGAGCAUCAG ACUUUUAAUC UGAGGGUCCA GGGUUCAAGU CCCUGUUCGG GC(DG)CCA (DC)(DT)(DG) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5.0 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: Full complex was prepared 5-8 hours before freezing. Beta-OG was added just prior to freezing. | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 292 K / 装置: LEICA EM GP / 詳細: 3 microliters applied, 2s pre-blot, 2.5s blot.. | |||||||||||||||
| 詳細 | Sample was monodisperse. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 77.6 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL |
|---|---|
| 得られたモデル |  PDB-6wb0: |
 ムービー
ムービー コントローラー
コントローラー





























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)