+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21232 | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | BG505 SOSIP.v5.2 in complex with rhesus macaque Fab RM20E1 and PGT122 Fab | ||||||||||||||||||
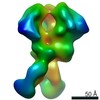
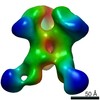
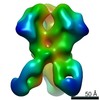
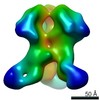
 マップデータ マップデータ | BG505 SOSIP.v5.2 in complex with Rhesus macaque Fab RM20E1 and PGT122 Fab | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | HIV / antibody / Fab / vaccine / VIRAL PROTEIN / VIRAL PROTEIN-IMMUNE SYSTEM complex | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / virus-mediated perturbation of host defense response / fusion of virus membrane with host endosome membrane / viral envelope ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / virus-mediated perturbation of host defense response / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / apoptotic process / host cell plasma membrane / structural molecule activity / virion membrane / identical protein binding / plasma membrane 類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  | ||||||||||||||||||
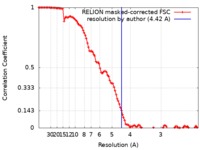
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.42 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Cottrell CA / Ward AB / Patel R | ||||||||||||||||||
| 資金援助 |  米国, 5件 米国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: PLoS Pathog / 年: 2020 ジャーナル: PLoS Pathog / 年: 2020タイトル: Mapping the immunogenic landscape of near-native HIV-1 envelope trimers in non-human primates. 著者: Christopher A Cottrell / Jelle van Schooten / Charles A Bowman / Meng Yuan / David Oyen / Mia Shin / Robert Morpurgo / Patricia van der Woude / Mariëlle van Breemen / Jonathan L Torres / Raj ...著者: Christopher A Cottrell / Jelle van Schooten / Charles A Bowman / Meng Yuan / David Oyen / Mia Shin / Robert Morpurgo / Patricia van der Woude / Mariëlle van Breemen / Jonathan L Torres / Raj Patel / Justin Gross / Leigh M Sewall / Jeffrey Copps / Gabriel Ozorowski / Bartek Nogal / Devin Sok / Eva G Rakasz / Celia Labranche / Vladimir Vigdorovich / Scott Christley / Diane G Carnathan / D Noah Sather / David Montefiori / Guido Silvestri / Dennis R Burton / John P Moore / Ian A Wilson / Rogier W Sanders / Andrew B Ward / Marit J van Gils /   要旨: The induction of broad and potent immunity by vaccines is the key focus of research efforts aimed at protecting against HIV-1 infection. Soluble native-like HIV-1 envelope glycoproteins have shown ...The induction of broad and potent immunity by vaccines is the key focus of research efforts aimed at protecting against HIV-1 infection. Soluble native-like HIV-1 envelope glycoproteins have shown promise as vaccine candidates as they can induce potent autologous neutralizing responses in rabbits and non-human primates. In this study, monoclonal antibodies were isolated and characterized from rhesus macaques immunized with the BG505 SOSIP.664 trimer to better understand vaccine-induced antibody responses. Our studies reveal a diverse landscape of antibodies recognizing immunodominant strain-specific epitopes and non-neutralizing neo-epitopes. Additionally, we isolated a subset of mAbs against an epitope cluster at the gp120-gp41 interface that recognize the highly conserved fusion peptide and the glycan at position 88 and have characteristics akin to several human-derived broadly neutralizing antibodies. #1:  ジャーナル: Biorxiv / 年: 2020 ジャーナル: Biorxiv / 年: 2020タイトル: Mapping the immunogenic landscape of native HIV-1 envelope trimers in non-human primates 著者: Cottrell CA / van Schooten J / Bowman CA / Yuan M / Oyen D / Shin M / Morpurgo R / van der Woude P / van Breemen M / Torres JL / Patel R / Gross J / Sewall LM / Copps J / Ozorowski G / Sok D ...著者: Cottrell CA / van Schooten J / Bowman CA / Yuan M / Oyen D / Shin M / Morpurgo R / van der Woude P / van Breemen M / Torres JL / Patel R / Gross J / Sewall LM / Copps J / Ozorowski G / Sok D / Rakasz EG / Labranche C / Vigdorovich V / Christley S / Sather DN / Montefiori D / Moore JP / Burton DR / Wilson IA / Sanders RW / Ward AB / van Gils MJ | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
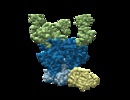
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21232.map.gz emd_21232.map.gz | 95.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21232-v30.xml emd-21232-v30.xml emd-21232.xml emd-21232.xml | 25.8 KB 25.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_21232_fsc.xml emd_21232_fsc.xml | 10.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_21232.png emd_21232.png | 131.6 KB | ||
| マスクデータ |  emd_21232_msk_1.map emd_21232_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-21232.cif.gz emd-21232.cif.gz | 7.4 KB | ||
| その他 |  emd_21232_half_map_1.map.gz emd_21232_half_map_1.map.gz emd_21232_half_map_2.map.gz emd_21232_half_map_2.map.gz | 95.5 MB 95.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21232 http://ftp.pdbj.org/pub/emdb/structures/EMD-21232 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21232 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21232 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_21232_validation.pdf.gz emd_21232_validation.pdf.gz | 1.3 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_21232_full_validation.pdf.gz emd_21232_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  emd_21232_validation.xml.gz emd_21232_validation.xml.gz | 17.6 KB | 表示 | |
| CIF形式データ |  emd_21232_validation.cif.gz emd_21232_validation.cif.gz | 23.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21232 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21232 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21232 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21232 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21232.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21232.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | BG505 SOSIP.v5.2 in complex with Rhesus macaque Fab RM20E1 and PGT122 Fab | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.15 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_21232_msk_1.map emd_21232_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: BG505 SOSIP.v5.2 in complex with Rhesus macaque Fab...
| ファイル | emd_21232_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | BG505 SOSIP.v5.2 in complex with Rhesus macaque Fab RM20E1 and PGT122 Fab | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: BG505 SOSIP.v5.2 in complex with Rhesus macaque Fab...
| ファイル | emd_21232_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | BG505 SOSIP.v5.2 in complex with Rhesus macaque Fab RM20E1 and PGT122 Fab | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : BG505 SOSIP.v5.2 in complex with rhesus macaque Fab RM20E1
| 全体 | 名称: BG505 SOSIP.v5.2 in complex with rhesus macaque Fab RM20E1 |
|---|---|
| 要素 |
|
-超分子 #1: BG505 SOSIP.v5.2 in complex with rhesus macaque Fab RM20E1
| 超分子 | 名称: BG505 SOSIP.v5.2 in complex with rhesus macaque Fab RM20E1 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#6 |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
-分子 #1: Envelope glycoprotein gp120
| 分子 | 名称: Envelope glycoprotein gp120 / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 53.268371 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: AENLWVTVYY GVPVWKDAET TLFCASDAKA YETKKHNVWA THCCVPTDPN PQEIHLENVT EEFNMWKNNM VEQMHTDIIS LWDQSLKPC VKLTPLCVTL QCTNVTNNIT DDMRGELKNC SFNMTTELRD KKQKVYSLFY RLDVVQINEN QGNRSNNSNK E YRLINCNT ...文字列: AENLWVTVYY GVPVWKDAET TLFCASDAKA YETKKHNVWA THCCVPTDPN PQEIHLENVT EEFNMWKNNM VEQMHTDIIS LWDQSLKPC VKLTPLCVTL QCTNVTNNIT DDMRGELKNC SFNMTTELRD KKQKVYSLFY RLDVVQINEN QGNRSNNSNK E YRLINCNT SAITQACPKV SFEPIPIHYC APAGFAILKC KDKKFNGTGP CPSVSTVQCT HGIKPVVSTQ LLLNGSLAEE EV MIRSENI TNNAKNILVQ FNTPVQINCT RPNNNTRKSI RIGPGQWFYA TGDIIGDIRQ AHCNVSKATW NETLGKVVKQ LRK HFGNNT IIRFANSSGG DLEVTTHSFN CGGEFFYCNT SGLFNSTWIS NTSVQGSNST GSNDSITLPC RIKQIINMWQ RIGQ AMYAP PIQGVIRCVS NITGLILTRD GGSTNSTTET FRPGGGDMRD NWRSELYKYK VVKIEPLGVA PTRCKRRVVG UniProtKB: Envelope glycoprotein gp160 |
-分子 #2: BG505 SOSIPv5.2 gp41
| 分子 | 名称: BG505 SOSIPv5.2 gp41 / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 17.178549 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: AVGIGAVFLG FLGAAGSTMG AASMTLTVQA RNLLSGIVQQ QSNLLRAPEC QQHLLKLTVW GIKQLQARVL AVERYLRDQQ LLGIWGCSG KLICCTNVPW NSSWSNRNLS EIWDNMTWLQ WDKEISNYTQ IIYGLLEESQ NQQEKNEQDL LALD UniProtKB: Envelope glycoprotein gp160 |
-分子 #3: PGT122 Fab Heavy Chain
| 分子 | 名称: PGT122 Fab Heavy Chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 14.838731 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QVHLQESGPG LVKPSETLSL TCNVSGTLVR DNYWSWIRQP LGKQPEWIGY VHDSGDTNYN PSLKSRVHLS LDKSKNLVSL RLTGVTAAD SAIYYCATTK HGRRIYGVVA FKEWFTYFYM DVWGKGTSVT VSS |
-分子 #4: PGT122 Fab Light Chain
| 分子 | 名称: PGT122 Fab Light Chain / タイプ: protein_or_peptide / ID: 4 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 11.510612 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: TFVSVAPGQT ARITCGEESL GSRSVIWYQQ RPGQAPSLII YNNNDRPSGI PDRFSGSPGS TFGTTATLTI TSVEAGDEAD YYCHIWDSR RPTNWVFGEG TTLIVLS |
-分子 #5: RM20E1 Fab Heavy Chain
| 分子 | 名称: RM20E1 Fab Heavy Chain / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 13.878558 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVQSEAE VKRPGESLKI SCQTSGYNFP NYWITWVRQM PGKGLEWMGT IDPRDSDTKY SPSFQGQVTI SADKSINTAY LQWTSLRAS DSATYYCVMW VYILTTGNIW VDVWGPGVLV TVSS |
-分子 #6: RM20E1 Fab Kappa Chain
| 分子 | 名称: RM20E1 Fab Kappa Chain / タイプ: protein_or_peptide / ID: 6 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 12.370759 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: DVVMTQSPLS LPITPGQPAS ISCRSSQSLV HNNGNTYLTW YQQRPGQPPR RLIYQVSNRD SGVPDRFIGS GAGTDFTLKI SRVESEDVG IYYCGQITDF PYSFGQGTKV DIK |
-分子 #12: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 12 / コピー数: 24 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 51.3 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: OTHER |
|---|---|
| 得られたモデル |  PDB-6vlr: |
 ムービー
ムービー コントローラー
コントローラー




















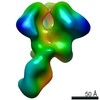

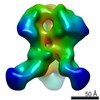


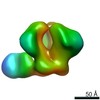





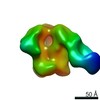




















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)