登録情報 データベース : EMDB / ID : EMD-20288タイトル The E. coli class-II CAP-dependent transcription activation complex at the state 2 classII CAP-TAC at state 2 複合体 : The E. coli class-II CAP-dependent transcription activation complex at the state 2複合体 : DNA-directed RNA polymerase subunit alpha, DNA-directed RNA polymerase subunit beta, DNA-directed RNA polymerase subunit beta', DNA-directed RNA polymerase subunit omega, RNA polymerase sigma factor RpoD, cAMP-activated global transcriptional regulator CRP複合体 : DNAリガンド : x 3種 / / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Escherichia coli (大腸菌)手法 / / 解像度 : 4.29 Å Liu B / Shi W ジャーナル : PLoS Biol / 年 : 2020タイトル : Visualization of two architectures in class-II CAP-dependent transcription activation.著者 : Wei Shi / Yanan Jiang / Yibin Deng / Zigang Dong / Bin Liu / 要旨 : Transcription activation by cyclic AMP (cAMP) receptor protein (CAP) is the classic paradigm of transcription regulation in bacteria. CAP was suggested to activate transcription on class-II promoters ... Transcription activation by cyclic AMP (cAMP) receptor protein (CAP) is the classic paradigm of transcription regulation in bacteria. CAP was suggested to activate transcription on class-II promoters via a recruitment and isomerization mechanism. However, whether and how it modifies RNA polymerase (RNAP) to initiate transcription remains unclear. Here, we report cryo-electron microscopy (cryo-EM) structures of an intact Escherichia coli class-II CAP-dependent transcription activation complex (CAP-TAC) with and without de novo RNA transcript. The structures reveal two distinct architectures of TAC and raise the possibility that CAP binding may induce substantial conformational changes in all the subunits of RNAP and transiently widen the main cleft of RNAP to facilitate DNA promoter entering and formation of the initiation open complex. These structural changes vanish during further RNA transcript synthesis. The observations in this study may reveal a possible on-pathway intermediate and suggest a possibility that CAP activates transcription by inducing intermediate state, in addition to the previously proposed stabilization mechanism. 履歴 登録 2019年6月13日 - ヘッダ(付随情報) 公開 2019年11月27日 - マップ公開 2020年3月18日 - 更新 2024年5月15日 - 現状 2024年5月15日 処理サイト : RCSB / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 引用
引用 ジャーナル: PLoS Biol / 年: 2020
ジャーナル: PLoS Biol / 年: 2020

 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_20288.map.gz
emd_20288.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-20288-v30.xml
emd-20288-v30.xml emd-20288.xml
emd-20288.xml EMDBヘッダ
EMDBヘッダ emd_20288.png
emd_20288.png emd-20288.cif.gz
emd-20288.cif.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-20288
http://ftp.pdbj.org/pub/emdb/structures/EMD-20288 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20288
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20288 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
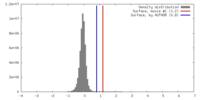
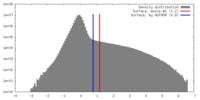
マップ ダウンロード / ファイル: emd_20288.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_20288.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) 試料の構成要素
試料の構成要素 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 画像解析
画像解析 ムービー
ムービー コントローラー
コントローラー





















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)