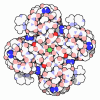
登録情報 データベース : PDB / ID : 1k4cタイトル Potassium Channel KcsA-Fab complex in high concentration of K+ (antibody Fab fragment ...) x 2 potassium channel KcsA キーワード / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / 生物種 Streptomyces lividans (バクテリア)Mus musculus (ハツカネズミ)手法 / / / 解像度 : 2 Å データ登録者 Zhou, Y. / Morais-Cabral, J.H. / Kaufman, A. / MacKinnon, R. ジャーナル : Nature / 年 : 2001タイトル : Chemistry of ion coordination and hydration revealed by a K+ channel-Fab complex at 2.0 A resolution.著者 : Zhou, Y. / Morais-Cabral, J.H. / Kaufman, A. / MacKinnon, R. 履歴 登録 2001年10月7日 登録サイト / 処理サイト 改定 1.0 2001年11月14日 Provider / タイプ 改定 1.1 2008年4月27日 Group 改定 1.2 2011年7月13日 Group 改定 1.3 2011年11月16日 Group 改定 1.4 2021年10月27日 Group / Derived calculationsカテゴリ database_2 / pdbx_struct_conn_angle ... database_2 / pdbx_struct_conn_angle / struct_conn / struct_ref_seq_dif / struct_site Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr1_symmetry / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.ptnr3_symmetry / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr1_symmetry / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_conn.ptnr2_symmetry / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id 改定 1.5 2024年10月30日 Group / Structure summaryカテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / pdbx_entry_details / pdbx_modification_feature
すべて表示 表示を減らす Remark 99 Some fragments of disordered amino acids were built as solvent(water) molecules with the following ... Some fragments of disordered amino acids were built as solvent(water) molecules with the following sequence numbers: 106, 129, 165, 205, 206, 228, 251, 301, 309, 316, 318, 328, 330, 351, 365, 400, 408, 423 and 466. The water molecules 1, 2, 3, 4 are near the potassium ion pathway inside molecule KcsA.
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Streptomyces lividans (バクテリア)
Streptomyces lividans (バクテリア)
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2 Å
分子置換 / 解像度: 2 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Nature / 年: 2001
ジャーナル: Nature / 年: 2001 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1k4c.cif.gz
1k4c.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1k4c.ent.gz
pdb1k4c.ent.gz PDB形式
PDB形式 1k4c.json.gz
1k4c.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 1k4c_validation.pdf.gz
1k4c_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 1k4c_full_validation.pdf.gz
1k4c_full_validation.pdf.gz 1k4c_validation.xml.gz
1k4c_validation.xml.gz 1k4c_validation.cif.gz
1k4c_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/k4/1k4c
https://data.pdbj.org/pub/pdb/validation_reports/k4/1k4c ftp://data.pdbj.org/pub/pdb/validation_reports/k4/1k4c
ftp://data.pdbj.org/pub/pdb/validation_reports/k4/1k4c リンク
リンク 集合体
集合体

 要素
要素 Streptomyces lividans (バクテリア)
Streptomyces lividans (バクテリア)








 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  CHESS
CHESS  / ビームライン: A1 / 波長: 0.93 Å
/ ビームライン: A1 / 波長: 0.93 Å 解析
解析 分子置換 / 解像度: 2→40 Å / Rfactor Rfree error: 0.001 / Data cutoff high absF: 3462539.1 / Data cutoff low absF: 0 / 交差検証法: THROUGHOUT / σ(F): 0
分子置換 / 解像度: 2→40 Å / Rfactor Rfree error: 0.001 / Data cutoff high absF: 3462539.1 / Data cutoff low absF: 0 / 交差検証法: THROUGHOUT / σ(F): 0  ムービー
ムービー コントローラー
コントローラー























 PDBj
PDBj