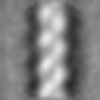+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 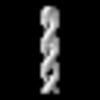 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | cryo sub-tomogram average of Ald4 filaments from purified meiotic yeast mitochondria | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | metabolic enzyme / filament / cryoET / mitochondria / CYTOSOLIC PROTEIN | |||||||||
| 生物種 |   | |||||||||
| 手法 | サブトモグラム平均法 / クライオ電子顕微鏡法 / 解像度: 44.0 Å | |||||||||
 データ登録者 データ登録者 | Hugener J / Xu J / Wettstein R / Ioannidi L / Velikov D / Wollweber F / Henggeler A / Matos J / Pilhofer M | |||||||||
| 資金援助 |  スイス, European Union, 2件 スイス, European Union, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2024 ジャーナル: Cell / 年: 2024タイトル: FilamentID reveals the composition and function of metabolic enzyme polymers during gametogenesis. 著者: Jannik Hugener / Jingwei Xu / Rahel Wettstein / Lydia Ioannidi / Daniel Velikov / Florian Wollweber / Adrian Henggeler / Joao Matos / Martin Pilhofer /   要旨: Gamete formation and subsequent offspring development often involve extended phases of suspended cellular development or even dormancy. How cells adapt to recover and resume growth remains poorly ...Gamete formation and subsequent offspring development often involve extended phases of suspended cellular development or even dormancy. How cells adapt to recover and resume growth remains poorly understood. Here, we visualized budding yeast cells undergoing meiosis by cryo-electron tomography (cryoET) and discovered elaborate filamentous assemblies decorating the nucleus, cytoplasm, and mitochondria. To determine filament composition, we developed a "filament identification" (FilamentID) workflow that combines multiscale cryoET/cryo-electron microscopy (cryoEM) analyses of partially lysed cells or organelles. FilamentID identified the mitochondrial filaments as being composed of the conserved aldehyde dehydrogenase Ald4 and the nucleoplasmic/cytoplasmic filaments as consisting of acetyl-coenzyme A (CoA) synthetase Acs1. Structural characterization further revealed the mechanism underlying polymerization and enabled us to genetically perturb filament formation. Acs1 polymerization facilitates the recovery of chronologically aged spores and, more generally, the cell cycle re-entry of starved cells. FilamentID is broadly applicable to characterize filaments of unknown identity in diverse cellular contexts. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_19552.map.gz emd_19552.map.gz | 119.6 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-19552-v30.xml emd-19552-v30.xml emd-19552.xml emd-19552.xml | 13.5 KB 13.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_19552.png emd_19552.png | 13 KB | ||
| Filedesc metadata |  emd-19552.cif.gz emd-19552.cif.gz | 4.8 KB | ||
| その他 |  emd_19552_half_map_1.map.gz emd_19552_half_map_1.map.gz emd_19552_half_map_2.map.gz emd_19552_half_map_2.map.gz | 106.3 KB 106.4 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-19552 http://ftp.pdbj.org/pub/emdb/structures/EMD-19552 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19552 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19552 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_19552_validation.pdf.gz emd_19552_validation.pdf.gz | 616.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_19552_full_validation.pdf.gz emd_19552_full_validation.pdf.gz | 616.4 KB | 表示 | |
| XML形式データ |  emd_19552_validation.xml.gz emd_19552_validation.xml.gz | 5.6 KB | 表示 | |
| CIF形式データ |  emd_19552_validation.cif.gz emd_19552_validation.cif.gz | 6.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19552 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19552 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19552 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19552 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_19552.map.gz / 形式: CCP4 / 大きさ: 128.9 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_19552.map.gz / 形式: CCP4 / 大きさ: 128.9 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 11 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_19552_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
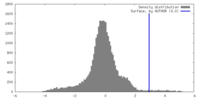
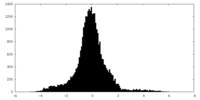
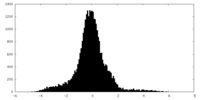
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_19552_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
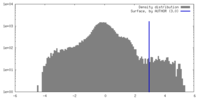
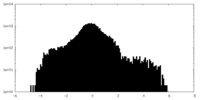
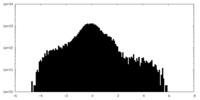
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Ald4 polymer from purified meiotic yeast mitochondria
| 全体 | 名称: Ald4 polymer from purified meiotic yeast mitochondria |
|---|---|
| 要素 |
|
-超分子 #1: Ald4 polymer from purified meiotic yeast mitochondria
| 超分子 | 名称: Ald4 polymer from purified meiotic yeast mitochondria タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Aldehyde dehydrogenase 4
| 分子 | 名称: Aldehyde dehydrogenase 4 / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: MFSRSTLCLK TSASSIGRL Q LRYFSHLP MT VPIKLPN GLE YEQPTG LFIN NKFVP SKQNK TFEV INPSTE EEI CHIYEGR ED DVEEAVQA A DRAFSNGSW NGIDPIDRGK ALYRLAELI E QDKDVIAS IE TLDNGKA ISS SRGDVD LVIN YLKSS ...文字列: MFSRSTLCLK TSASSIGRL Q LRYFSHLP MT VPIKLPN GLE YEQPTG LFIN NKFVP SKQNK TFEV INPSTE EEI CHIYEGR ED DVEEAVQA A DRAFSNGSW NGIDPIDRGK ALYRLAELI E QDKDVIAS IE TLDNGKA ISS SRGDVD LVIN YLKSS AGFAD KIDG RMIDTG RTH FSYTKRQ PL GVCGQIIP W NFPLLMWAW KIAPALVTGN TVVLKTAES T PLSALYVS KY IPQAGIP PGV INIVSG FGKI VGEAI TNHPK IKKV AFTGST ATG RHIYQSA AA GLKKVTLE L GGKSPNIVF ADAELKKAVQ NIILGIYYN S GEVCCAGS RV YVEESIY DKF IEEFKA ASES IKVGD PFDES TFQG AQTSQM QLN KILKYVD IG KNEGATLI T GGERLGSKG YFIKPTVFGD VKEDMRIVK E EIFGPVVT VT KFKSADE VIN MANDSE YGLA AGIHT SNINT ALKV ADRVNA GTV WINTYND FH HAVPFGGF N ASGLGREMS VDALQNYLQV KAVRAKLDE |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | helical array |
- 試料調製
試料調製
| 緩衝液 | pH: 7.2 |
|---|---|
| 凍結 | 凍結剤: ETHANE-PROPANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 2.62 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 8.0 µm / 最小 デフォーカス(公称値): 8.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 想定した対称性 - 点群: C2 (2回回転対称) / 解像度のタイプ: BY AUTHOR / 解像度: 44.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用したサブトモグラム数: 564 |
|---|---|
| 抽出 | トモグラム数: 3 / 使用した粒子像数: 564 |
| 最終 角度割当 | タイプ: ANGULAR RECONSTITUTION / ソフトウェア - 名称: RELION |
 ムービー
ムービー コントローラー
コントローラー







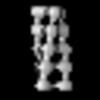
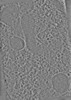

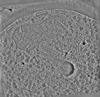
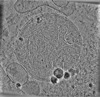



 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)