+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Hepatitis B core protein with bound P1dC | ||||||||||||||||||
 マップデータ マップデータ | |||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | Hepatitis B core protein / Spikes dimeric peptide binder aggregator Hepatitis B virus Capsid LIKE PARTICLE / VIRUS LIKE PARTICLE | ||||||||||||||||||
| 機能・相同性 | Hepatitis B virus, capsid N-terminal / Hepatitis core protein, putative zinc finger / Hepatitis core antigen / Viral capsid core domain supefamily, Hepatitis B virus / Hepatitis core antigen / virus-mediated perturbation of host defense response / structural molecule activity / extracellular region / External core antigen 機能・相同性情報 機能・相同性情報 | ||||||||||||||||||
| 生物種 |   Hepatitis B virus (B 型肝炎ウイルス) / synthetic construct (人工物) Hepatitis B virus (B 型肝炎ウイルス) / synthetic construct (人工物) | ||||||||||||||||||
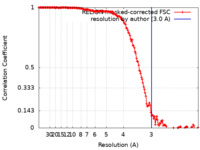
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.0 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Makbul C / Khayenko V / Maric MH / Bottcher B | ||||||||||||||||||
| 資金援助 |  ドイツ, 5件 ドイツ, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Peptide dimers aggregate Hepatitis B core proteins in live cells 著者: Khayenko V / Makbul C / Schulte C / Hemmelmann N / Bottcher B / Maric HM | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_18000.map.gz emd_18000.map.gz | 301.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-18000-v30.xml emd-18000-v30.xml emd-18000.xml emd-18000.xml | 19.6 KB 19.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_18000_fsc.xml emd_18000_fsc.xml | 15.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_18000.png emd_18000.png | 254.4 KB | ||
| マスクデータ |  emd_18000_msk_1.map emd_18000_msk_1.map | 325 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-18000.cif.gz emd-18000.cif.gz | 6.3 KB | ||
| その他 |  emd_18000_half_map_1.map.gz emd_18000_half_map_1.map.gz emd_18000_half_map_2.map.gz emd_18000_half_map_2.map.gz | 300.2 MB 300.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-18000 http://ftp.pdbj.org/pub/emdb/structures/EMD-18000 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18000 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18000 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_18000_validation.pdf.gz emd_18000_validation.pdf.gz | 1.3 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_18000_full_validation.pdf.gz emd_18000_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  emd_18000_validation.xml.gz emd_18000_validation.xml.gz | 23.5 KB | 表示 | |
| CIF形式データ |  emd_18000_validation.cif.gz emd_18000_validation.cif.gz | 31.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18000 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18000 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18000 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18000 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_18000.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_18000.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.0635 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_18000_msk_1.map emd_18000_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
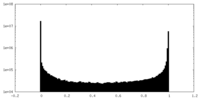
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_18000_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
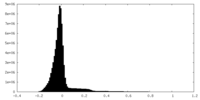
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_18000_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
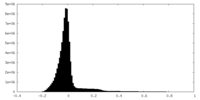
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Hepatitis B virus
| 全体 | 名称:   Hepatitis B virus (B 型肝炎ウイルス) Hepatitis B virus (B 型肝炎ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Hepatitis B virus
| 超分子 | 名称: Hepatitis B virus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / NCBI-ID: 10407 / 生物種: Hepatitis B virus / Sci species strain: ayw/France/Tiollais/1979 / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: OTHER / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 5 MDa |
| ウイルス殻 | Shell ID: 1 / 直径: 360.0 Å / T番号(三角分割数): 4 |
-分子 #1: External core antigen
| 分子 | 名称: External core antigen / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Hepatitis B virus (B 型肝炎ウイルス) Hepatitis B virus (B 型肝炎ウイルス) |
| 分子量 | 理論値: 21.146217 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MDIDPYKEFG ATVELLSFLP SDFFPSVRDL LDTASALYRE ALESPEHCSP HHTALRQAIL CWGELMTLAT WVGVNLEDPA SRDLVVSYV NTNMGLKFRQ LLWFHISCLT FGRETVIEYL VSFGVWIRTP PAYRPPNAPI LSTLPETTVV RRRGRSPRRR T PSPRRRRS QSPRRRRSQS RESQC UniProtKB: External core antigen |
-分子 #2: P1dC
| 分子 | 名称: P1dC / タイプ: protein_or_peptide / ID: 2 詳細: The binder consists of 2 peptide moieties linked by a PEG-linker: The peptide moiety is 'MHRSLLGRMKGA' The resolved density has a length of 6 residues of the moiety. The position is ...詳細: The binder consists of 2 peptide moieties linked by a PEG-linker: The peptide moiety is 'MHRSLLGRMKGA' The resolved density has a length of 6 residues of the moiety. The position is unresolved and modelled as Poly-Ala コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 1.039273 KDa |
| 配列 | 文字列: (UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: PLASMA CLEANING / 前処理 - 時間: 120 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.029 kPa |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 2784 / 平均露光時間: 2.5 sec. / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 1.4000000000000001 µm 最小 デフォーカス(公称値): 0.9 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)