+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of cytochrome bc1 complex (complex-III) from respiratory supercomplex of Tetrahymena thermophila | |||||||||||||||
 マップデータ マップデータ | Sharpened mask refined map | |||||||||||||||
 試料 試料 |
| |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報quinol-cytochrome-c reductase / protein processing involved in protein targeting to mitochondrion / : / ubiquinol-cytochrome-c reductase activity / mitochondrial electron transport, ubiquinol to cytochrome c / : / metalloendopeptidase activity / 2 iron, 2 sulfur cluster binding / mitochondrial inner membrane / electron transfer activity ...quinol-cytochrome-c reductase / protein processing involved in protein targeting to mitochondrion / : / ubiquinol-cytochrome-c reductase activity / mitochondrial electron transport, ubiquinol to cytochrome c / : / metalloendopeptidase activity / 2 iron, 2 sulfur cluster binding / mitochondrial inner membrane / electron transfer activity / oxidoreductase activity / heme binding / mitochondrion / membrane / metal ion binding / plasma membrane 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |   Tetrahymena thermophila SB210 (真核生物) Tetrahymena thermophila SB210 (真核生物) | |||||||||||||||
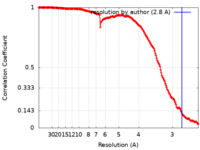
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.8 Å | |||||||||||||||
 データ登録者 データ登録者 | Muhleip A / Kock Flygaard R / Amunts A | |||||||||||||||
| 資金援助 |  スウェーデン, European Union, 4件 スウェーデン, European Union, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2023 ジャーナル: Nature / 年: 2023タイトル: Structural basis of mitochondrial membrane bending by the I-II-III-IV supercomplex. 著者: Alexander Mühleip / Rasmus Kock Flygaard / Rozbeh Baradaran / Outi Haapanen / Thomas Gruhl / Victor Tobiasson / Amandine Maréchal / Vivek Sharma / Alexey Amunts /      要旨: Mitochondrial energy conversion requires an intricate architecture of the inner mitochondrial membrane. Here we show that a supercomplex containing all four respiratory chain components contributes ...Mitochondrial energy conversion requires an intricate architecture of the inner mitochondrial membrane. Here we show that a supercomplex containing all four respiratory chain components contributes to membrane curvature induction in ciliates. We report cryo-electron microscopy and cryo-tomography structures of the supercomplex that comprises 150 different proteins and 311 bound lipids, forming a stable 5.8-MDa assembly. Owing to subunit acquisition and extension, complex I associates with a complex IV dimer, generating a wedge-shaped gap that serves as a binding site for complex II. Together with a tilted complex III dimer association, it results in a curved membrane region. Using molecular dynamics simulations, we demonstrate that the divergent supercomplex actively contributes to the membrane curvature induction and tubulation of cristae. Our findings highlight how the evolution of protein subunits of respiratory complexes has led to the I-II-III-IV supercomplex that contributes to the shaping of the bioenergetic membrane, thereby enabling its functional specialization. #1:  ジャーナル: Biorxiv / 年: 2022 ジャーナル: Biorxiv / 年: 2022タイトル: Structural basis of mitochondrial membrane bending by I-II-III2-IV2 supercomplex 著者: Muhleip A / Flygaard RK / Haapanen O / Baradaran R / Gruhl T / Tobiasson V / Marechal A / Sharma V / Amunts A | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15868.map.gz emd_15868.map.gz | 398.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15868-v30.xml emd-15868-v30.xml emd-15868.xml emd-15868.xml | 35.9 KB 35.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_15868_fsc.xml emd_15868_fsc.xml | 16.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_15868.png emd_15868.png | 79.3 KB | ||
| マスクデータ |  emd_15868_msk_1.map emd_15868_msk_1.map | 421.9 MB |  マスクマップ マスクマップ | |
| その他 |  emd_15868_additional_1.map.gz emd_15868_additional_1.map.gz emd_15868_additional_2.map.gz emd_15868_additional_2.map.gz emd_15868_additional_3.map.gz emd_15868_additional_3.map.gz emd_15868_half_map_1.map.gz emd_15868_half_map_1.map.gz emd_15868_half_map_2.map.gz emd_15868_half_map_2.map.gz | 213.4 MB 1.8 MB 1.8 MB 390.9 MB 390.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15868 http://ftp.pdbj.org/pub/emdb/structures/EMD-15868 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15868 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15868 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15868.map.gz / 形式: CCP4 / 大きさ: 421.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15868.map.gz / 形式: CCP4 / 大きさ: 421.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened mask refined map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.25 Å | ||||||||||||||||||||
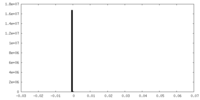
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_15868_msk_1.map emd_15868_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
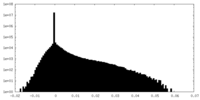
| 密度ヒストグラム |
-追加マップ: Unsharpened mask refined map
| ファイル | emd_15868_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened mask refined map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
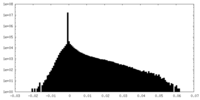
| 密度ヒストグラム |
-追加マップ: Rieske B-state map from focused classification
| ファイル | emd_15868_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Rieske B-state map from focused classification | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Rieske C-state map from focused classification
| ファイル | emd_15868_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Rieske C-state map from focused classification | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half-map A
| ファイル | emd_15868_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
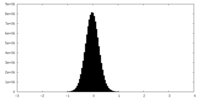
| 密度ヒストグラム |
-ハーフマップ: Half-map B
| ファイル | emd_15868_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Dimeric cytochrome bc1 complex (complex-III2)
+超分子 #1: Dimeric cytochrome bc1 complex (complex-III2)
+分子 #1: Peptidase M16 inactive domain protein
+分子 #2: M16 family peptidase, putative
+分子 #3: Apocytochrome b
+分子 #4: Cytochrome protein c1
+分子 #5: Rieske iron-sulfur protein, ubiquinol-cytochrome C reductase iron...
+分子 #6: Ubiquinol-cytochrome C reductase hinge protein
+分子 #7: UQCRTT1
+分子 #8: Transmembrane protein, putative
+分子 #9: Transmembrane protein, putative
+分子 #10: UQCRTT3/UP1
+分子 #11: Transmembrane protein, putative
+分子 #12: UQCRTT2
+分子 #13: 1,2-DIACYL-SN-GLYCERO-3-PHOSPHOCHOLINE
+分子 #14: PROTOPORPHYRIN IX CONTAINING FE
+分子 #15: CARDIOLIPIN
+分子 #16: Ubiquinone-8
+分子 #17: 1,2-dioleoyl-sn-glycero-3-phosphoethanolamine
+分子 #18: HEME C
+分子 #19: FE2/S2 (INORGANIC) CLUSTER
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 平均電子線量: 25.66 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 0.6 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X