+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10817 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the TFIIIC subcomplex tauA | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | TFIIIC / tauA / Transcription initiation / Pol III / TFIIIB / Transcription factor / TRANSCRIPTION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報5S class rRNA transcription by RNA polymerase III / transcription factor TFIIIC complex / RNA polymerase III type 1 promoter sequence-specific DNA binding / RNA polymerase III type 2 promoter sequence-specific DNA binding / RNA Polymerase III Transcription Initiation From Type 2 Promoter / transcription initiation at RNA polymerase III promoter / phosphatase activity / transcription by RNA polymerase III / DNA binding / nucleoplasm ...5S class rRNA transcription by RNA polymerase III / transcription factor TFIIIC complex / RNA polymerase III type 1 promoter sequence-specific DNA binding / RNA polymerase III type 2 promoter sequence-specific DNA binding / RNA Polymerase III Transcription Initiation From Type 2 Promoter / transcription initiation at RNA polymerase III promoter / phosphatase activity / transcription by RNA polymerase III / DNA binding / nucleoplasm / nucleus / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
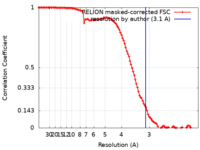
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Vorlaender MK / Muller CW | |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2020 ジャーナル: Nat Commun / 年: 2020タイトル: Structure of the TFIIIC subcomplex τA provides insights into RNA polymerase III pre-initiation complex formation. 著者: Matthias K Vorländer / Anna Jungblut / Kai Karius / Florence Baudin / Helga Grötsch / Jan Kosinski / Christoph W Müller /  要旨: Transcription factor (TF) IIIC is a conserved eukaryotic six-subunit protein complex with dual function. It serves as a general TF for most RNA polymerase (Pol) III genes by recruiting TFIIIB, but it ...Transcription factor (TF) IIIC is a conserved eukaryotic six-subunit protein complex with dual function. It serves as a general TF for most RNA polymerase (Pol) III genes by recruiting TFIIIB, but it is also involved in chromatin organization and regulation of Pol II genes through interaction with CTCF and condensin II. Here, we report the structure of the S. cerevisiae TFIIIC subcomplex τA, which contains the most conserved subunits of TFIIIC and is responsible for recruitment of TFIIIB and transcription start site (TSS) selection at Pol III genes. We show that τA binding to its promoter is auto-inhibited by a disordered acidic tail of subunit τ95. We further provide a negative-stain reconstruction of τA bound to the TFIIIB subunits Brf1 and TBP. This shows that a ruler element in τA achieves positioning of TFIIIB upstream of the TSS, and suggests remodeling of the complex during assembly of TFIIIB by TFIIIC. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10817.map.gz emd_10817.map.gz | 62.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10817-v30.xml emd-10817-v30.xml emd-10817.xml emd-10817.xml | 20.9 KB 20.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_10817_fsc.xml emd_10817_fsc.xml | 10.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_10817.png emd_10817.png | 140.1 KB | ||
| Filedesc metadata |  emd-10817.cif.gz emd-10817.cif.gz | 7.5 KB | ||
| その他 |  emd_10817_half_map_1.map.gz emd_10817_half_map_1.map.gz emd_10817_half_map_2.map.gz emd_10817_half_map_2.map.gz | 81.5 MB 81.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10817 http://ftp.pdbj.org/pub/emdb/structures/EMD-10817 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10817 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10817 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_10817_validation.pdf.gz emd_10817_validation.pdf.gz | 789.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_10817_full_validation.pdf.gz emd_10817_full_validation.pdf.gz | 789.5 KB | 表示 | |
| XML形式データ |  emd_10817_validation.xml.gz emd_10817_validation.xml.gz | 17.9 KB | 表示 | |
| CIF形式データ |  emd_10817_validation.cif.gz emd_10817_validation.cif.gz | 23.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10817 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10817 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10817 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10817 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10817.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10817.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.041 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
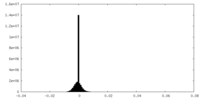
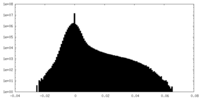
-ハーフマップ: #1
| ファイル | emd_10817_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
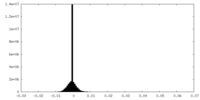
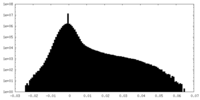
-ハーフマップ: #2
| ファイル | emd_10817_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : TFIIIC subcomplex tauA
| 全体 | 名称: TFIIIC subcomplex tauA |
|---|---|
| 要素 |
|
-超分子 #1: TFIIIC subcomplex tauA
| 超分子 | 名称: TFIIIC subcomplex tauA / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Generated by co-expression of subunits in insect cells |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 245 KDa |
-分子 #1: Transcription factor tau 131 kDa subunit
| 分子 | 名称: Transcription factor tau 131 kDa subunit / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 120.746969 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MAAGKLKKEQ QNQSAERESA DTGKVNDEDE EHLYGNIDDY KHLIQDEEYD DEDVPHDLQL SEDEYNSERD SSLLAEFSDY GEISEDDEE DFMNAIREAS NFKVKKKKKN DKGKSYGRQR KERVLDPEVA QLLSQANEAF VRNDLQVAER LFNEVIKKDA R NFAAYETL ...文字列: MAAGKLKKEQ QNQSAERESA DTGKVNDEDE EHLYGNIDDY KHLIQDEEYD DEDVPHDLQL SEDEYNSERD SSLLAEFSDY GEISEDDEE DFMNAIREAS NFKVKKKKKN DKGKSYGRQR KERVLDPEVA QLLSQANEAF VRNDLQVAER LFNEVIKKDA R NFAAYETL GDIYQLQGRL NDCCNSWFLA AHLNASDWEF WKIVAILSAD LDHVRQAIYC FSRVISLNPM EWESIYRRSM LY KKTGQLA RALDGFQRLY MYNPYDANIL RELAILYVDY DRIEDSIELY MKVFNANVER REAILAALEN ALDSSDEESA AEG EDADEK EPLEQDEDRQ MFPDINWKKI DAKYKCIPFD WSSLNILAEL FLKLAVSEVD GIKTIKKCAR WIQRRESQTF WDHV PDDSE FDNRRFKNST FDSLLAAEKE KSYNIPIDIR VRLGLLRLNT DNLVEALNHF QCLYDETFSD VADLYFEAAT ALTRA EKYK EAIDFFTPLL SLEEWRTTDV FKPLARCYKE IESYETAKEF YELAIKSEPD DLDIRVSLAE VYYRLNDPET FKHMLV DVV EMRKHQVDET LHRISNEKSS NDTSDISSKP LLEDSKFRTF RKKKRTPYDA ERERIERERR ITAKVVDKYE KMKKFEL NS GLNEAKQASI WINTVSELVD IFSSVKNFFM KSRSRKFVGI LRRTKKFNTE LDFQIERLSK LAEGDSVFEG PLMEERVT L TSATELRGLS YEQWFELFME LSLVIAKYQS VEDGLSVVET AQEVNVFFQD PERVKMMKFV KLAIVLQMDD EEELAENLR GLLNQFQFNR KVLQVFMYSL CRGPSSLNIL SSTIQQKFFL RQLKAFDSCR YNTEVNGQAS ITNKEVYNPN KKSSPYLYYI YAVLLYSSR GFLSALQYLT RLEEDIPDDP MVNLLMGLSH IHRAMQRLTA QRHFQIFHGL RYLYRYHKIR KSLYTDLEKQ E ADYNLGRA FHLIGLVSIA IEYYNRVLEN YDDGKLKKHA AYNSIIIYQQ SGNVELADHL MEKYLSIRSG G UniProtKB: Transcription factor tau 131 kDa subunit |
-分子 #2: Transcription factor tau 95 kDa subunit,Transcription factor tau ...
| 分子 | 名称: Transcription factor tau 95 kDa subunit,Transcription factor tau 95 kDa subunit タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 77.363664 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MHHHHHHENL YFQSMPVEEP LATLSSIPDS SADQAPPLIA DEFTLDLPRI PSLELPLNVS TKHSSIQKAI KMCGGIEKVK EAFKEHGPI ESQHGLQLYL NDDTDSDGSK SYFNEHPVIG KRVPFRDESV ILKVTMPKGT LSKNNNSVKD SIKSLKDSNK L RVTPVSIV ...文字列: MHHHHHHENL YFQSMPVEEP LATLSSIPDS SADQAPPLIA DEFTLDLPRI PSLELPLNVS TKHSSIQKAI KMCGGIEKVK EAFKEHGPI ESQHGLQLYL NDDTDSDGSK SYFNEHPVIG KRVPFRDESV ILKVTMPKGT LSKNNNSVKD SIKSLKDSNK L RVTPVSIV DNTIKFREMS DFQIKLDNVP SAREFKSSFG SLEWNNFKSF VNSVPDNDSQ PQENIGNLIL DRSVKIPSTD FQ LPPPPKL SMVGFPLLYK YKANPFAKKK KNGVTEVKGT YIKNYQLFVH DLSDKTVIPS QAHEQVLYDF EVAKKTKVYP GTK SDSKFY ESLEECLKIL RELFARRPIW VKRHLDGIVP KKIHHTMKIA LALISYRFTM GPWRNTYIKF GIDPRSSVEY AQYQ TEYFK IERKLLSSPI VKKNVPKPPP LVFESDTPGG IDSRFKFDGK RIPWYLMLQI DLLIGEPNIA EVFHNVEYLD KANEL TGWF KELDLVKIRR IVKYELGCMV QGNYEYNKYK LKYFKTMLFV KESMVPENKN SEEGMGVNTN KDADGDINMD AGSQMS SNA IEEDKGIAAG DDFDDNGAIT EEPDDAALEN EEMDTDQNLK VPASIDDDVD DVDADEEEQE SFDVKTASFQ DIINKIA KL DPKTAETMKS ELKGFVDEVD L(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK) (UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK)(UNK)(UNK) UniProtKB: Transcription factor tau 95 kDa subunit |
-分子 #3: Transcription factor tau 55 kDa subunit
| 分子 | 名称: Transcription factor tau 55 kDa subunit / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 49.198898 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MVVNTIYIAR HGYRSNWLPE GPYPDPLTGI DSDVPLAEHG VQQAKELAHY LLSLDNQPEA AFASPFYRCL ETVQPIAKLL EIPVYLERG IGEWYRPDRK PVIPVPAGYE ILSKFFPGVI SQEWDSTLTP NEKGETEQEM YMRFKKFWPL FIERVEKEYP N VECILLVT ...文字列: MVVNTIYIAR HGYRSNWLPE GPYPDPLTGI DSDVPLAEHG VQQAKELAHY LLSLDNQPEA AFASPFYRCL ETVQPIAKLL EIPVYLERG IGEWYRPDRK PVIPVPAGYE ILSKFFPGVI SQEWDSTLTP NEKGETEQEM YMRFKKFWPL FIERVEKEYP N VECILLVT HAASKIALGM SLLGYDNPRM SLNENGDKIR SGSCSLDKYE ILKKSYDTID ETDDQTSFTY IPFSDRKWVL TM NGNTEFL SSGEEMNWNF DCVAEAGSDA DIKKRQMTKK TSSPIPEADD QTEVETVYIS VDIPSGNYKE RTEIAKSAIL QYS GLETDA PLFRIGNRLY EGSWERLVGT ELAFPNAAHV HKKTAGLLSP TEENETTNAG QSKGSSTAND PNIQIQEEDV GLPD STNTS RDHTGDKEEV QSEKIYRIKE RIVLSNVRPM UniProtKB: Transcription factor tau 55 kDa subunit |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.3 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: 20 mM HEPES, 5 mM DTT, 75 mM NaCl |
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. / 詳細: Pelco Easygglow instrument |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV / 詳細: Blot force 2, Blot time 4. |
| 詳細 | 4 mM CHAPSO added prior to freezing |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - 画像ごとのフレーム数: 1-36 / 撮影したグリッド数: 1 / 実像数: 5824 / 平均露光時間: 48.73 sec. / 平均電子線量: 1.35 e/Å2 / 詳細: collected 8 frames per hole using beam shift |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): -2.0 µm / 最小 デフォーカス(公称値): -0.5 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-6yj6: |
 ムービー
ムービー コントローラー
コントローラー






















 Z
Z Y
Y X
X