+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10361 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human Influenza B polymerase recycling complex | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Influenza / polymerase / viral transcription / RNA / VIRAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報virion component => GO:0044423 / cap snatching / viral transcription / symbiont-mediated suppression of host mRNA transcription via inhibition of RNA polymerase II activity / host cell mitochondrion / 7-methylguanosine mRNA capping / virion component / endonuclease activity / host cell cytoplasm / 加水分解酵素; エステル加水分解酵素 ...virion component => GO:0044423 / cap snatching / viral transcription / symbiont-mediated suppression of host mRNA transcription via inhibition of RNA polymerase II activity / host cell mitochondrion / 7-methylguanosine mRNA capping / virion component / endonuclease activity / host cell cytoplasm / 加水分解酵素; エステル加水分解酵素 / RNA-directed RNA polymerase / viral RNA genome replication / RNA-dependent RNA polymerase activity / nucleotide binding / DNA-templated transcription / host cell nucleus / RNA binding / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.18 Å | |||||||||
 データ登録者 データ登録者 | Wandzik JM / Kouba T | |||||||||
| 資金援助 |  フランス, 1件 フランス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2020 ジャーナル: Cell / 年: 2020タイトル: A Structure-Based Model for the Complete Transcription Cycle of Influenza Polymerase. 著者: Joanna M Wandzik / Tomas Kouba / Manikandan Karuppasamy / Alexander Pflug / Petra Drncova / Jan Provaznik / Nayara Azevedo / Stephen Cusack /   要旨: Influenza polymerase uses unique mechanisms to synthesize capped and polyadenylated mRNAs from the genomic viral RNA (vRNA) template, which is packaged inside ribonucleoprotein particles (vRNPs). ...Influenza polymerase uses unique mechanisms to synthesize capped and polyadenylated mRNAs from the genomic viral RNA (vRNA) template, which is packaged inside ribonucleoprotein particles (vRNPs). Here, we visualize by cryoelectron microscopy the conformational dynamics of the polymerase during the complete transcription cycle from pre-initiation to termination, focusing on the template trajectory. After exiting the active site cavity, the template 3' extremity rebinds into a specific site on the polymerase surface. Here, it remains sequestered during all subsequent transcription steps, forcing the template to loop out as it further translocates. At termination, the strained connection between the bound template 5' end and the active site results in polyadenylation by stuttering at uridine 17. Upon product dissociation, further conformational changes release the trapped template, allowing recycling back into the pre-initiation state. Influenza polymerase thus performs transcription while tightly binding to and protecting both template ends, allowing efficient production of multiple mRNAs from a single vRNP. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10361.map.gz emd_10361.map.gz | 19.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10361-v30.xml emd-10361-v30.xml emd-10361.xml emd-10361.xml | 20.9 KB 20.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_10361_fsc.xml emd_10361_fsc.xml | 6.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_10361.png emd_10361.png | 89.6 KB | ||
| Filedesc metadata |  emd-10361.cif.gz emd-10361.cif.gz | 6.9 KB | ||
| その他 |  emd_10361_additional.map.gz emd_10361_additional.map.gz emd_10361_half_map_1.map.gz emd_10361_half_map_1.map.gz emd_10361_half_map_2.map.gz emd_10361_half_map_2.map.gz | 9.9 MB 15.9 MB 15.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10361 http://ftp.pdbj.org/pub/emdb/structures/EMD-10361 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10361 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10361 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_10361_validation.pdf.gz emd_10361_validation.pdf.gz | 909.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_10361_full_validation.pdf.gz emd_10361_full_validation.pdf.gz | 909 KB | 表示 | |
| XML形式データ |  emd_10361_validation.xml.gz emd_10361_validation.xml.gz | 11.8 KB | 表示 | |
| CIF形式データ |  emd_10361_validation.cif.gz emd_10361_validation.cif.gz | 16.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10361 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10361 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10361 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10361 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6t0wMC  6szuC  6szvC  6t0nC  6t0rC  6t0sC  6t0uC  6t0vC  6t2cC  6tu5C  6tw1C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10361.map.gz / 形式: CCP4 / 大きさ: 20.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10361.map.gz / 形式: CCP4 / 大きさ: 20.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.0506 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: LocScale map
| ファイル | emd_10361_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | LocScale map | ||||||||||||
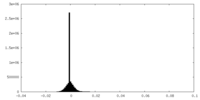
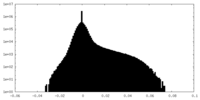
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_10361_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_10361_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human Influenza B polymerase recycling complex
| 全体 | 名称: Human Influenza B polymerase recycling complex |
|---|---|
| 要素 |
|
-超分子 #1: Human Influenza B polymerase recycling complex
| 超分子 | 名称: Human Influenza B polymerase recycling complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|
-超分子 #2: Polymerase
| 超分子 | 名称: Polymerase / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) |
-超分子 #3: Nucleic acid
| 超分子 | 名称: Nucleic acid / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #4 |
|---|---|
| 由来(天然) | 生物種:  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) |
-分子 #1: Polymerase acidic protein
| 分子 | 名称: Polymerase acidic protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO EC番号: 加水分解酵素; エステル加水分解酵素 |
|---|---|
| 由来(天然) | 生物種:  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) |
| 分子量 | 理論値: 85.822781 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: GSHHHHHHHH GSGSMDTFIT RNFQTTIIQK AKNTMAEFSE DPELQPAMLF NICVHLEVCY VISDMNFLDE EGKAYTALEG QGKEQNLRP QYEVIEGMPR TIAWMVQRSL AQEHGIETPK YLADLFDYKT KRFIEVGITK GLADDYFWKK KEKLGNSMEL M IFSYNQDY ...文字列: GSHHHHHHHH GSGSMDTFIT RNFQTTIIQK AKNTMAEFSE DPELQPAMLF NICVHLEVCY VISDMNFLDE EGKAYTALEG QGKEQNLRP QYEVIEGMPR TIAWMVQRSL AQEHGIETPK YLADLFDYKT KRFIEVGITK GLADDYFWKK KEKLGNSMEL M IFSYNQDY SLSNESSLDE EGKGRVLSRL TELQAELSLK NLWQVLIGEE DVEKGIDFKL GQTISRLRDI SVPAGFSNFE GM RSYIDNI DPKGAIERNL ARMSPLVSVT PKKLTWEDLR PIGPHIYNHE LPEVPYNAFL LMSDELGLAN MTEGKSKKPK TLA KECLEK YSTLRDQTDP ILIMKSEKAN ENFLWKLWRD CVNTISNEEM SNELQKTNYA KWATGDGLTY QKIMKEVAID DETM CQEEP KIPNKCRVAA WVQTEMNLLS TLTSKRALDL PEIGPDVAPV EHVGSERRKY FVNEINYCKA STVMMKYVLF HTSLL NESN ASMGKYKVIP ITNRVVNEKG ESFDMLYGLA VKGQSHLRGD TDVVTVVTFE FSSTDPRVDS GKWPKYTVFR IGSLFV SGR EKSVYLYCRV NGTNKIQMKW GMEARRCLLQ SMQQMEAIVE QESSIQGYDM TKACFKGDRV NSPKTFSIGT QEGKLVK GS FGKALRVIFT KCLMHYVFGN AQLEGFSAES RRLLLLIQAL KDRKGPWVFD LEGMYSGIEE CISNNPWVIQ SAYWFNEW L GFEKEGSKVL ESVDEIMDEG SGSGENLYFQ UniProtKB: Polymerase acidic protein |
-分子 #2: RNA-directed RNA polymerase catalytic subunit
| 分子 | 名称: RNA-directed RNA polymerase catalytic subunit / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO / EC番号: RNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) |
| 分子量 | 理論値: 86.207016 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: GSGSGSGSGM NINPYFLFID VPIQAAISTT FPYTGVPPYS HGTGTGYTID TVIRTHEYSN KGKQYISDVT GCTMVDPTNG PLPEDNEPS AYAQLDCVLE ALDRMDEEHP GLFQAASQNA METLMVTTVD KLTQGRQTFD WTVCRNQPAA TALNTTITSF R LNDLNGAD ...文字列: GSGSGSGSGM NINPYFLFID VPIQAAISTT FPYTGVPPYS HGTGTGYTID TVIRTHEYSN KGKQYISDVT GCTMVDPTNG PLPEDNEPS AYAQLDCVLE ALDRMDEEHP GLFQAASQNA METLMVTTVD KLTQGRQTFD WTVCRNQPAA TALNTTITSF R LNDLNGAD KGGLIPFCQD IIDSLDRPEM TFFSVKNIKK KLPAKNRKGF LIKRIPMKVK DKITKVEYIK RALSLNTMTK DA ERGKLKR RAIATAGIQI RGFVLVVENL AKNICENLEQ SGLPVGGNEK KAKLSNAVAK MLSNCPPGGI SMTVTGDNTK WNE CLNPRI FLAMTERITR DSPIWFRDFC SIAPVLFSNK IARLGKGFMI TSKTKRLKAQ IPCPDLFSIP LERYNEETRA KLKK LKPFF NEEGTASLSP GMMMGMFNML STVLGVAALG IKNIGNKEYL WDGLQSSDDF ALFVNAKDEE TCMEGINDFY RTCKL LGIN MSKKKSYCNE TGMFEFTSMF YRDGFVSNFA MELPSFGVAG VNESADMAIG MTIIKNNMIN NGMGPATAQT AIQLFI ADY RYTYKCHRGD SKVEGKRMKI IKELWENTKG RDGLLVADGG PNIYNLRNLH IPEIVLKYNL MDPEYKGRLL HPQNPFV GH LSIEGIKEAD ITPAHGPVKK MDYDAVSGTH SWRTKRNRSI LNTDQRNMIL EEQCYAKCCN LFEACFNSAS YRKPVGQH S MLEAMAHRLR MDARLDYESG RMSKDDFEKA MAHLGEIGYI GSGSGENLYF Q UniProtKB: RNA-directed RNA polymerase catalytic subunit |
-分子 #3: Polymerase PB2
| 分子 | 名称: Polymerase PB2 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) |
| 分子量 | 理論値: 90.971281 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: GSGSGSGSGM TLAKIELLKQ LLRDNEAKTV LKQTTVDQYN IIRKFNTSRI EKNPSLRMKW AMCSNFPLAL TKGDMANRIP LEYKGIQLK TNAEDIGTKG QMCSIAAVTW WNTYGPIGDT EGFERVYESF FLRKMRLDNA TWGRITFGPV ERVRKRVLLN P LTKEMPPD ...文字列: GSGSGSGSGM TLAKIELLKQ LLRDNEAKTV LKQTTVDQYN IIRKFNTSRI EKNPSLRMKW AMCSNFPLAL TKGDMANRIP LEYKGIQLK TNAEDIGTKG QMCSIAAVTW WNTYGPIGDT EGFERVYESF FLRKMRLDNA TWGRITFGPV ERVRKRVLLN P LTKEMPPD EASNVIMEIL FPKEAGIPRE STWIHRELIK EKREKLKGTM ITPIVLAYML ERELVARRRF LPVAGATSAE FI EMLHCLQ GENWRQIYHP GGNKLTESRS QSMIVACRKI IRRSIVASNP LELAVEIANK TVIDTEPLKS CLAAIDGGDV ACD IIRAAL GLKIRQRQRF GRLELKRISG RGFKNDEEIL IGNGTIQKIG IWDGEEEFHV RCGECRGILK KSKMKLEKLL INSA KKEDM RDLIILCMVF SQDTRMFQGV RGEINFLNRA GQLLSPMYQL QRYFLNRSND LFDQWGYEES PKASELHGIN ESMNA SDYT LKGVVVTRNV IDDFSSTETE KVSITKNLSL IKRTGEVIMG ANDVSELESQ AQLMITYDTP KMWEMGTTKE LVQNTY QWV LKNLVTLKAQ FLLGKEDMFQ WDAFEAFESI IPQKMAGQYS GFARAVLKQM RDQEVMKTDQ FIKLLPFCFS PPKLRSN GE PYQFLKLVLK GGGENFIEVR KGSPLFSYNP QTEVLTICGR MMSLKGKIED EERNRSMGNA VLAGFLVSGK YDPDLGDF K TIEELEKLKP GEKANILLYQ GKPVKVVKRK RYSALSNDIS QGIKRQRMTV ESMGWALSGW SHPQFEKGRS GGENLYFQ UniProtKB: Polymerase basic protein 2 |
-分子 #4: vRNA
| 分子 | 名称: vRNA / タイプ: rna / ID: 4 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Influenza B virus (B型インフルエンザウイルス) Influenza B virus (B型インフルエンザウイルス) |
| 分子量 | 理論値: 10.838431 KDa |
| 配列 | 文字列: AGUAGUAACA AGAGGUAUUA CCUCUGCUUC UGCU |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 平均電子線量: 35.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




















 Z
Z Y
Y X
X