+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0933 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of immature Zika virus | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | immature Zika virus / virus / flavivirus | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報flavivirin / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / negative regulation of innate immune response / viral capsid / double-stranded RNA binding / nucleoside-triphosphate phosphatase / 4 iron, 4 sulfur cluster binding / clathrin-dependent endocytosis of virus by host cell ...flavivirin / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / negative regulation of innate immune response / viral capsid / double-stranded RNA binding / nucleoside-triphosphate phosphatase / 4 iron, 4 sulfur cluster binding / clathrin-dependent endocytosis of virus by host cell / molecular adaptor activity / mRNA (guanine-N7)-methyltransferase / methyltransferase cap1 / methyltransferase cap1 activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / RNA helicase activity / protein dimerization activity / host cell perinuclear region of cytoplasm / host cell endoplasmic reticulum membrane / RNA helicase / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / serine-type endopeptidase activity / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / viral RNA genome replication / RNA-directed RNA polymerase activity / fusion of virus membrane with host endosome membrane / viral envelope / centrosome / lipid binding / virion attachment to host cell / GTP binding / host cell nucleus / virion membrane / structural molecule activity / ATP hydrolysis activity / proteolysis / extracellular region / ATP binding / metal ion binding 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Zika virus (isolate ZIKV/Human/French Polynesia/10087PF/2013) (ジカ熱ウイルス) / Zika virus (isolate ZIKV/Human/French Polynesia/10087PF/2013) (ジカ熱ウイルス) /  Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013 (ジカ熱ウイルス) Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013 (ジカ熱ウイルス) | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 9.0 Å | ||||||||||||
 データ登録者 データ登録者 | Tan TY / Fibriansah G | ||||||||||||
| 資金援助 |  シンガポール, 3件 シンガポール, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2020 ジャーナル: Nat Commun / 年: 2020タイトル: Capsid protein structure in Zika virus reveals the flavivirus assembly process. 著者: Ter Yong Tan / Guntur Fibriansah / Victor A Kostyuchenko / Thiam-Seng Ng / Xin-Xiang Lim / Shuijun Zhang / Xin-Ni Lim / Jiaqi Wang / Jian Shi / Marc C Morais / Davide Corti / Shee-Mei Lok /    要旨: Structures of flavivirus (dengue virus and Zika virus) particles are known to near-atomic resolution and show detailed structure and arrangement of their surface proteins (E and prM in immature virus ...Structures of flavivirus (dengue virus and Zika virus) particles are known to near-atomic resolution and show detailed structure and arrangement of their surface proteins (E and prM in immature virus or M in mature virus). By contrast, the arrangement of the capsid proteins:RNA complex, which forms the core of the particle, is poorly understood, likely due to inherent dynamics. Here, we stabilize immature Zika virus via an antibody that binds across the E and prM proteins, resulting in a subnanometer resolution structure of capsid proteins within the virus particle. Fitting of the capsid protein into densities shows the presence of a helix previously thought to be removed via proteolysis. This structure illuminates capsid protein quaternary organization, including its orientation relative to the lipid membrane and the genomic RNA, and its interactions with the transmembrane regions of the surface proteins. Results show the capsid protein plays a central role in the flavivirus assembly process. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0933.map.gz emd_0933.map.gz | 522.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0933-v30.xml emd-0933-v30.xml emd-0933.xml emd-0933.xml | 13.3 KB 13.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_0933.png emd_0933.png | 230.7 KB | ||
| Filedesc metadata |  emd-0933.cif.gz emd-0933.cif.gz | 5.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0933 http://ftp.pdbj.org/pub/emdb/structures/EMD-0933 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0933 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0933 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0933.map.gz / 形式: CCP4 / 大きさ: 669.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0933.map.gz / 形式: CCP4 / 大きさ: 669.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.34 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
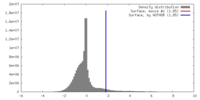
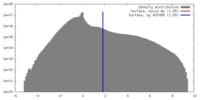
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013
| 全体 | 名称:  Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013 (ジカ熱ウイルス) Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013 (ジカ熱ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013
| 超分子 | 名称: Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013 タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: The virus was isolated from Zika patient. The immature Zika virus was grown in Aedes Albopictus clone C6/36 cell. NCBI-ID: 2043570 生物種: Zika virus ZIKV/H. sapiens/FrenchPolynesia/10087PF/2013 Sci species strain: H/PF/2013 / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No |
|---|
-分子 #1: Genome polyprotein
| 分子 | 名称: Genome polyprotein / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO / EC番号: flavivirin |
|---|---|
| 由来(天然) | 生物種:  Zika virus (isolate ZIKV/Human/French Polynesia/10087PF/2013) (ジカ熱ウイルス) Zika virus (isolate ZIKV/Human/French Polynesia/10087PF/2013) (ジカ熱ウイルス)株: isolate ZIKV/Human/French Polynesia/10087PF/2013 |
| 分子量 | 理論値: 54.444051 KDa |
| 配列 | 文字列: IRCIGVSNRD FVEGMSGGTW VDVVLEHGGC VTVMAQDKPT VDIELVTTTV SNMAEVRSYC YEASISDMAS DSRCPTQGEA YLDKQSDTQ YVCKRTLVDR GWGNGCGLFG KGSLVTCAKF ACSKKMTGKS IQPENLEYRI MLSVHGSQHS GMIVNDTGHE T DENRAKVE ...文字列: IRCIGVSNRD FVEGMSGGTW VDVVLEHGGC VTVMAQDKPT VDIELVTTTV SNMAEVRSYC YEASISDMAS DSRCPTQGEA YLDKQSDTQ YVCKRTLVDR GWGNGCGLFG KGSLVTCAKF ACSKKMTGKS IQPENLEYRI MLSVHGSQHS GMIVNDTGHE T DENRAKVE ITPNSPRAEA TLGGFGSLGL DCEPRTGLDF SDLYYLTMNN KHWLVHKEWF HDIPLPWHAG ADTGTPHWNN KE ALVEFKD AHAKRQTVVV LGSQEGAVHT ALAGALEAEM DGAKGRLSSG HLKCRLKMDK LRLKGVSYSL CTAAFTFTKI PAE TLHGTV TVEVQYAGTD GPCKVPAQMA VDMQTLTPVG RLITANPVIT ESTENSKMML ELDPPFGDSY IVIGVGEKKI THHW HRSGS TIGKAFEATV RGAKRMAVLG DTAWDFGSVG GALNSLGKGI HQIFGAAFKS LFGGMSWFSQ ILIGTLLMWL GLNTK NGSI SLMCLALGGV LIFLSTAVSA UniProtKB: Genome polyprotein |
-分子 #2: Genome polyprotein
| 分子 | 名称: Genome polyprotein / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO / EC番号: flavivirin |
|---|---|
| 由来(天然) | 生物種:  Zika virus (isolate ZIKV/Human/French Polynesia/10087PF/2013) (ジカ熱ウイルス) Zika virus (isolate ZIKV/Human/French Polynesia/10087PF/2013) (ジカ熱ウイルス)株: isolate ZIKV/Human/French Polynesia/10087PF/2013 |
| 分子量 | 理論値: 18.561266 KDa |
| 配列 | 文字列: RGSAYYMYLD RNDAGEAISF PTTLGMNKCY IQIMDLGHMC DATMSYECPM LDEGVEPDDV DCWCNTTSTW VVYGTCHHKK GEARRSRRA VTLPSHSTRK LQTRSQTWLE SREYTKHLIR VENWIFRNPG FALAAAAIAW LLGSSTSQKV IYLVMILLIA P AYS UniProtKB: Genome polyprotein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 / 詳細: 10 mM Tris-HCl, 120 mM NaCl, 1 mM EDTA, pH 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
| 詳細 | the virus sample was incubated at 37deg C for 30 min prior to sample blotting onto the grid. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 平均電子線量: 18.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 59000 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: EMDB MAP EMDB ID: |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: I (正20面体型対称) / 解像度のタイプ: BY AUTHOR / 解像度: 9.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION / 使用した粒子像数: 7922 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 2.1) |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 2.1) |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)