+Search query
-Structure paper
| Title | Structural insights into pre-pore intermediates of alpha-hemolysin in the lipidic environment. |
|---|---|
| Journal, issue, pages | Nat Commun, Vol. 16, Issue 1, Page 6348, Year 2025 |
| Publish date | Jul 10, 2025 |
 Authors Authors | Arnab Chatterjee / Anupam Roy / Thejas Satheesh / Partho Pratim Das / Bapan Mondal / Prithiv Kishore / Mahipal Ganji / Somnath Dutta /  |
| PubMed Abstract | The infectious microbe Staphylococcus aureus releases an array of cytotoxic pore-forming toxins (PFTs) that severely damage the cell membrane during bacterial infection. However, the interaction ...The infectious microbe Staphylococcus aureus releases an array of cytotoxic pore-forming toxins (PFTs) that severely damage the cell membrane during bacterial infection. However, the interaction interfaces between the host cell membrane and toxin were hardly explored. So far, there are no pore, and intermediate structures of these toxins available in the presence of bio-membrane, which could elucidate the pore-forming mechanism. Here, we investigate the structure of different conformational states of this alpha-hemolysin (α-HL/Hla), a β-PFT in lipidic environment using single-particle cryo-EM. Additionally, we explore lipid destabilization by the toxin, using single-molecule imaging, confocal imaging, and validation of lipid-protein interactions using mutational studies. We elucidate eight cryo-EM structures of wildtype α-HL with various liposomes, which are composed of either 10:0 PC or Egg-PC/Cholesterol or Egg-PC/Sphingomyelin or 10:0 PC/Sphingomyelin. Our structural and biophysical studies confirm that different chain lengths and various membrane compositions facilitate the formation of intermediate pre-pores and complete pore species. We also demonstrate that the percentage of pre-pore population increases due to sphingomyelin-induced membrane rigidity. Altogether, this study unveils the structure-function analysis of the pre-pore to pore transition of wildtype α-HL during its crosstalk with the lipid membrane. |
 External links External links |  Nat Commun / Nat Commun /  PubMed:40640160 / PubMed:40640160 /  PubMed Central PubMed Central |
| Methods | EM (single particle) |
| Resolution | 2.6 - 3.2 Å |
| Structure data |  EMDB-62302: Cryo-EM Density map of Staphylococcus aureus alpha-hemolysin pore structure derived from 12:0 Phosphatidylcholine (12:0 PC) liposome  EMDB-62303: Structure of Alpha-hemolysin heptameric pore state derived from Egg-PC/SM liposomes. EMDB-62304, PDB-9kg0: EMDB-62305, PDB-9kg1: EMDB-62307, PDB-9kg3:  EMDB-62308: Map of EggPC/SM derived prepore structure of alpha-hemolysin  EMDB-62309: 12:0 PC liposome derived pre-pore structure of alpha hemolysin |
| Chemicals | 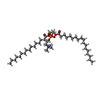 ChemComp-POV: 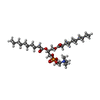 ChemComp-P1O: |
| Source |
|
 Keywords Keywords | LIPID BINDING PROTEIN / PFT / Liposomes |
 Movie
Movie Controller
Controller Structure viewers
Structure viewers About Yorodumi Papers
About Yorodumi Papers
















