+検索条件
-Structure paper
| タイトル | Craspase is a CRISPR RNA-guided, RNA-activated protease. |
|---|---|
| ジャーナル・号・ページ | Science, Vol. 377, Issue 6612, Page 1278-1285, Year 2022 |
| 掲載日 | 2022年9月16日 |
 著者 著者 | Chunyi Hu / Sam P B van Beljouw / Ki Hyun Nam / Gabriel Schuler / Fran Ding / Yanru Cui / Alicia Rodríguez-Molina / Anna C Haagsma / Menno Valk / Martin Pabst / Stan J J Brouns / Ailong Ke /    |
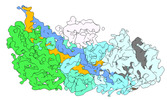
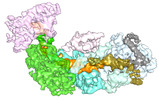
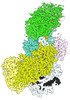
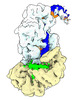
| PubMed 要旨 | The CRISPR-Cas type III-E RNA-targeting effector complex gRAMP/Cas7-11 is associated with a caspase-like protein (TPR-CHAT/Csx29) to form Craspase (CRISPR-guided caspase). Here, we use cryo-electron ...The CRISPR-Cas type III-E RNA-targeting effector complex gRAMP/Cas7-11 is associated with a caspase-like protein (TPR-CHAT/Csx29) to form Craspase (CRISPR-guided caspase). Here, we use cryo-electron microscopy snapshots of Craspase to explain its target RNA cleavage and protease activation mechanisms. Target-guide pairing extending into the 5' region of the guide RNA displaces a gating loop in gRAMP, which triggers an extensive conformational relay that allosterically aligns the protease catalytic dyad and opens an amino acid side-chain-binding pocket. We further define Csx30 as the endogenous protein substrate that is site-specifically proteolyzed by RNA-activated Craspase. This protease activity is switched off by target RNA cleavage by gRAMP and is not activated by RNA targets containing a matching protospacer flanking sequence. We thus conclude that Craspase is a target RNA-activated protease with self-regulatory capacity. |
 リンク リンク |  Science / Science /  PubMed:36007061 / PubMed:36007061 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) |
| 解像度 | 2.57 - 3.8 Å |
| 構造データ | EMDB-27252, PDB-8d8n: EMDB-27257, PDB-8d97: EMDB-27259, PDB-8d9e: EMDB-27260, PDB-8d9f: EMDB-27261, PDB-8d9g: EMDB-27262, PDB-8d9h: EMDB-27263, PDB-8d9i: |
| 化合物 |  ChemComp-ZN:  ChemComp-PO4: |
| 由来 |
|
 キーワード キーワード | RNA BINDING PROTEIN/RNA /  CRISPR (CRISPR) / GRAMP / RNA BINDING PROTEIN-RNA complex / CRISPR (CRISPR) / GRAMP / RNA BINDING PROTEIN-RNA complex /  RNA BINDING PROTEIN (RNA結合タンパク質) / Craspase RNA BINDING PROTEIN (RNA結合タンパク質) / Craspase |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について