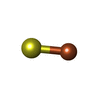+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30069 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of FMO-RC complex from green sulfur bacteria | |||||||||
 マップデータ マップデータ | structure of FMO-RC complex from a green sulfur bacterium | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報thylakoid / bacteriochlorophyll binding / iron-sulfur cluster binding / photosynthesis / membrane / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Chlorobaculum tepidum (strain ATCC 49652 / DSM 12025 / NBRC 103806 / TLS) (バクテリア) / Chlorobaculum tepidum (strain ATCC 49652 / DSM 12025 / NBRC 103806 / TLS) (バクテリア) /  Chlorobaculum tepidum TLS (バクテリア) Chlorobaculum tepidum TLS (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.7 Å | |||||||||
 データ登録者 データ登録者 | Chen JH / Zhang X | |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2020 ジャーナル: Science / 年: 2020タイトル: Architecture of the photosynthetic complex from a green sulfur bacterium. 著者: Jing-Hua Chen / Hangjun Wu / Caihuang Xu / Xiao-Chi Liu / Zihui Huang / Shenghai Chang / Wenda Wang / Guangye Han / Tingyun Kuang / Jian-Ren Shen / Xing Zhang /   要旨: The photosynthetic apparatus of green sulfur bacteria (GSB) contains a peripheral antenna chlorosome, light-harvesting Fenna-Matthews-Olson proteins (FMO), and a reaction center (GsbRC). We used cryo- ...The photosynthetic apparatus of green sulfur bacteria (GSB) contains a peripheral antenna chlorosome, light-harvesting Fenna-Matthews-Olson proteins (FMO), and a reaction center (GsbRC). We used cryo-electron microscopy to determine a 2.7-angstrom structure of the FMO-GsbRC supercomplex from The GsbRC binds considerably fewer (bacterio)chlorophylls [(B)Chls] than other known type I RCs do, and the organization of (B)Chls is similar to that in photosystem II. Two BChl layers in GsbRC are not connected by Chls, as seen in other RCs, but associate with two carotenoid derivatives. Relatively long distances of 22 to 33 angstroms were observed between BChls of FMO and GsbRC, consistent with the inefficient energy transfer between these entities. The structure contains common features of both type I and type II RCs and provides insight into the evolution of photosynthetic RCs. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30069.map.gz emd_30069.map.gz | 14.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30069-v30.xml emd-30069-v30.xml emd-30069.xml emd-30069.xml | 20.1 KB 20.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_30069.png emd_30069.png | 158.4 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30069 http://ftp.pdbj.org/pub/emdb/structures/EMD-30069 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30069 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30069 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_30069_validation.pdf.gz emd_30069_validation.pdf.gz | 576.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_30069_full_validation.pdf.gz emd_30069_full_validation.pdf.gz | 576.2 KB | 表示 | |
| XML形式データ |  emd_30069_validation.xml.gz emd_30069_validation.xml.gz | 5.3 KB | 表示 | |
| CIF形式データ |  emd_30069_validation.cif.gz emd_30069_validation.cif.gz | 6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30069 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30069 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30069 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30069 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30069.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30069.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | structure of FMO-RC complex from a green sulfur bacterium | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.307 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : FMO-RC of green sulfur bacteria
+超分子 #1: FMO-RC of green sulfur bacteria
+分子 #1: Bacteriochlorophyll a protein
+分子 #2: P840 reaction center 17 kDa protein
+分子 #3: Photosystem P840 reaction center iron-sulfur protein
+分子 #4: Photosystem P840 reaction center, large subunit
+分子 #5: BACTERIOCHLOROPHYLL A
+分子 #6: IRON/SULFUR CLUSTER
+分子 #7: Bacteriochlorophyll A isomer
+分子 #8: 2-[(1E,3E,5E,7E,9E,11E,13E,15E,17E,19E)-3,7,12,16,20,24-hexamethy...
+分子 #9: [(2R,3S,4S,5R,6R)-6-[(10E,12E,14E)-2,6,10,14,19,23-hexamethyl-25-...
+分子 #10: 1,2-DIPALMITOYL-PHOSPHATIDYL-GLYCEROLE
+分子 #11: 1,2-DISTEAROYL-MONOGALACTOSYL-DIGLYCERIDE
+分子 #12: CALCIUM ION
+分子 #13: Chlorophyll A ester
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: GRAPHENE OXIDE / 支持フィルム - トポロジー: HOLEY ARRAY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / デジタル化 - サイズ - 横: 3710 pixel / デジタル化 - サイズ - 縦: 3838 pixel / デジタル化 - 画像ごとのフレーム数: 1-40 / 撮影したグリッド数: 3 / 実像数: 9156 / 平均露光時間: 10.0 sec. / 平均電子線量: 47.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 最大 デフォーカス(補正後): 2.5 µm / 最小 デフォーカス(補正後): 1.5 µm / 倍率(補正後): 38244 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm / 倍率(公称値): 22500 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)