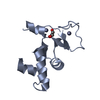
登録情報 データベース : PDB / ID : 4up5タイトル Crystal structure of the Pygo2 PHD finger in complex with the B9L HD1 domain and a chemical fragment PYGOPUS HOMOLOG 2, B-CELL CLL/LYMPHOMA 9-LIKE PROTEIN キーワード / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 HOMO SAPIENS (ヒト)手法 / / / 解像度 : 1.65 Å データ登録者 Miller, T.C.R. / Fiedler, M. / Rutherford, T.J. / Birchall, K. / Chugh, J. / Bienz, M. ジャーナル : Acs Chem.Biol. / 年 : 2014タイトル : Competitive Binding of a Benzimidazole to the Histone-Binding Pocket of the Pygo Phd Finger.著者 : Miller, T.C.R. / Rutherford, T.J. / Birchall, K. / Chugh, J. / Fiedler, M. / Bienz, M. 履歴 登録 2014年6月12日 登録サイト / 処理サイト 改定 1.0 2014年11月5日 Provider / タイプ 改定 1.1 2015年1月14日 Group 改定 1.2 2024年1月10日 Group Data collection / Database references ... Data collection / Database references / Derived calculations / Other / Refinement description カテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / pdbx_database_status / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn / struct_site Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_sf / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード TRANSCRIPTION (転写 (生物学)) / PYGO /
TRANSCRIPTION (転写 (生物学)) / PYGO /  WNT SIGNALLING (Wntシグナル経路) /
WNT SIGNALLING (Wntシグナル経路) /  HISTONE H3 (ヒストンH3) / FRAGMENT SCREENING
HISTONE H3 (ヒストンH3) / FRAGMENT SCREENING 機能・相同性情報
機能・相同性情報 mammary gland development / regulation of cell morphogenesis / myoblast differentiation / lens development in camera-type eye / roof of mouth development / skeletal muscle cell differentiation ...histone acetyltransferase regulator activity / spermatid nucleus differentiation / regulation of mammary gland epithelial cell proliferation / beta-catenin-TCF complex /
mammary gland development / regulation of cell morphogenesis / myoblast differentiation / lens development in camera-type eye / roof of mouth development / skeletal muscle cell differentiation ...histone acetyltransferase regulator activity / spermatid nucleus differentiation / regulation of mammary gland epithelial cell proliferation / beta-catenin-TCF complex /  mammary gland development / regulation of cell morphogenesis / myoblast differentiation / lens development in camera-type eye / roof of mouth development / skeletal muscle cell differentiation / somatic stem cell population maintenance / developmental growth / canonical Wnt signaling pathway / positive regulation of epithelial to mesenchymal transition /
mammary gland development / regulation of cell morphogenesis / myoblast differentiation / lens development in camera-type eye / roof of mouth development / skeletal muscle cell differentiation / somatic stem cell population maintenance / developmental growth / canonical Wnt signaling pathway / positive regulation of epithelial to mesenchymal transition /  kidney development / Deactivation of the beta-catenin transactivating complex / negative regulation of transforming growth factor beta receptor signaling pathway / Formation of the beta-catenin:TCF transactivating complex /
kidney development / Deactivation of the beta-catenin transactivating complex / negative regulation of transforming growth factor beta receptor signaling pathway / Formation of the beta-catenin:TCF transactivating complex /  brain development /
brain development /  核小体 /
核小体 /  beta-catenin binding /
beta-catenin binding /  histone binding / transcription by RNA polymerase II /
histone binding / transcription by RNA polymerase II /  transcription coactivator activity /
transcription coactivator activity /  chromatin binding / positive regulation of transcription by RNA polymerase II /
chromatin binding / positive regulation of transcription by RNA polymerase II /  核質 /
核質 /  metal ion binding /
metal ion binding /  細胞核
細胞核
 HOMO SAPIENS (ヒト)
HOMO SAPIENS (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.65 Å
分子置換 / 解像度: 1.65 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Acs Chem.Biol. / 年: 2014
ジャーナル: Acs Chem.Biol. / 年: 2014 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4up5.cif.gz
4up5.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4up5.ent.gz
pdb4up5.ent.gz PDB形式
PDB形式 4up5.json.gz
4up5.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/up/4up5
https://data.pdbj.org/pub/pdb/validation_reports/up/4up5 ftp://data.pdbj.org/pub/pdb/validation_reports/up/4up5
ftp://data.pdbj.org/pub/pdb/validation_reports/up/4up5 リンク
リンク 集合体
集合体
 要素
要素
 HOMO SAPIENS (ヒト) / プラスミド: PETM11 / 発現宿主:
HOMO SAPIENS (ヒト) / プラスミド: PETM11 / 発現宿主: 
 ESCHERICHIA COLI (大腸菌) / 株 (発現宿主): BL21(DE3) / Variant (発現宿主): CODONPLUS RIL / 参照: UniProt: Q9BRQ0, UniProt: Q86UU0
ESCHERICHIA COLI (大腸菌) / 株 (発現宿主): BL21(DE3) / Variant (発現宿主): CODONPLUS RIL / 参照: UniProt: Q9BRQ0, UniProt: Q86UU0 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  Diamond
Diamond  / ビームライン: I04 / 波長: 1.0332
/ ビームライン: I04 / 波長: 1.0332  : 1.0332 Å / 相対比: 1
: 1.0332 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj



