[English] 日本語
 Yorodumi
Yorodumi- PDB-4ur0: Crystal structure of the PCE reductive dehalogenase from S. multi... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4ur0 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of the PCE reductive dehalogenase from S. multivorans in complex with trichloroethene | ||||||
 Components Components | TETRACHLOROETHENE REDUCTIVE DEHALOGENASE CATALYTIC SUBUNIT PCEA | ||||||
 Keywords Keywords |  OXIDOREDUCTASE OXIDOREDUCTASE | ||||||
| Function / homology |  Function and homology information Function and homology information4 iron, 4 sulfur cluster binding / identical protein binding /  metal ion binding metal ion bindingSimilarity search - Function | ||||||
| Biological species |  SULFUROSPIRILLUM MULTIVORANS (bacteria) SULFUROSPIRILLUM MULTIVORANS (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 1.798 Å SAD / Resolution: 1.798 Å | ||||||
 Authors Authors | Bommer, M. / Kunze, C. / Fesseler, J. / Schubert, T. / Diekert, G. / Dobbek, H. | ||||||
 Citation Citation |  Journal: Science / Year: 2014 Journal: Science / Year: 2014Title: Structural Basis for Organohalide Respiration. Authors: Bommer, M. / Kunze, C. / Fesseler, J. / Schubert, T. / Diekert, G. / Dobbek, H. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4ur0.cif.gz 4ur0.cif.gz | 382.9 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4ur0.ent.gz pdb4ur0.ent.gz | 326.5 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4ur0.json.gz 4ur0.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/ur/4ur0 https://data.pdbj.org/pub/pdb/validation_reports/ur/4ur0 ftp://data.pdbj.org/pub/pdb/validation_reports/ur/4ur0 ftp://data.pdbj.org/pub/pdb/validation_reports/ur/4ur0 | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
| ||||||||
| Noncrystallographic symmetry (NCS) | NCS oper: (Code: given Matrix: (-0.5114, 0.0011, 0.8594), Vector  : : |
- Components
Components
-Protein , 1 types, 2 molecules AB
| #1: Protein | Mass: 52164.387 Da / Num. of mol.: 2 / Fragment: RESIDUES 38-501 / Source method: isolated from a natural source / Details: GERMAN COLLECTION OF MICROORGANISMS (DSM) 12446 / Source: (natural)  SULFUROSPIRILLUM MULTIVORANS (bacteria) / References: UniProt: W6EQP0, EC: 1.97.1.8 SULFUROSPIRILLUM MULTIVORANS (bacteria) / References: UniProt: W6EQP0, EC: 1.97.1.8 |
|---|
-Non-polymers , 6 types, 824 molecules 
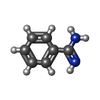

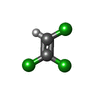






| #2: Chemical | ChemComp-SF4 /  Iron–sulfur cluster Iron–sulfur cluster#3: Chemical | #4: Chemical | ChemComp-BEN / |  Benzamidine Benzamidine#5: Chemical | ChemComp-GOL /  Glycerol Glycerol#6: Chemical | ChemComp-TCV / |  Trichloroethylene Trichloroethylene#7: Water | ChemComp-HOH / |  Water Water |
|---|
-Details
| Sequence details | THE DATA BASE ENTRY CONTAINS A SIGNAL PEPTIDE (AA 1-37) NOT PRESENT IN THE MATURE PEPTIDE |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.55 Å3/Da / Density % sol: 51.7 % / Description: NONE |
|---|---|
Crystal grow | Method: vapor diffusion / pH: 8 Details: VAPOUR DIFFUSION UNDER ANAEROBIC CONDITIONS (95% N2 / 5% H2), 50 MM TRIS-HCL PH 8.0, 15% PEG 3350, 0.2 M NAMALONATE, 2% BENZAMIDINE |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  BESSY BESSY  / Beamline: 14.1 / Wavelength: 0.9184 / Beamline: 14.1 / Wavelength: 0.9184 |
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Nov 23, 2013 / Details: MIRRORS |
| Radiation | Monochromator: SI-111 CRYSTAL / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength : 0.9184 Å / Relative weight: 1 : 0.9184 Å / Relative weight: 1 |
| Reflection | Resolution: 1.8→45.5 Å / Num. obs: 91944 / % possible obs: 99.9 % / Observed criterion σ(I): 2 / Redundancy: 13.8 % / Biso Wilson estimate: 20.14 Å2 / Rmerge(I) obs: 0.15 / Net I/σ(I): 16 |
| Reflection shell | Resolution: 1.8→1.86 Å / Redundancy: 12.3 % / Rmerge(I) obs: 1.25 / Mean I/σ(I) obs: 1.93 / % possible all: 99.3 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  SAD SADStarting model: NONE Resolution: 1.798→45.548 Å / SU ML: 0.17 / σ(F): 1.36 / Phase error: 16.09 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 26.4 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.798→45.548 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller
















 PDBj
PDBj












