+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Rat Cardiac Sodium Channel with Ranolazine Bound | |||||||||
 マップデータ マップデータ | Sharpened map used for model building and interpretation | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報voltage-gated sodium channel activity involved in AV node cell action potential / voltage-gated sodium channel activity involved in bundle of His cell action potential / voltage-gated sodium channel activity involved in SA node cell action potential / bundle of His cell action potential / AV node cell action potential /  sodium channel complex / SA node cell action potential / AV node cell to bundle of His cell communication / membrane depolarization during SA node cell action potential / cardiac ventricle development ...voltage-gated sodium channel activity involved in AV node cell action potential / voltage-gated sodium channel activity involved in bundle of His cell action potential / voltage-gated sodium channel activity involved in SA node cell action potential / bundle of His cell action potential / AV node cell action potential / sodium channel complex / SA node cell action potential / AV node cell to bundle of His cell communication / membrane depolarization during SA node cell action potential / cardiac ventricle development ...voltage-gated sodium channel activity involved in AV node cell action potential / voltage-gated sodium channel activity involved in bundle of His cell action potential / voltage-gated sodium channel activity involved in SA node cell action potential / bundle of His cell action potential / AV node cell action potential /  sodium channel complex / SA node cell action potential / AV node cell to bundle of His cell communication / membrane depolarization during SA node cell action potential / cardiac ventricle development / response to denervation involved in regulation of muscle adaptation / regulation of ventricular cardiac muscle cell membrane depolarization / regulation of atrial cardiac muscle cell membrane repolarization / membrane depolarization during atrial cardiac muscle cell action potential / membrane depolarization during action potential / voltage-gated sodium channel activity involved in Purkinje myocyte action potential / regulation of sodium ion transmembrane transport / brainstem development / membrane depolarization during AV node cell action potential / voltage-gated sodium channel activity involved in cardiac muscle cell action potential / membrane depolarization during bundle of His cell action potential / positive regulation of action potential / atrial cardiac muscle cell action potential / membrane depolarization during Purkinje myocyte cell action potential / telencephalon development / regulation of atrial cardiac muscle cell membrane depolarization / sodium channel complex / SA node cell action potential / AV node cell to bundle of His cell communication / membrane depolarization during SA node cell action potential / cardiac ventricle development / response to denervation involved in regulation of muscle adaptation / regulation of ventricular cardiac muscle cell membrane depolarization / regulation of atrial cardiac muscle cell membrane repolarization / membrane depolarization during atrial cardiac muscle cell action potential / membrane depolarization during action potential / voltage-gated sodium channel activity involved in Purkinje myocyte action potential / regulation of sodium ion transmembrane transport / brainstem development / membrane depolarization during AV node cell action potential / voltage-gated sodium channel activity involved in cardiac muscle cell action potential / membrane depolarization during bundle of His cell action potential / positive regulation of action potential / atrial cardiac muscle cell action potential / membrane depolarization during Purkinje myocyte cell action potential / telencephalon development / regulation of atrial cardiac muscle cell membrane depolarization /  voltage-gated sodium channel complex / membrane depolarization during cardiac muscle cell action potential / positive regulation of sodium ion transport / sodium ion import across plasma membrane / cardiac muscle cell action potential involved in contraction / ventricular cardiac muscle cell action potential / regulation of cardiac muscle cell contraction / voltage-gated sodium channel complex / membrane depolarization during cardiac muscle cell action potential / positive regulation of sodium ion transport / sodium ion import across plasma membrane / cardiac muscle cell action potential involved in contraction / ventricular cardiac muscle cell action potential / regulation of cardiac muscle cell contraction /  voltage-gated sodium channel activity / regulation of ventricular cardiac muscle cell membrane repolarization / voltage-gated sodium channel activity / regulation of ventricular cardiac muscle cell membrane repolarization /  ankyrin binding / positive regulation of heart rate / sodium ion transport / ankyrin binding / positive regulation of heart rate / sodium ion transport /  fibroblast growth factor binding / fibroblast growth factor binding /  nitric-oxide synthase binding / odontogenesis of dentin-containing tooth / regulation of heart rate by cardiac conduction / nitric-oxide synthase binding / odontogenesis of dentin-containing tooth / regulation of heart rate by cardiac conduction /  脱分極 / neuronal action potential / sodium ion transmembrane transport / 脱分極 / neuronal action potential / sodium ion transmembrane transport /  介在板 / lateral plasma membrane / cardiac muscle contraction / 介在板 / lateral plasma membrane / cardiac muscle contraction /  横行小管 / cellular response to calcium ion / 横行小管 / cellular response to calcium ion /  regulation of heart rate / cerebellum development / regulation of heart rate / cerebellum development /  生物発光 / generation of precursor metabolites and energy / positive regulation of epithelial cell proliferation / 生物発光 / generation of precursor metabolites and energy / positive regulation of epithelial cell proliferation /  カベオラ / カベオラ /  筋鞘 / response to organic cyclic compound / Z disc / 筋鞘 / response to organic cyclic compound / Z disc /  scaffold protein binding / transmembrane transporter binding / scaffold protein binding / transmembrane transporter binding /  calmodulin binding / calmodulin binding /  神経繊維 / protein domain specific binding / 神経繊維 / protein domain specific binding /  ubiquitin protein ligase binding / ubiquitin protein ligase binding /  protein kinase binding / perinuclear region of cytoplasm / protein kinase binding / perinuclear region of cytoplasm /  enzyme binding / enzyme binding /  細胞膜 / 細胞膜 /  小胞体 / 小胞体 /  生体膜 / 生体膜 /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Rattus norvegicus (ドブネズミ) / Rattus norvegicus (ドブネズミ) /   Aequorea victoria (オワンクラゲ) Aequorea victoria (オワンクラゲ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.2 Å クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Lenaeus MJ / Tonggu L | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Structural Basis for Inhibition of the Cardiac Sodium Channel by the Atypical Antiarrhythmic Drug Ranolazine 著者: Lenaeus MJ / Tonggu L | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28887.map.gz emd_28887.map.gz | 59.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28887-v30.xml emd-28887-v30.xml emd-28887.xml emd-28887.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_28887.png emd_28887.png | 56.1 KB | ||
| その他 |  emd_28887_half_map_1.map.gz emd_28887_half_map_1.map.gz emd_28887_half_map_2.map.gz emd_28887_half_map_2.map.gz | 59.4 MB 59.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28887 http://ftp.pdbj.org/pub/emdb/structures/EMD-28887 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28887 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28887 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8f6pMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28887.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28887.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map used for model building and interpretation | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.056 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: HalfMap B
| ファイル | emd_28887_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HalfMap B | ||||||||||||
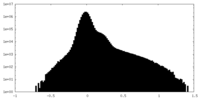
| 投影像・断面図 |
| ||||||||||||
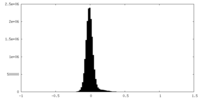
| 密度ヒストグラム |
-ハーフマップ: HalfMap A
| ファイル | emd_28887_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HalfMap A | ||||||||||||
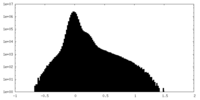
| 投影像・断面図 |
| ||||||||||||
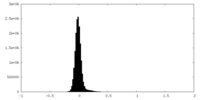
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Complex of rat cardiac sodium channel with the antiarrhythmic dru...
| 全体 | 名称: Complex of rat cardiac sodium channel with the antiarrhythmic drug ranolazine |
|---|---|
| 要素 |
|
-超分子 #1: Complex of rat cardiac sodium channel with the antiarrhythmic dru...
| 超分子 | 名称: Complex of rat cardiac sodium channel with the antiarrhythmic drug ranolazine タイプ: complex / ID: 1 / キメラ: Yes / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Rattus norvegicus (ドブネズミ) Rattus norvegicus (ドブネズミ) |
| 分子量 | 理論値: 250 KDa |
-分子 #1: Sodium channel protein type 5 subunit alpha,Green fluorescent protein
| 分子 | 名称: Sodium channel protein type 5 subunit alpha,Green fluorescent protein タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Aequorea victoria (オワンクラゲ) Aequorea victoria (オワンクラゲ) |
| 分子量 | 理論値: 209.096922 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MANLLLPRGT SSFRRFTRES LAAIEKRMAE KQARGGSATS QESREGLQEE EAPRPQLDLQ ASKKLPDLYG NPPRELIGEP LEDLDPFYS TQKTFIVLNK GKTIFRFSAT NALYVLSPFH PVRRAAVKIL VHSLFSMLIM CTILTNCVFM AQHDPPPWTK Y VEYTFTAI ...文字列: MANLLLPRGT SSFRRFTRES LAAIEKRMAE KQARGGSATS QESREGLQEE EAPRPQLDLQ ASKKLPDLYG NPPRELIGEP LEDLDPFYS TQKTFIVLNK GKTIFRFSAT NALYVLSPFH PVRRAAVKIL VHSLFSMLIM CTILTNCVFM AQHDPPPWTK Y VEYTFTAI YTFESLVKIL ARGFCLHAFT FLRDPWNWLD FSVIVMAYTT EFVDLGNVSA LRTFRVLRAL KTISVISGLK TI VGALIQS VKKLADVMVL TVFCLSVFAL IGLQLFMGNL RHKCVRNFTE LNGTNGSVEA DGLVWNSLDV YLNDPANYLL KNG TTDVLL CGNSSDAGTC PEGYRCLKAG QNPDHGYTSF DSFAWAFLAL FRLMTQDCWE RLYQQTLRSA GKIYMIFFML VIFL GSFYL VNLILAVVAM AYEEQNQATI AETEEKEKRF QEAMEMLKKE HEALTIRGVD TVSRSSARQR ALSAVSVLTS ALEEL EESH RKCPPCWNRF AQHYLIWECC PLWMSIKQKV KFVVMDPFAD LTITMCIVLN TLFMALEHYN MTAEFEEMLQ VGNLVF TGI FTAEMTFKII ALDPYYYFQQ GWNIFDSIIV ILSLMELGLS RMGNLSVLRS FRLLRVFKLA KSWPTLNTLI KIIGNSV GA LGNLTLVLAI IVFIFAVVGM QLFGKNYSEL RHRISDSGLL PRWHMMDFFH AFLIIFRILC GEWIETMWDC MEVSGQSL C LLVFLLVMVI GNLVVLNLFL ALLLSSFSAD NLTAPDEDGE MNNLQLALAR IQRGLRFVKR TTWDFCCGIL RRRPKKPAA LATHSQLPSC ITAPRSPPPP EVEKVPPARK ETRFEEDKRP GQGTPGDSEP VCVPIAVAES DTEDQEEDEE NGKVWWRLRK TCYRIVEHS WFETFIIFMI LLSSGALAFE DIYLEERKTI KVLLEYADKM FTYVFVLEML LKWVAYGFKK YFTNAWCWLD F LIVDVSLV SLVANTLGFA EMGPIKSLRT LRALRPLRAL SRFEGMRVVV NALVGAIPSI MNVLLVCLIF WLIFSIMGVN LF AGKFGRC INQTEGDLPL NYTIVNNKSE CESFNVTGEL YWTKVKVNFD NVGAGYLALL QVATFKGWMD IMYAAVDSRG YEE QPQWED NLYMYIYFVV FIIFGSFFTL NLFIGVIIDN FNQQKKKLGG QDIFMTEEQK KYYNMMKKLG SKKPQKPIPR PLNK YQGFI FDIVTKQAFD VTIMFLICLN MVTMMVETDD QSPEKVNILA KINLLFVAIF TGECIVKMAA LRHYYFTNSW NIFDF VVVI LSIVGTVLSD IIQKYFFSPT LFRVIRLARI GRILRLIRGA KGIRTLLFAL MMSLPALFNI GLLLFLVMFI YSIFGM ANF AYVKWEAGID DMFNFQTFAN SMLCLFQITT SAGWDGLLSP ILNTGPPYCD PNLPNSNGSR GNCGSPAVGI LFFTTYI II SFLIVVNMYI AIILENFSVA TEESTEPLSE DDFDMFYEIW EKFDPEATQF IEYLALSDFA DALSEPLRIA KPNQISLI N MDLPMVSGDR IHCMDILFAF TKRVLGESGE MDALKIQMEE KFMAANPSKI SYEPITTTLE VLFQGPGSMV SKGEELFTG VVPILVELDG DVNGHKFSVS GEGEGDATYG KLTLKFICTT GKLPVPWPTL VTTLTYGVQC FSRYPDHMKQ HDFFKSAMPE GYVQERTIF FKDDGNYKTR AEVKFEGDTL VNRIELKGID FKEDGNILGH KLEYNYNSHN VYIMADKQKN GIKVNFKIRH N IEDGSVQL ADHYQQNTPI GDGPVLLPDN HYLSTQSALS KDPNEKRDHM VLLEFVTAAG ITLGMDELYK GSDYKDDDDK |
-分子 #3: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 3 / コピー数: 7 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #4: beta-D-mannopyranose
| 分子 | 名称: beta-D-mannopyranose / タイプ: ligand / ID: 4 / コピー数: 3 / 式: BMA |
|---|---|
| 分子量 | 理論値: 180.156 Da |
| Chemical component information | 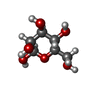 ChemComp-BMA: |
-分子 #5: (R)-ranolazine
| 分子 | 名称: (R)-ranolazine / タイプ: ligand / ID: 5 / コピー数: 1 / 式: XHO |
|---|---|
| 分子量 | 理論値: 427.537 Da |
| Chemical component information | 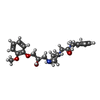 ChemComp-XHO: |
-分子 #6: [(2~{R})-1-[2-azanylethoxy(oxidanyl)phosphoryl]oxy-3-hexadecanoyl...
| 分子 | 名称: [(2~{R})-1-[2-azanylethoxy(oxidanyl)phosphoryl]oxy-3-hexadecanoyloxy-propan-2-yl] (~{Z})-octadec-9-enoate タイプ: ligand / ID: 6 / コピー数: 6 / 式: 6OU |
|---|---|
| 分子量 | 理論値: 717.996 Da |
| Chemical component information | 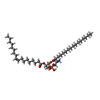 ChemComp-6OU: |
-分子 #7: CHOLESTEROL HEMISUCCINATE
| 分子 | 名称: CHOLESTEROL HEMISUCCINATE / タイプ: ligand / ID: 7 / コピー数: 13 / 式: Y01 |
|---|---|
| 分子量 | 理論値: 486.726 Da |
| Chemical component information |  ChemComp-Y01: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4 mg/mL |
|---|---|
| 緩衝液 | pH: 6 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / 支持フィルム - 材質: GRAPHENE / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
| 詳細 | Monodisperse protein from SEC |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 1.2 µm |
| 特殊光学系 | エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 60.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT |
| 最終 3次元分類 | ソフトウェア - 名称: cryoSPARC (ver. 3.3) |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 165532 |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
|---|---|
| 得られたモデル |  PDB-8f6p: |
 ムービー
ムービー コントローラー
コントローラー







 Z
Z Y
Y X
X