+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 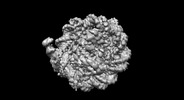 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CX3CR1 nucleosome and wild type PU.1 complex | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  nucleosome (ヌクレオソーム) / nucleosome (ヌクレオソーム) /  transcription factor (転写因子) / transcription factor (転写因子) /  transcription (転写 (生物学)) / chromatin binding protein-DNA complex / DNA BINDING PROTEIN-DNA complex / TRANSCRIPTION-DNA complex transcription (転写 (生物学)) / chromatin binding protein-DNA complex / DNA BINDING PROTEIN-DNA complex / TRANSCRIPTION-DNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of myeloid dendritic cell chemotaxis / anatomical structure regression / follicular B cell differentiation / positive regulation of antifungal innate immune response / regulation of myeloid progenitor cell differentiation / pro-T cell differentiation / negative regulation of neutrophil degranulation / germinal center B cell differentiation / positive regulation of microglial cell mediated cytotoxicity / myeloid leukocyte differentiation ...positive regulation of myeloid dendritic cell chemotaxis / anatomical structure regression / follicular B cell differentiation / positive regulation of antifungal innate immune response / regulation of myeloid progenitor cell differentiation / pro-T cell differentiation / negative regulation of neutrophil degranulation / germinal center B cell differentiation / positive regulation of microglial cell mediated cytotoxicity / myeloid leukocyte differentiation / granulocyte differentiation / TRAIL-activated apoptotic signaling pathway / apoptotic process involved in blood vessel morphogenesis / lymphocyte differentiation / endothelial to hematopoietic transition / negative regulation of adipose tissue development / pericyte cell differentiation / negative regulation of MHC class II biosynthetic process / immature B cell differentiation / lymphoid progenitor cell differentiation / myeloid dendritic cell differentiation / defense response to tumor cell / vasculature development / regulation of DNA-binding transcription factor activity / negative regulation of non-canonical NF-kappaB signal transduction / oncogene-induced cell senescence / negative regulation of protein localization to chromatin / positive regulation of p38MAPK cascade / positive regulation of B cell differentiation / DNA-binding transcription repressor activity / STAT family protein binding / DNA-binding transcription activator activity / interleukin-6-mediated signaling pathway /  NFAT protein binding / somatic stem cell population maintenance / macrophage differentiation / negative regulation of megakaryocyte differentiation / protein localization to CENP-A containing chromatin / cis-regulatory region sequence-specific DNA binding / Chromatin modifying enzymes / Replacement of protamines by nucleosomes in the male pronucleus / CENP-A containing nucleosome / epigenetic regulation of gene expression / Packaging Of Telomere Ends / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine / Deposition of new CENPA-containing nucleosomes at the centromere / lipopolysaccharide-mediated signaling pathway / transcription initiation-coupled chromatin remodeling / Recognition and association of DNA glycosylase with site containing an affected pyrimidine / Cleavage of the damaged pyrimidine / Inhibition of DNA recombination at telomere / Meiotic synapsis / telomere organization / RNA Polymerase I Promoter Opening / Interleukin-7 signaling / Assembly of the ORC complex at the origin of replication / SUMOylation of chromatin organization proteins / NFAT protein binding / somatic stem cell population maintenance / macrophage differentiation / negative regulation of megakaryocyte differentiation / protein localization to CENP-A containing chromatin / cis-regulatory region sequence-specific DNA binding / Chromatin modifying enzymes / Replacement of protamines by nucleosomes in the male pronucleus / CENP-A containing nucleosome / epigenetic regulation of gene expression / Packaging Of Telomere Ends / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine / Deposition of new CENPA-containing nucleosomes at the centromere / lipopolysaccharide-mediated signaling pathway / transcription initiation-coupled chromatin remodeling / Recognition and association of DNA glycosylase with site containing an affected pyrimidine / Cleavage of the damaged pyrimidine / Inhibition of DNA recombination at telomere / Meiotic synapsis / telomere organization / RNA Polymerase I Promoter Opening / Interleukin-7 signaling / Assembly of the ORC complex at the origin of replication / SUMOylation of chromatin organization proteins /  DNAメチル化 / transforming growth factor beta receptor signaling pathway / DNAメチル化 / transforming growth factor beta receptor signaling pathway /  赤血球形成 / protein sequestering activity / Condensation of Prophase Chromosomes / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / Chromatin modifications during the maternal to zygotic transition (MZT) / SIRT1 negatively regulates rRNA expression / HCMV Late Events / 赤血球形成 / protein sequestering activity / Condensation of Prophase Chromosomes / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / Chromatin modifications during the maternal to zygotic transition (MZT) / SIRT1 negatively regulates rRNA expression / HCMV Late Events /  innate immune response in mucosa / PRC2 methylates histones and DNA / Defective pyroptosis / HDACs deacetylate histones / RNA Polymerase I Promoter Escape / Nonhomologous End-Joining (NHEJ) / Transcriptional regulation by small RNAs / Formation of the beta-catenin:TCF transactivating complex / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / NoRC negatively regulates rRNA expression / B-WICH complex positively regulates rRNA expression / G2/M DNA damage checkpoint / HDMs demethylate histones / innate immune response in mucosa / PRC2 methylates histones and DNA / Defective pyroptosis / HDACs deacetylate histones / RNA Polymerase I Promoter Escape / Nonhomologous End-Joining (NHEJ) / Transcriptional regulation by small RNAs / Formation of the beta-catenin:TCF transactivating complex / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / NoRC negatively regulates rRNA expression / B-WICH complex positively regulates rRNA expression / G2/M DNA damage checkpoint / HDMs demethylate histones /  regulation of erythrocyte differentiation / DNA Damage/Telomere Stress Induced Senescence / Metalloprotease DUBs / PKMTs methylate histone lysines / RMTs methylate histone arginines / regulation of erythrocyte differentiation / DNA Damage/Telomere Stress Induced Senescence / Metalloprotease DUBs / PKMTs methylate histone lysines / RMTs methylate histone arginines /  遺伝的組換え / Pre-NOTCH Transcription and Translation / DNA-binding transcription repressor activity, RNA polymerase II-specific / 遺伝的組換え / Pre-NOTCH Transcription and Translation / DNA-binding transcription repressor activity, RNA polymerase II-specific /  nucleosome assembly / positive regulation of miRNA transcription / Activation of anterior HOX genes in hindbrain development during early embryogenesis / HCMV Early Events / Transcriptional regulation of granulopoiesis / nucleosome assembly / positive regulation of miRNA transcription / Activation of anterior HOX genes in hindbrain development during early embryogenesis / HCMV Early Events / Transcriptional regulation of granulopoiesis /  histone deacetylase binding / structural constituent of chromatin / UCH proteinases / histone deacetylase binding / structural constituent of chromatin / UCH proteinases /  ヌクレオソーム / antimicrobial humoral immune response mediated by antimicrobial peptide / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks ヌクレオソーム / antimicrobial humoral immune response mediated by antimicrobial peptide / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) / Homo sapiens (ヒト) /   Escherichia coli (大腸菌) / Escherichia coli (大腸菌) /   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.85 Å クライオ電子顕微鏡法 / 解像度: 2.85 Å | |||||||||
 データ登録者 データ登録者 | Lian T / Guan R / Bai Y | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2024 ジャーナル: Nat Struct Mol Biol / 年: 2024タイトル: Structural mechanism of synergistic targeting of the CX3CR1 nucleosome by PU.1 and C/EBPα. 著者: Tengfei Lian / Ruifang Guan / Bing-Rui Zhou / Yawen Bai /  要旨: Pioneer transcription factors are vital for cell fate changes. PU.1 and C/EBPα work together to regulate hematopoietic stem cell differentiation. However, how they recognize in vivo nucleosomal DNA ...Pioneer transcription factors are vital for cell fate changes. PU.1 and C/EBPα work together to regulate hematopoietic stem cell differentiation. However, how they recognize in vivo nucleosomal DNA targets remains elusive. Here we report the structures of the nucleosome containing the mouse genomic CX3CR1 enhancer DNA and its complexes with PU.1 alone and with both PU.1 and the C/EBPα DNA binding domain. Our structures reveal that PU.1 binds the DNA motif at the exit linker, shifting 17 bp of DNA into the core region through interactions with H2A, unwrapping ~20 bp of nucleosomal DNA. C/EBPα binding, aided by PU.1's repositioning, unwraps ~25 bp of entry DNA. The PU.1 Q218H mutation, linked to acute myeloid leukemia, disrupts PU.1-H2A interactions. PU.1 and C/EBPα jointly displace linker histone H1 and open the H1-condensed nucleosome array. Our study unveils how two pioneer factors can work cooperatively to open closed chromatin by altering DNA positioning in the nucleosome. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
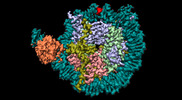
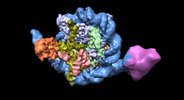
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28629.map.gz emd_28629.map.gz | 43.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28629-v30.xml emd-28629-v30.xml emd-28629.xml emd-28629.xml | 21.5 KB 21.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_28629.png emd_28629.png | 40.8 KB | ||
| Filedesc metadata |  emd-28629.cif.gz emd-28629.cif.gz | 6.7 KB | ||
| その他 |  emd_28629_half_map_1.map.gz emd_28629_half_map_1.map.gz emd_28629_half_map_2.map.gz emd_28629_half_map_2.map.gz | 41.1 MB 41.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28629 http://ftp.pdbj.org/pub/emdb/structures/EMD-28629 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28629 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28629 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28629.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28629.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.056 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_28629_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
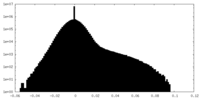
| 投影像・断面図 |
| ||||||||||||
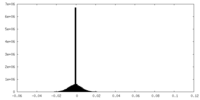
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_28629_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
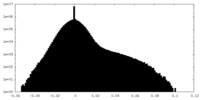
| 投影像・断面図 |
| ||||||||||||
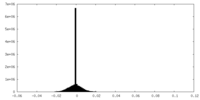
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : nucleosome PU.1 complex
| 全体 | 名称: nucleosome PU.1 complex |
|---|---|
| 要素 |
|
-超分子 #1: nucleosome PU.1 complex
| 超分子 | 名称: nucleosome PU.1 complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#8 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Histone H3.1
| 分子 | 名称: Histone H3.1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 15.437167 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MARTKQTARK STGGKAPRKQ LATKAARKSA PATGGVKKPH RYRPGTVALR EIRRYQKSTE LLIRKLPFQR LVREIAQDFK TDLRFQSSA VMALQEACEA YLVGLFEDTN LCAIHAKRVT IMPKDIQLAR RIRGERA UniProtKB:  ヒストンH3 ヒストンH3 |
-分子 #2: Histone H4
| 分子 | 名称: Histone H4 / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 11.394426 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MSGRGKGGKG LGKGGAKRHR KVLRDNIQGI TKPAIRRLAR RGGVKRISGL IYEETRGVLK VFLENVIRDA VTYTEHAKRK TVTAMDVVY ALKRQGRTLY GFGG UniProtKB:  ヒストンH4 ヒストンH4 |
-分子 #3: Histone H2A type 2-C
| 分子 | 名称: Histone H2A type 2-C / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 14.017428 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MSGRGKQGGK ARAKAKSRSS RAGLQFPVGR VHRLLRKGNY AERVGAGAPV YMAAVLEYLT AEILELAGNA ARDNKKTRII PRHLQLAIR NDEELNKLLG KVTIAQGGVL PNIQAVLLPK KTESHKAKSK UniProtKB: Histone H2A type 2-C |
-分子 #4: Histone H2B type 2-E
| 分子 | 名称: Histone H2B type 2-E / タイプ: protein_or_peptide / ID: 4 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 13.951239 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MPEPAKSAPA PKKGSKKAVT KAQKKDGKKR KRSRKESYSI YVYKVLKQVH PDTGISSKAM GIMNSFVNDI FERIAGEASR LAHYNKRST ITSREIQTAV RLLLPGELAK HAVSEGTKAV TKYTSSK UniProtKB: Histone H2B type 2-E |
-分子 #7: Single-chain variable fragment
| 分子 | 名称: Single-chain variable fragment / タイプ: protein_or_peptide / ID: 7 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 分子量 | 理論値: 29.030146 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MKSSHHHHHH ENLYFQSNAM EVQLQQSGPE LVEPGTSVKM PCKASGYTFT SYTIQWVKQT PRQGLEWIGY IYPYNAGTKY NEKFKGKAT LTSDKSSSTV YMELSSLTSE DSAVYYCARK SSRLRSTLDY WGQGTSVTVS SGGGGSGGGG SGGGGSMDIK M TQSPSSMH ...文字列: MKSSHHHHHH ENLYFQSNAM EVQLQQSGPE LVEPGTSVKM PCKASGYTFT SYTIQWVKQT PRQGLEWIGY IYPYNAGTKY NEKFKGKAT LTSDKSSSTV YMELSSLTSE DSAVYYCARK SSRLRSTLDY WGQGTSVTVS SGGGGSGGGG SGGGGSMDIK M TQSPSSMH ASLGERVTIT CKASQDIRSY LSWYQQKPWK SPKTLIYYAT SLADGVPSRF SGSGSGQDFS LTINNLESDD TA TYYCLQH GESPYTFGSG TKLEIKRA |
-分子 #8: Transcription factor PU.1
| 分子 | 名称: Transcription factor PU.1 / タイプ: protein_or_peptide / ID: 8 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 分子量 | 理論値: 32.81975 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MGSSHHHHHH SSGMLQACKM EGFSLTAPPS DDLVTYDSEL YQRPMHDYYS FVGSDGESHS DHYWDFSAHH VHNNEFENFP ENHFTELQS VQPPQLQQLY RHMELEQMHV LDTPMVPPHT GLSHQVSYMP RMCFPYQTLS PAHQQSSDEE EGERQSPPLE V SDGEADGL ...文字列: MGSSHHHHHH SSGMLQACKM EGFSLTAPPS DDLVTYDSEL YQRPMHDYYS FVGSDGESHS DHYWDFSAHH VHNNEFENFP ENHFTELQS VQPPQLQQLY RHMELEQMHV LDTPMVPPHT GLSHQVSYMP RMCFPYQTLS PAHQQSSDEE EGERQSPPLE V SDGEADGL EPGPGLLHGE TGSKKKIRLY QFLLDLLRSG DMKDSIWWVD KDKGTFQFSS KHKEALAHRW GIQKGNRKKM TY QKMARAL RNYGKTGEVK KVKKKLTYQF SGEVLGRGGL AERRLPPH UniProtKB: Transcription factor PU.1 |
-分子 #5: DNA (162-MER)
| 分子 | 名称: DNA (162-MER) / タイプ: dna / ID: 5 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 分子量 | 理論値: 50.043855 KDa |
| 配列 | 文字列: (DT)(DA)(DG)(DG)(DT)(DG)(DC)(DA)(DG)(DG) (DG)(DC)(DC)(DT)(DC)(DT)(DC)(DG)(DG)(DC) (DT)(DG)(DC)(DT)(DG)(DA)(DT)(DC)(DT) (DT)(DC)(DA)(DG)(DC)(DT)(DG)(DG)(DT)(DT) (DG) (DC)(DT)(DG)(DA)(DG) ...文字列: (DT)(DA)(DG)(DG)(DT)(DG)(DC)(DA)(DG)(DG) (DG)(DC)(DC)(DT)(DC)(DT)(DC)(DG)(DG)(DC) (DT)(DG)(DC)(DT)(DG)(DA)(DT)(DC)(DT) (DT)(DC)(DA)(DG)(DC)(DT)(DG)(DG)(DT)(DT) (DG) (DC)(DT)(DG)(DA)(DG)(DA)(DG)(DT) (DT)(DG)(DC)(DA)(DG)(DC)(DA)(DT)(DT)(DG) (DC)(DT) (DG)(DA)(DG)(DT)(DC)(DT)(DT) (DA)(DG)(DC)(DA)(DA)(DT)(DG)(DG)(DA)(DT) (DA)(DC)(DT) (DT)(DC)(DC)(DC)(DG)(DA) (DT)(DT)(DC)(DC)(DC)(DC)(DT)(DC)(DA)(DC) (DA)(DA)(DA)(DA) (DA)(DT)(DA)(DG)(DG) (DT)(DC)(DA)(DG)(DT)(DC)(DT)(DG)(DT)(DC) (DT)(DG)(DG)(DC)(DT) (DA)(DG)(DT)(DT) (DC)(DT)(DG)(DT)(DA)(DC)(DT)(DT)(DG)(DC) (DA)(DG)(DA)(DC)(DA)(DC) (DA)(DG)(DG) (DG)(DC)(DA)(DT)(DG)(DT)(DG)(DG)(DG)(DG) (DT)(DT)(DC)(DC)(DT)(DA)(DT) (DT)(DT) |
-分子 #6: DNA (162-MER)
| 分子 | 名称: DNA (162-MER) / タイプ: dna / ID: 6 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 分子量 | 理論値: 49.965957 KDa |
| 配列 | 文字列: (DA)(DA)(DA)(DT)(DA)(DG)(DG)(DA)(DA)(DC) (DC)(DC)(DC)(DA)(DC)(DA)(DT)(DG)(DC)(DC) (DC)(DT)(DG)(DT)(DG)(DT)(DC)(DT)(DG) (DC)(DA)(DA)(DG)(DT)(DA)(DC)(DA)(DG)(DA) (DA) (DC)(DT)(DA)(DG)(DC) ...文字列: (DA)(DA)(DA)(DT)(DA)(DG)(DG)(DA)(DA)(DC) (DC)(DC)(DC)(DA)(DC)(DA)(DT)(DG)(DC)(DC) (DC)(DT)(DG)(DT)(DG)(DT)(DC)(DT)(DG) (DC)(DA)(DA)(DG)(DT)(DA)(DC)(DA)(DG)(DA) (DA) (DC)(DT)(DA)(DG)(DC)(DC)(DA)(DG) (DA)(DC)(DA)(DG)(DA)(DC)(DT)(DG)(DA)(DC) (DC)(DT) (DA)(DT)(DT)(DT)(DT)(DT)(DG) (DT)(DG)(DA)(DG)(DG)(DG)(DG)(DA)(DA)(DT) (DC)(DG)(DG) (DG)(DA)(DA)(DG)(DT)(DA) (DT)(DC)(DC)(DA)(DT)(DT)(DG)(DC)(DT)(DA) (DA)(DG)(DA)(DC) (DT)(DC)(DA)(DG)(DC) (DA)(DA)(DT)(DG)(DC)(DT)(DG)(DC)(DA)(DA) (DC)(DT)(DC)(DT)(DC) (DA)(DG)(DC)(DA) (DA)(DC)(DC)(DA)(DG)(DC)(DT)(DG)(DA)(DA) (DG)(DA)(DT)(DC)(DA)(DG) (DC)(DA)(DG) (DC)(DC)(DG)(DA)(DG)(DA)(DG)(DG)(DC)(DC) (DC)(DT)(DG)(DC)(DA)(DC)(DC) (DT)(DA) |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.3 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 53.8 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.85 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 89583 |
 ムービー
ムービー コントローラー
コントローラー
















 Z
Z Y
Y X
X