+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21511 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of 5HT3A receptor in presence of Alosetron | |||||||||
 マップデータ マップデータ | 5HT3A receptor in presence of Alosetron | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Neurotransmitter receptors and postsynaptic signal transmission / serotonin-gated monoatomic cation channel activity / serotonin-activated cation-selective channel complex / serotonin receptor signaling pathway /  serotonin binding / acetylcholine-gated monoatomic cation-selective channel activity / inorganic cation transmembrane transport / extracellular ligand-gated monoatomic ion channel activity / serotonin binding / acetylcholine-gated monoatomic cation-selective channel activity / inorganic cation transmembrane transport / extracellular ligand-gated monoatomic ion channel activity /  分裂溝 / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential ...Neurotransmitter receptors and postsynaptic signal transmission / serotonin-gated monoatomic cation channel activity / serotonin-activated cation-selective channel complex / serotonin receptor signaling pathway / 分裂溝 / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential ...Neurotransmitter receptors and postsynaptic signal transmission / serotonin-gated monoatomic cation channel activity / serotonin-activated cation-selective channel complex / serotonin receptor signaling pathway /  serotonin binding / acetylcholine-gated monoatomic cation-selective channel activity / inorganic cation transmembrane transport / extracellular ligand-gated monoatomic ion channel activity / serotonin binding / acetylcholine-gated monoatomic cation-selective channel activity / inorganic cation transmembrane transport / extracellular ligand-gated monoatomic ion channel activity /  分裂溝 / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / transmembrane signaling receptor activity / 分裂溝 / ligand-gated monoatomic ion channel activity involved in regulation of presynaptic membrane potential / transmembrane signaling receptor activity /  presynaptic membrane / presynaptic membrane /  postsynaptic membrane / neuron projection / postsynaptic membrane / neuron projection /  神経繊維 / neuronal cell body / glutamatergic synapse / 神経繊維 / neuronal cell body / glutamatergic synapse /  シナプス / identical protein binding シナプス / identical protein binding類似検索 - 分子機能 | |||||||||
| 生物種 |   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.92 Å クライオ電子顕微鏡法 / 解像度: 2.92 Å | |||||||||
 データ登録者 データ登録者 | Basak S / Chakrapani S | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019タイトル: Molecular mechanism of setron-mediated inhibition of full-length 5-HT receptor. 著者: Sandip Basak / Yvonne Gicheru / Abhijeet Kapoor / Megan L Mayer / Marta Filizola / Sudha Chakrapani /  要旨: Serotonin receptor (5-HTR) is the most common therapeutic target to manage the nausea and vomiting during cancer therapies and in the treatment of irritable bowel syndrome. Setrons, a class of ...Serotonin receptor (5-HTR) is the most common therapeutic target to manage the nausea and vomiting during cancer therapies and in the treatment of irritable bowel syndrome. Setrons, a class of competitive antagonists, cause functional inhibition of 5-HTR in the gastrointestinal tract and brainstem, acting as effective anti-emetic agents. Despite their prevalent use, the molecular mechanisms underlying setron binding and inhibition of 5-HTR are not fully understood. Here, we present the structure of granisetron-bound full-length 5-HTR solved by single-particle cryo-electron microscopy to 2.92 Å resolution. The reconstruction reveals the orientation of granisetron in the orthosteric site with unambiguous density for interacting sidechains. Molecular dynamics simulations and electrophysiology confirm the granisetron binding orientation and the residues central for ligand recognition. Comparison of granisetron-bound 5-HTR with the apo and serotonin-bound structures, reveals key insights into the mechanism underlying 5-HTR inhibition. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21511.map.gz emd_21511.map.gz | 10.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21511-v30.xml emd-21511-v30.xml emd-21511.xml emd-21511.xml | 19.4 KB 19.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_21511.png emd_21511.png | 287.9 KB | ||
| マスクデータ |  emd_21511_msk_1.map emd_21511_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| その他 |  emd_21511_half_map_1.map.gz emd_21511_half_map_1.map.gz emd_21511_half_map_2.map.gz emd_21511_half_map_2.map.gz | 80.5 MB 80.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21511 http://ftp.pdbj.org/pub/emdb/structures/EMD-21511 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21511 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21511 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21511.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21511.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 5HT3A receptor in presence of Alosetron | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.848 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
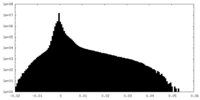
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_21511_msk_1.map emd_21511_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
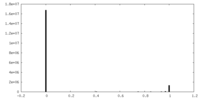
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_21511_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
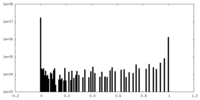
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_21511_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
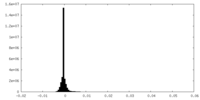
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Serotonin receptor
| 全体 | 名称: Serotonin receptor セロトニン受容体 セロトニン受容体 |
|---|---|
| 要素 |
|
-超分子 #1: Serotonin receptor
| 超分子 | 名称: Serotonin receptor / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 組換発現 | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ)組換細胞: sf9 |
| 分子量 | 理論値: 270 KDa |
-分子 #1: 5-hydroxytryptamine receptor 3A
| 分子 | 名称: 5-hydroxytryptamine receptor 3A / タイプ: protein_or_peptide / ID: 1 / コピー数: 5 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 分子量 | 理論値: 52.042121 KDa |
| 組換発現 | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ) |
| 配列 | 文字列: TTQPALLRLS DHLLANYKKG VRPVRDWRKP TTVSIDVIMY AILNVDEKNQ VLTTYIWYRQ YWTDEFLQWT PEDFDNVTKL SIPTDSIWV PDILINEFVD VGKSPNIPYV YVHHRGEVQN YKPLQLVTAC SLDIYNFPFD VQNCSLTFTS WLHTIQDINI T LWRSPEEV ...文字列: TTQPALLRLS DHLLANYKKG VRPVRDWRKP TTVSIDVIMY AILNVDEKNQ VLTTYIWYRQ YWTDEFLQWT PEDFDNVTKL SIPTDSIWV PDILINEFVD VGKSPNIPYV YVHHRGEVQN YKPLQLVTAC SLDIYNFPFD VQNCSLTFTS WLHTIQDINI T LWRSPEEV RSDKSIFINQ GEWELLEVFP QFKEFSIDIS NSYAEMKFYV IIRRRPLFYA VSLLLPSIFL MVVDIVGFCL PP DSGERVS FKITLLLGYS VFLIIVSDTL PATAIGTPLI GVYFVVCMAL LVISLAETIF IVRLVHKQDL QRPVPDWLRH LVL DRIAWI LCLGEQPMAH RPPATFQANK TDDCSAMGNH CSHVGGPQDL EKTPRGRGSP LPPPREASLA VRGLLQELSS IRHF LEKRD EMREVARDWL RVGYVLDRLL FRIYLLAVLA YSITLVTLWS IWHYS |
-分子 #5: alosetron
| 分子 | 名称: alosetron / タイプ: ligand / ID: 5 / コピー数: 5 / 式: S7Y |
|---|---|
| 分子量 | 理論値: 294.351 Da |
| Chemical component information | 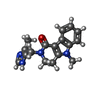 ChemComp-S7Y: |
-分子 #6: CHLORIDE ION
| 分子 | 名称: CHLORIDE ION / タイプ: ligand / ID: 6 / コピー数: 1 / 式: CL |
|---|---|
| 分子量 | 理論値: 35.453 Da |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3 mg/mL |
|---|---|
| 緩衝液 | pH: 8 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK I / 詳細: blot for 2.5 seconds. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 倍率(公称値): 105000 Bright-field microscopy / Cs: 2.7 mm / 倍率(公称値): 105000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 検出モード: SUPER-RESOLUTION / デジタル化 - 画像ごとのフレーム数: 1-30 / 実像数: 4350 / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 粒子像選択 | 選択した数: 568452 |
|---|---|
| CTF補正 | ソフトウェア - 名称: Gctf (ver. 1.06) |
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 3次元分類 | ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 角度割当 | タイプ: ANGULAR RECONSTITUTION / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 再構成 | 想定した対称性 - 点群: C5 (5回回転対称 ) / 解像度のタイプ: BY AUTHOR / 解像度: 2.92 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1) / 使用した粒子像数: 42065 ) / 解像度のタイプ: BY AUTHOR / 解像度: 2.92 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1) / 使用した粒子像数: 42065 |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: OTHER / 温度因子: 30 |
|---|---|
| 得られたモデル |  PDB-6w1j: |
 ムービー
ムービー コントローラー
コントローラー



















 Z
Z Y
Y X
X