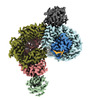
登録情報 データベース : EMDB / ID : EMD-14312タイトル phospho-STING binding to adaptor protein complex-1 複合体 : phospho-STING binding to adaptor protein complex-1タンパク質・ペプチド : AP-1 complex subunit beta-1タンパク質・ペプチド : ADP-ribosylation factor 1タンパク質・ペプチド : AP-1 complex subunit gamma-1タンパク質・ペプチド : Stimulator of interferon genes proteinタンパク質・ペプチド : AP-1 complex subunit mu-1タンパク質・ペプチド : AP-1 complex subunit sigma-3リガンド : GUANOSINE-5'-TRIPHOSPHATEリガンド : MAGNESIUM ION機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Homo sapiens (ヒト) / Mus musculus (ハツカネズミ)手法 / / 解像度 : 2.34 Å Xu P / Ablasser A 資金援助 European Union, 1件 Organization Grant number 国 European Molecular Biology Organization (EMBO) ALTF-184 European Union
ジャーナル : Nature / 年 : 2022タイトル : Clathrin-associated AP-1 controls termination of STING signalling.著者 : Ying Liu / Pengbiao Xu / Sophie Rivara / Chong Liu / Jonathan Ricci / Xuefeng Ren / James H Hurley / Andrea Ablasser / 要旨 : Stimulator of interferon genes (STING) functions downstream of cyclic GMP-AMP synthase in DNA sensing or as a direct receptor for bacterial cyclic dinucleotides and small molecules to activate ... Stimulator of interferon genes (STING) functions downstream of cyclic GMP-AMP synthase in DNA sensing or as a direct receptor for bacterial cyclic dinucleotides and small molecules to activate immunity during infection, cancer and immunotherapy. Precise regulation of STING is essential to ensure balanced immune responses and prevent detrimental autoinflammation. After activation, STING, a transmembrane protein, traffics from the endoplasmic reticulum to the Golgi, where its phosphorylation by the protein kinase TBK1 enables signal transduction. The mechanism that ends STING signalling at the Golgi remains unknown. Here we show that adaptor protein complex 1 (AP-1) controls the termination of STING-dependent immune activation. We find that AP-1 sorts phosphorylated STING into clathrin-coated transport vesicles for delivery to the endolysosomal system, where STING is degraded. We identify a highly conserved dileucine motif in the cytosolic C-terminal tail (CTT) of STING that, together with TBK1-dependent CTT phosphorylation, dictates the AP-1 engagement of STING. A cryo-electron microscopy structure of AP-1 in complex with phosphorylated STING explains the enhanced recognition of TBK1-activated STING. We show that suppression of AP-1 exacerbates STING-induced immune responses. Our results reveal a structural mechanism of negative regulation of STING and establish that the initiation of signalling is inextricably associated with its termination to enable transient activation of immunity. 履歴 登録 2022年2月8日 - ヘッダ(付随情報) 公開 2022年9月14日 - マップ公開 2022年9月14日 - 更新 2022年11月9日 - 現状 2022年11月9日 処理サイト : PDBe / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報
 マップデータ
マップデータ 試料
試料 機能・相同性情報
機能・相同性情報 basolateral protein secretion / mitotic cleavage furrow ingression / AP-1 adaptor complex / trans-Golgi Network Vesicle Budding / endosome to melanosome transport / positive regulation of natural killer cell degranulation / Lysosome Vesicle Biogenesis / platelet dense granule organization /
basolateral protein secretion / mitotic cleavage furrow ingression / AP-1 adaptor complex / trans-Golgi Network Vesicle Budding / endosome to melanosome transport / positive regulation of natural killer cell degranulation / Lysosome Vesicle Biogenesis / platelet dense granule organization /  regulation of receptor internalization /
regulation of receptor internalization /  melanosome assembly ...
melanosome assembly ... basolateral protein secretion / mitotic cleavage furrow ingression / AP-1 adaptor complex / trans-Golgi Network Vesicle Budding / endosome to melanosome transport / positive regulation of natural killer cell degranulation / Lysosome Vesicle Biogenesis / platelet dense granule organization /
basolateral protein secretion / mitotic cleavage furrow ingression / AP-1 adaptor complex / trans-Golgi Network Vesicle Budding / endosome to melanosome transport / positive regulation of natural killer cell degranulation / Lysosome Vesicle Biogenesis / platelet dense granule organization /  regulation of receptor internalization /
regulation of receptor internalization /  melanosome assembly / regulation of Arp2/3 complex-mediated actin nucleation / STING complex / Golgi to lysosome transport / Intra-Golgi traffic / Golgi to vacuole transport / STAT6-mediated induction of chemokines / Synthesis of PIPs at the Golgi membrane / Golgi Associated Vesicle Biogenesis /
melanosome assembly / regulation of Arp2/3 complex-mediated actin nucleation / STING complex / Golgi to lysosome transport / Intra-Golgi traffic / Golgi to vacuole transport / STAT6-mediated induction of chemokines / Synthesis of PIPs at the Golgi membrane / Golgi Associated Vesicle Biogenesis /  serine/threonine protein kinase complex / 2',3'-cyclic GMP-AMP binding /
serine/threonine protein kinase complex / 2',3'-cyclic GMP-AMP binding /  proton channel activity / GTP-dependent protein binding / clathrin adaptor activity / cyclic-di-GMP binding / STING mediated induction of host immune responses / MHC class II antigen presentation / melanosome organization / Nef Mediated CD4 Down-regulation / IRF3-mediated induction of type I IFN / cGAS/STING signaling pathway / dendritic spine organization / positive regulation of type I interferon-mediated signaling pathway / reticulophagy / determination of left/right symmetry / long-term synaptic depression / COPI-dependent Golgi-to-ER retrograde traffic /
proton channel activity / GTP-dependent protein binding / clathrin adaptor activity / cyclic-di-GMP binding / STING mediated induction of host immune responses / MHC class II antigen presentation / melanosome organization / Nef Mediated CD4 Down-regulation / IRF3-mediated induction of type I IFN / cGAS/STING signaling pathway / dendritic spine organization / positive regulation of type I interferon-mediated signaling pathway / reticulophagy / determination of left/right symmetry / long-term synaptic depression / COPI-dependent Golgi-to-ER retrograde traffic /  クラスリン / Lysosome Vesicle Biogenesis / pattern recognition receptor signaling pathway /
クラスリン / Lysosome Vesicle Biogenesis / pattern recognition receptor signaling pathway /  clathrin binding / Golgi Associated Vesicle Biogenesis / positive regulation of natural killer cell mediated cytotoxicity / cellular response to exogenous dsRNA / cytoplasmic pattern recognition receptor signaling pathway / cell leading edge / autophagosome membrane / Synthesis of PIPs at the plasma membrane / antiviral innate immune response /
clathrin binding / Golgi Associated Vesicle Biogenesis / positive regulation of natural killer cell mediated cytotoxicity / cellular response to exogenous dsRNA / cytoplasmic pattern recognition receptor signaling pathway / cell leading edge / autophagosome membrane / Synthesis of PIPs at the plasma membrane / antiviral innate immune response /  kinesin binding /
kinesin binding /  autophagosome assembly / positive regulation of macroautophagy / intracellular copper ion homeostasis / cellular response to organic cyclic compound /
autophagosome assembly / positive regulation of macroautophagy / intracellular copper ion homeostasis / cellular response to organic cyclic compound /  オートファゴソーム /
オートファゴソーム /  protein targeting / positive regulation of type I interferon production / cellular response to interferon-beta / signaling adaptor activity / COPI-mediated anterograde transport /
protein targeting / positive regulation of type I interferon production / cellular response to interferon-beta / signaling adaptor activity / COPI-mediated anterograde transport /  クラスリン / vesicle-mediated transport / positive regulation of defense response to virus by host / MHC class II antigen presentation / Regulation of innate immune responses to cytosolic DNA / Gene and protein expression by JAK-STAT signaling after Interleukin-12 stimulation / activation of innate immune response / Neutrophil degranulation / endoplasmic reticulum-Golgi intermediate compartment membrane / positive regulation of interferon-beta production /
クラスリン / vesicle-mediated transport / positive regulation of defense response to virus by host / MHC class II antigen presentation / Regulation of innate immune responses to cytosolic DNA / Gene and protein expression by JAK-STAT signaling after Interleukin-12 stimulation / activation of innate immune response / Neutrophil degranulation / endoplasmic reticulum-Golgi intermediate compartment membrane / positive regulation of interferon-beta production /  sarcomere /
sarcomere /  低分子量GTPアーゼ / secretory granule membrane / trans-Golgi network membrane / Nef mediated downregulation of MHC class I complex cell surface expression /
低分子量GTPアーゼ / secretory granule membrane / trans-Golgi network membrane / Nef mediated downregulation of MHC class I complex cell surface expression /  kidney development /
kidney development /  intracellular protein transport / cytoplasmic vesicle membrane /
intracellular protein transport / cytoplasmic vesicle membrane /  ゴルジ体 / recycling endosome / cellular response to virus /
ゴルジ体 / recycling endosome / cellular response to virus /  small GTPase binding /
small GTPase binding /  ペルオキシソーム / SARS-CoV-1 activates/modulates innate immune responses / positive regulation of DNA-binding transcription factor activity / protein complex oligomerization /
ペルオキシソーム / SARS-CoV-1 activates/modulates innate immune responses / positive regulation of DNA-binding transcription factor activity / protein complex oligomerization /  heart development / positive regulation of protein binding /
heart development / positive regulation of protein binding /  regulation of inflammatory response / defense response to virus / mitochondrial outer membrane / RNA polymerase II-specific DNA-binding transcription factor binding /
regulation of inflammatory response / defense response to virus / mitochondrial outer membrane / RNA polymerase II-specific DNA-binding transcription factor binding /  postsynaptic density /
postsynaptic density /  エンドソーム /
エンドソーム /  エンドソーム / neuron projection / lysosomal membrane / protein domain specific binding /
エンドソーム / neuron projection / lysosomal membrane / protein domain specific binding /  ゴルジ体 /
ゴルジ体 /  focal adhesion / intracellular membrane-bounded organelle
focal adhesion / intracellular membrane-bounded organelle
 Homo sapiens (ヒト) /
Homo sapiens (ヒト) / 
 Mus musculus (ハツカネズミ)
Mus musculus (ハツカネズミ) 単粒子再構成法 /
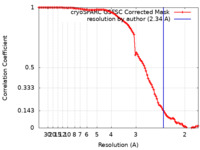
単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.34 Å
クライオ電子顕微鏡法 / 解像度: 2.34 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Nature / 年: 2022
ジャーナル: Nature / 年: 2022

 構造の表示
構造の表示 ダウンロードとリンク
ダウンロードとリンク emd_14312.map.gz
emd_14312.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-14312-v30.xml
emd-14312-v30.xml emd-14312.xml
emd-14312.xml EMDBヘッダ
EMDBヘッダ emd_14312_fsc.xml
emd_14312_fsc.xml FSCデータファイル
FSCデータファイル emd_14312.png
emd_14312.png emd_14312_half_map_1.map.gz
emd_14312_half_map_1.map.gz emd_14312_half_map_2.map.gz
emd_14312_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-14312
http://ftp.pdbj.org/pub/emdb/structures/EMD-14312 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14312
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14312
 F&H 検索
F&H 検索 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_14312.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_14312.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) 試料の構成要素
試料の構成要素
 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 Mus musculus (ハツカネズミ)
Mus musculus (ハツカネズミ)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 Mus musculus (ハツカネズミ)
Mus musculus (ハツカネズミ)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 Escherichia coli BL21(DE3) (大腸菌)
Escherichia coli BL21(DE3) (大腸菌)
 クライオ電子顕微鏡法
クライオ電子顕微鏡法 解析
解析 単粒子再構成法
単粒子再構成法 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN Bright-field microscopy / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm
Bright-field microscopy / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm
 ムービー
ムービー コントローラー
コントローラー






































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)