+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1356 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structural basis for the PufX-mediated dimerization of bacterial photosynthetic core complexes. | |||||||||
 マップデータ マップデータ | 3D map file of Rhobacter veldkampii LH1-RC obtained by cryoEM and low-pass filtered at a resolution of 11 angstroems | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Rhodobacter veldkampii (バクテリア) Rhodobacter veldkampii (バクテリア) | |||||||||
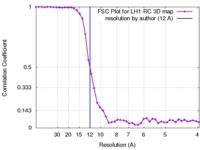
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / ネガティブ染色法 / 解像度: 12.0 Å | |||||||||
 データ登録者 データ登録者 | Busselez J / Cottevieille M / Cuniasse P / Boisset N / Levy D | |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2007 ジャーナル: Structure / 年: 2007タイトル: Structural basis for the PufX-mediated dimerization of bacterial photosynthetic core complexes. 著者: Johan Busselez / Magali Cottevieille / Philippe Cuniasse / Francesca Gubellini / Nicolas Boisset / Daniel Lévy /  要旨: In Rhodobacter (Rba.) sphaeroides, the subunit PufX is involved in the dimeric organization of the core complex. Here, we report the 3D reconstruction at 12 A by cryoelectron microscopy of the core ...In Rhodobacter (Rba.) sphaeroides, the subunit PufX is involved in the dimeric organization of the core complex. Here, we report the 3D reconstruction at 12 A by cryoelectron microscopy of the core complex of Rba. veldkampii, a complex of approximately 300 kDa without symmetry. The core complex is monomeric and constituted by a light-harvesting complex 1 (LH1) ring surrounding a uniquely oriented reaction center (RC). The LH1 consists of 15 resolved alpha/beta heterodimers and is interrupted. Within the opening, PufX polypeptide is assigned at a position facing the Q(B) site of the RC. This core complex is different from a dissociated dimer of the core complex of Rba. sphaeroides revealing that PufX in Rba. veldkampii is unable to dimerize. The absence in PufX of Rba. veldkampii of a G(31)XXXG(35) dimerization motif highlights the transmembrane interactions between PufX subunits involved in the dimerization of the core complexes of Rhodobacter species. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1356.map.gz emd_1356.map.gz | 5.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1356-v30.xml emd-1356-v30.xml emd-1356.xml emd-1356.xml | 9.5 KB 9.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_1356_fsc.xml emd_1356_fsc.xml | 4.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  EMD-1356.png EMD-1356.png emd_1356.tif emd_1356.tif | 148.4 KB 145.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1356 http://ftp.pdbj.org/pub/emdb/structures/EMD-1356 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1356 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1356 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1356_validation.pdf.gz emd_1356_validation.pdf.gz | 250.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1356_full_validation.pdf.gz emd_1356_full_validation.pdf.gz | 249.7 KB | 表示 | |
| XML形式データ |  emd_1356_validation.xml.gz emd_1356_validation.xml.gz | 7.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1356 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1356 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1356 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1356 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1356.map.gz / 形式: CCP4 / 大きさ: 5.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1356.map.gz / 形式: CCP4 / 大きさ: 5.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3D map file of Rhobacter veldkampii LH1-RC obtained by cryoEM and low-pass filtered at a resolution of 11 angstroems | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.95 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Core complex of Rhodobacter veldkampii
| 全体 | 名称: Core complex of Rhodobacter veldkampii |
|---|---|
| 要素 |
|
-超分子 #1000: Core complex of Rhodobacter veldkampii
| 超分子 | 名称: Core complex of Rhodobacter veldkampii / タイプ: sample / ID: 1000 / 集合状態: monomers / Number unique components: 1 |
|---|---|
| 分子量 | 理論値: 300 KDa |
-分子 #1: core complex of Rba. veldkampii
| 分子 | 名称: core complex of Rba. veldkampii / タイプ: protein_or_peptide / ID: 1 / Name.synonym: LH1-RC of Rba. veldkampii / コピー数: 1 / 集合状態: Monomer / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:  Rhodobacter veldkampii (バクテリア) / 株: DSM 11550 Rhodobacter veldkampii (バクテリア) / 株: DSM 11550 |
| 分子量 | 実験値: 300 KDa |
-実験情報
-構造解析
| 手法 | ネガティブ染色法, クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.6 / 詳細: Glycine-glycine 50 mM, NaCl 200 mM, DOTM 0.1 % |
| 染色 | タイプ: NEGATIVE 詳細: CRYOEM : 4 microL were applied on a Lacey Formwar grid. |
| 凍結 | 凍結剤: ETHANE / チャンバー内温度: 93 K / 装置: HOMEMADE PLUNGER / 詳細: Vitrification instrument: manual plunger / 手法: Manual single-sided blotting |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 2010F |
|---|---|
| 温度 | 最低: 93 K / 最高: 94 K |
| 詳細 | low-dose illumination |
| 日付 | 2005年6月1日 |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: OTHER / 実像数: 74 / 平均電子線量: 10 e/Å2 / 詳細: Scanner model : Nikon Coolscan 8000ED / ビット/ピクセル: 8 |
| Tilt angle min | 0 |
| Tilt angle max | 0 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 45000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.0 mm / 最大 デフォーカス(公称値): 3.46 µm / 最小 デフォーカス(公称値): 1.87 µm / 倍率(公称値): 45000 |
| 試料ステージ | 試料ホルダー: Gatan / 試料ホルダーモデル: GATAN LIQUID NITROGEN |
 ムービー
ムービー コントローラー
コントローラー