+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9q62 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Human prolyl endopeptidase (PREP) - complex with KT-2-108 | ||||||
 要素 要素 | Prolyl endopeptidase | ||||||
 キーワード キーワード | HYDROLASE/HYDROLASE INHIBITOR / inhibitor-bound / peptide cleavage / HYDROLASE / HYDROLASE-HYDROLASE INHIBITOR complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報prolyl oligopeptidase / oligopeptidase activity / angiotensin maturation / metallocarboxypeptidase activity / serine-type peptidase activity / serine-type endopeptidase activity / proteolysis / extracellular region / membrane / nucleus ...prolyl oligopeptidase / oligopeptidase activity / angiotensin maturation / metallocarboxypeptidase activity / serine-type peptidase activity / serine-type endopeptidase activity / proteolysis / extracellular region / membrane / nucleus / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.83 Å 分子置換 / 解像度: 1.83 Å | ||||||
 データ登録者 データ登録者 | Fucci, I.J. / Thakur, K. / Pandian, J. / Yoo, E. / Monteiro, D.C.F. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2026 ジャーナル: J.Med.Chem. / 年: 2026タイトル: Structure-Guided Optimization of 4-Chloro-Pyrazolopyridine Analogs for Covalent PREP Inhibition. 著者: Thakur, K. / Fucci, I. / Pandian, J. / Suazo, K.F. / Monteiro, D.C.F. / Yoo, E. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9q62.cif.gz 9q62.cif.gz | 1.9 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9q62.ent.gz pdb9q62.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  9q62.json.gz 9q62.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/q6/9q62 https://data.pdbj.org/pub/pdb/validation_reports/q6/9q62 ftp://data.pdbj.org/pub/pdb/validation_reports/q6/9q62 ftp://data.pdbj.org/pub/pdb/validation_reports/q6/9q62 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  9q5gC  9q5xC  9q5yC  9q5zC  9q64C  9q65C  9q66C  9q6jC  9q6kC  9q6lC  9q6xC  9xykC  9xylC  9xzzC C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
| 実験データセット #1 | データ参照:  10.15785/SBGRID/1205 / データの種類: diffraction image data 10.15785/SBGRID/1205 / データの種類: diffraction image data |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 3 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 3分子 ABC
| #1: タンパク質 | 分子量: 80851.367 Da / 分子数: 3 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: PREP, PEP / 発現宿主: Homo sapiens (ヒト) / 遺伝子: PREP, PEP / 発現宿主:  |
|---|
-非ポリマー , 6種, 1423分子 

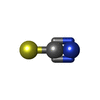






| #2: 化合物 | | #3: 化合物 | ChemComp-B3P / #4: 化合物 | 分子量: 439.938 Da / 分子数: 3 / 由来タイプ: 合成 / 式: C23H26ClN5O2 / タイプ: SUBJECT OF INVESTIGATION #5: 化合物 | ChemComp-SCN / #6: 化合物 | ChemComp-GOL / #7: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.28 Å3/Da / 溶媒含有率: 46 % |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: 25-30% PEG 3350, 200 mM KSCN and 100 mM bis-tris propane pH 7.5 |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  NSLS-II NSLS-II  / ビームライン: 17-ID-1 / 波長: 0.919764 Å / ビームライン: 17-ID-1 / 波長: 0.919764 Å |
| 検出器 | タイプ: DECTRIS EIGER X 9M / 検出器: PIXEL / 日付: 2025年4月5日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.919764 Å / 相対比: 1 |
| 反射 | 解像度: 1.83→43.9 Å / Num. obs: 144444 / % possible obs: 92.1 % / 冗長度: 6.8 % / Biso Wilson estimate: 17.8 Å2 / CC1/2: 0.99 / Rmerge(I) obs: 0.237 / Rpim(I) all: 0.097 / Rrim(I) all: 0.256 / Net I/σ(I): 6.6 |
| 反射 シェル | 解像度: 1.83→2 Å / Rmerge(I) obs: 1.42 / Mean I/σ(I) obs: 1.4 / Num. unique obs: 7222 / CC1/2: 0.38 / Rpim(I) all: 0.589 / Rrim(I) all: 1.536 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 / 解像度: 1.83→43.9 Å / Cor.coef. Fo:Fc: 0.953 / Cor.coef. Fo:Fc free: 0.911 / SU B: 9.18 / SU ML: 0.143 / 交差検証法: FREE R-VALUE / ESU R: 0.194 / ESU R Free: 0.181 / 詳細: Hydrogens have been added in their riding positions 分子置換 / 解像度: 1.83→43.9 Å / Cor.coef. Fo:Fc: 0.953 / Cor.coef. Fo:Fc free: 0.911 / SU B: 9.18 / SU ML: 0.143 / 交差検証法: FREE R-VALUE / ESU R: 0.194 / ESU R Free: 0.181 / 詳細: Hydrogens have been added in their riding positions
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: MASK BULK SOLVENT | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 25.592 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.83→43.9 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj





