+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9mwr | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of human endothelial nitric oxide synthase heme domain bound with N-(4-(2-((3-(thiazole-2-carboximidamido)benzyl)amino)ethyl)phenyl)thiazole-2-carboximidamide | ||||||
 要素 要素 | Nitric oxide synthase, endothelial | ||||||
 キーワード キーワード | OXIDOREDUCTASE / nitric oxide synthase inhibitor binding | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of the force of heart contraction by chemical signal / NOSIP mediated eNOS trafficking / negative regulation of muscle hyperplasia / NOSTRIN mediated eNOS trafficking / tetrahydrobiopterin metabolic process / smooth muscle hyperplasia / regulation of nervous system process / superoxide-generating NAD(P)H oxidase activity / ovulation from ovarian follicle / pulmonary valve morphogenesis ...regulation of the force of heart contraction by chemical signal / NOSIP mediated eNOS trafficking / negative regulation of muscle hyperplasia / NOSTRIN mediated eNOS trafficking / tetrahydrobiopterin metabolic process / smooth muscle hyperplasia / regulation of nervous system process / superoxide-generating NAD(P)H oxidase activity / ovulation from ovarian follicle / pulmonary valve morphogenesis / negative regulation of biomineral tissue development / response to fluid shear stress / Nitric oxide stimulates guanylate cyclase / regulation of systemic arterial blood pressure by endothelin / ROS and RNS production in phagocytes / tetrahydrobiopterin binding / arginine binding / aortic valve morphogenesis / endocardial cushion morphogenesis / ventricular septum morphogenesis / positive regulation of Notch signaling pathway / cadmium ion binding / negative regulation of calcium ion transport / negative regulation of potassium ion transport / negative regulation of platelet activation / nitric-oxide synthase (NADPH) / actin monomer binding / positive regulation of blood vessel endothelial cell migration / : / blood vessel remodeling / nitric-oxide synthase activity / endothelial cell migration / L-arginine catabolic process / negative regulation of extrinsic apoptotic signaling pathway via death domain receptors / regulation of sodium ion transport / nitric oxide metabolic process / eNOS activation / negative regulation of blood pressure / nitric oxide biosynthetic process / Tetrahydrobiopterin (BH4) synthesis, recycling, salvage and regulation / response to hormone / removal of superoxide radicals / lung development / homeostasis of number of cells within a tissue / cell redox homeostasis / lipopolysaccharide-mediated signaling pathway / blood vessel diameter maintenance / VEGFR2 mediated vascular permeability / negative regulation of smooth muscle cell proliferation / potassium ion transport / mitochondrion organization / caveola / vasodilation / regulation of blood pressure / positive regulation of angiogenesis / protein import into nucleus / endocytic vesicle membrane / calcium ion transport / NADP binding / FMN binding / flavin adenine dinucleotide binding / response to heat / scaffold protein binding / angiogenesis / High laminar flow shear stress activates signaling by PIEZO1 and PECAM1:CDH5:KDR in endothelial cells / response to lipopolysaccharide / gene expression / in utero embryonic development / cytoskeleton / calmodulin binding / Extra-nuclear estrogen signaling / negative regulation of cell population proliferation / Golgi membrane / heme binding / positive regulation of gene expression / Golgi apparatus / nucleus / plasma membrane / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  フーリエ合成 / 解像度: 1.97 Å フーリエ合成 / 解像度: 1.97 Å | ||||||
 データ登録者 データ登録者 | Li, H. / Poulos, T.L. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2026 ジャーナル: J.Med.Chem. / 年: 2026タイトル: New Inhibitors of Neuronal Nitric Oxide Synthase for the Treatment of Melanoma. 著者: Awasthi, A. / Patel, A. / Li, H. / Kang, K.M. / Hardy, C.D. / Ansari, A. / Nowar, R. / Hasan, M.E. / Yang, S. / Poulos, T.L. / Silverman, R.B. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9mwr.cif.gz 9mwr.cif.gz | 688.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9mwr.ent.gz pdb9mwr.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  9mwr.json.gz 9mwr.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/mw/9mwr https://data.pdbj.org/pub/pdb/validation_reports/mw/9mwr ftp://data.pdbj.org/pub/pdb/validation_reports/mw/9mwr ftp://data.pdbj.org/pub/pdb/validation_reports/mw/9mwr | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  9mwaC  9mwbC  9mwcC  9mwdC  9mweC  9mwfC  9mwgC  9mwhC  9mwiC  9mwjC  9mwkC  9mwlC  9mwmC  9mwnC  9mwoC  9mwpC  9mwqC  9mwsC  9mwtC  9mwuC  9mwvC  9mwwC  9mwxC C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 4分子 ABCD
| #1: タンパク質 | 分子量: 49345.770 Da / 分子数: 4 / 断片: heme domain / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / Cell: endothelial / 遺伝子: NOS3 / プラスミド: pCWori / 発現宿主: Homo sapiens (ヒト) / Cell: endothelial / 遺伝子: NOS3 / プラスミド: pCWori / 発現宿主:  |
|---|
-非ポリマー , 11種, 976分子 
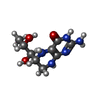

















| #2: 化合物 | ChemComp-HEM / #3: 化合物 | ChemComp-H4B / #4: 化合物 | ChemComp-A1BTV / 分子量: 461.606 Da / 分子数: 4 / 由来タイプ: 合成 / 式: C23H23N7S2 / タイプ: SUBJECT OF INVESTIGATION #5: 化合物 | #6: 化合物 | ChemComp-BTB / #7: 化合物 | ChemComp-GOL / #8: 化合物 | ChemComp-CL / #9: 化合物 | ChemComp-GD / #10: 化合物 | #11: 化合物 | #12: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.44 Å3/Da / 溶媒含有率: 54.3 % / 解説: rods |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: 10-12% PEG3350, 0.1M BIS-TRIS 0.2-0.3M MG ACETATE 0.1M GDCL3 10% GLYCEROL, 5 MM TCEP |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  ALS ALS  / ビームライン: 8.2.1 / 波長: 1 Å / ビームライン: 8.2.1 / 波長: 1 Å |
| 検出器 | タイプ: DECTRIS PILATUS 6M / 検出器: PIXEL / 日付: 2024年5月8日 / 詳細: mirrors |
| 放射 | モノクロメーター: DOUBLE CRYSTAL SI(III) / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1 Å / 相対比: 1 |
| 反射 | 解像度: 1.97→49.1 Å / Num. obs: 127972 / % possible obs: 96.3 % / 冗長度: 5.1 % / CC1/2: 0.995 / Rmerge(I) obs: 0.094 / Rpim(I) all: 0.046 / Rrim(I) all: 0.104 / Net I/σ(I): 8.4 / Num. measured all: 651628 |
| 反射 シェル | 解像度: 1.97→2 Å / 冗長度: 4.7 % / Rmerge(I) obs: 0.402 / Num. unique obs: 5658 / CC1/2: 0.902 / Rpim(I) all: 0.203 / Rrim(I) all: 0.452 / % possible all: 86.2 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  フーリエ合成 / 解像度: 1.97→49.099 Å / SU ML: 0.21 / 交差検証法: FREE R-VALUE / σ(F): 0.23 / 位相誤差: 22.04 / 立体化学のターゲット値: ML フーリエ合成 / 解像度: 1.97→49.099 Å / SU ML: 0.21 / 交差検証法: FREE R-VALUE / σ(F): 0.23 / 位相誤差: 22.04 / 立体化学のターゲット値: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.97→49.099 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj


















