+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9fvu | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Aspartyl/Asparaginyl beta-hydroxylase (AspH) in complex with Fe, 2-oxoglutarate, thiocyanate and Factor X derived peptide fragment | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | OXIDOREDUCTASE / AspH / Aspartyl/Asparaginyl beta-hydroxylase / O2 exposure / product complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報peptide-aspartate beta-dioxygenase / : / regulation of protein depolymerization / activation of store-operated calcium channel activity / regulation of cell communication by electrical coupling / junctional sarcoplasmic reticulum membrane / peptidyl-aspartic acid 3-dioxygenase activity / sarcoplasmic reticulum lumen / cortical endoplasmic reticulum / limb morphogenesis ...peptide-aspartate beta-dioxygenase / : / regulation of protein depolymerization / activation of store-operated calcium channel activity / regulation of cell communication by electrical coupling / junctional sarcoplasmic reticulum membrane / peptidyl-aspartic acid 3-dioxygenase activity / sarcoplasmic reticulum lumen / cortical endoplasmic reticulum / limb morphogenesis / positive regulation of intracellular protein transport / coagulation factor Xa / pattern specification process / Defective factor IX causes thrombophilia / Defective cofactor function of FVIIIa variant / Defective F9 variant does not activate FX / : / face morphogenesis / structural constituent of muscle / response to ATP / positive regulation of proteolysis / roof of mouth development / Protein hydroxylation / positive regulation of calcium ion transport into cytosol / positive regulation of TOR signaling / Transport of gamma-carboxylated protein precursors from the endoplasmic reticulum to the Golgi apparatus / : / Gamma-carboxylation of protein precursors / detection of calcium ion / Removal of aminoterminal propeptides from gamma-carboxylated proteins / regulation of cytosolic calcium ion concentration / calcium ion homeostasis / : / Ion homeostasis / regulation of release of sequestered calcium ion into cytosol by sarcoplasmic reticulum / regulation of cardiac muscle contraction by regulation of the release of sequestered calcium ion / sarcoplasmic reticulum membrane / calcium channel complex / cellular response to calcium ion / muscle contraction / regulation of protein stability / phospholipid binding / Golgi lumen / Stimuli-sensing channels / calcium ion transmembrane transport / blood coagulation / transmembrane transporter binding / electron transfer activity / cell population proliferation / positive regulation of cell migration / endoplasmic reticulum lumen / negative regulation of cell population proliferation / serine-type endopeptidase activity / external side of plasma membrane / calcium ion binding / endoplasmic reticulum membrane / positive regulation of DNA-templated transcription / structural molecule activity / endoplasmic reticulum / proteolysis / : / extracellular region / plasma membrane 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.7 Å 分子置換 / 解像度: 1.7 Å | ||||||
 データ登録者 データ登録者 | Brasnett, A. / de Munnik, M. / Brewitz, L. / Rabe, P. / Schofield, C.J. | ||||||
| 資金援助 |  英国, 1件 英国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2026 ジャーナル: Nat Commun / 年: 2026タイトル: Structural basis of the promiscuity of the unusual Fe(II) and 2-oxoglutarate dependent human aspartate/asparagine-beta-hydroxylase. 著者: de Munnik, M. / Brasnett, A. / Zhou, T. / Myers, W. / Wang, Y. / Chatterjee, K. / Tumber, A. / Marshall, S.A. / Simon, P.S. / Aller, P. / Shilova, A. / Axford, D. / Makita, H. / Paley, D.W. / ...著者: de Munnik, M. / Brasnett, A. / Zhou, T. / Myers, W. / Wang, Y. / Chatterjee, K. / Tumber, A. / Marshall, S.A. / Simon, P.S. / Aller, P. / Shilova, A. / Axford, D. / Makita, H. / Paley, D.W. / Tiwari, V. / Stead, A.T. / Dehe, S. / Sanchez, H. / Rosenberg, D.J. / Alonso-Mori, R. / Bhowmick, A. / Yano, J. / Yachandra, V.K. / Park, J. / Park, S. / Orville, A.M. / Brewitz, L. / Kern, J.F. / Schofield, C.J. / Rabe, P. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9fvu.cif.gz 9fvu.cif.gz | 236.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9fvu.ent.gz pdb9fvu.ent.gz | 162.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9fvu.json.gz 9fvu.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/fv/9fvu https://data.pdbj.org/pub/pdb/validation_reports/fv/9fvu ftp://data.pdbj.org/pub/pdb/validation_reports/fv/9fvu ftp://data.pdbj.org/pub/pdb/validation_reports/fv/9fvu | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  9fvvC  9fvwC  9fvxC  9fvyC  9fvzC  9fw0C  9hnzC  9ho0C  9ho1C  9ho2C  9ho3C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 / タンパク質・ペプチド , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 85976.555 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: ASPH, BAH / 発現宿主: Homo sapiens (ヒト) / 遺伝子: ASPH, BAH / 発現宿主:  |
|---|---|
| #2: タンパク質・ペプチド | 分子量: 4189.399 Da / 分子数: 1 / Mutation: C90S, C95S, C112S, C121S / 由来タイプ: 合成 / 由来: (合成)  Homo sapiens (ヒト) / 参照: UniProt: P00742 Homo sapiens (ヒト) / 参照: UniProt: P00742 |
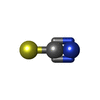
-非ポリマー , 5種, 462分子 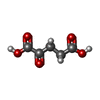







| #3: 化合物 | ChemComp-AKG / | ||||
|---|---|---|---|---|---|
| #4: 化合物 | ChemComp-FE / | ||||
| #5: 化合物 | ChemComp-PEG / #6: 化合物 | ChemComp-SCN / | #7: 水 | ChemComp-HOH / | |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.44 Å3/Da / 溶媒含有率: 18.1 % / 解説: needle morphology, 4 um x 4 um x 300 um |
|---|---|
| 結晶化 | 温度: 278 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: 0.1 M bis tris propane pH 7.5, 0.2 M NaSCN, 20% PEG 3350 |
-データ収集
| 回折 | 平均測定温度: 100 K / Ambient temp details: cryogenic / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  Diamond Diamond  / ビームライン: I03 / 波長: 0.9763 Å / ビームライン: I03 / 波長: 0.9763 Å |
| 検出器 | タイプ: DECTRIS EIGER2 XE 16M / 検出器: PIXEL / 日付: 2023年8月2日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.9763 Å / 相対比: 1 |
| 反射 | 解像度: 1.7→50.24 Å / Num. obs: 59190 / % possible obs: 100 % / 冗長度: 13.3 % / Biso Wilson estimate: 24.02 Å2 / CC1/2: 0.999 / Rmerge(I) obs: 0.079 / Rrim(I) all: 0.082 / Net I/σ(I): 17.3 |
| 反射 シェル | 解像度: 1.7→1.73 Å / 冗長度: 9.9 % / Rmerge(I) obs: 0.916 / Mean I/σ(I) obs: 1.1 / Num. unique obs: 2904 / CC1/2: 0.824 / Rrim(I) all: 0.966 / % possible all: 99.5 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 / 解像度: 1.7→46.08 Å / SU ML: 0.1801 / 交差検証法: FREE R-VALUE / σ(F): 1.36 / 位相誤差: 19.0566 分子置換 / 解像度: 1.7→46.08 Å / SU ML: 0.1801 / 交差検証法: FREE R-VALUE / σ(F): 1.36 / 位相誤差: 19.0566 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 30.44 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.7→46.08 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ | Refine-ID: X-RAY DIFFRACTION
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj




















