登録情報 データベース : PDB / ID : 9di0タイトル Cryo-EM structure of Kif18A bound to a microtubule Kinesin-like protein KIF18A, Methylated-DNA--protein-cysteine methyltransferase chimera Tubulin alpha-1B chain Tubulin beta chain キーワード / / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Homo sapiens (ヒト)Sus scrofa (ブタ)手法 / / / 解像度 : 3.1 Å データ登録者 Perez-Bertoldi, J.M. / Nogales, E. 資金援助 European Union, 組織 認可番号 国 European Research Council (ERC) European Union Howard Hughes Medical Institute (HHMI) National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS)
ジャーナル : Nat Commun / 年 : 2024タイトル : HURP regulates Kif18A recruitment and activity to synergistically control microtubule dynamics.著者 : Juan M Perez-Bertoldi / Yuanchang Zhao / Akanksha Thawani / Ahmet Yildiz / Eva Nogales / 要旨 : During mitosis, microtubule dynamics are regulated to ensure proper alignment and segregation of chromosomes. The dynamics of kinetochore-attached microtubules are regulated by hepatoma-upregulated ... During mitosis, microtubule dynamics are regulated to ensure proper alignment and segregation of chromosomes. The dynamics of kinetochore-attached microtubules are regulated by hepatoma-upregulated protein (HURP) and the mitotic kinesin-8 Kif18A, but the underlying mechanism remains elusive. Using single-molecule imaging in vitro, we demonstrate that Kif18A motility is regulated by HURP. While sparse decoration of HURP activates the motor, higher concentrations hinder processive motility. To shed light on this behavior, we determine the binding mode of HURP to microtubules using cryo-EM. The structure helps rationalize why HURP functions as a microtubule stabilizer. Additionally, HURP partially overlaps with the microtubule-binding site of the Kif18A motor domain, indicating that excess HURP inhibits Kif18A motility by steric exclusion. We also observe that HURP and Kif18A function together to suppress dynamics of the microtubule plus-end, providing a mechanistic basis for how they collectively serve in microtubule length control. 履歴 登録 2024年9月4日 登録サイト / 処理サイト 改定 1.0 2025年7月16日 Provider / タイプ
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 データ登録者
データ登録者 米国, 3件
米国, 3件  引用
引用 ジャーナル: Nat Commun / 年: 2024
ジャーナル: Nat Commun / 年: 2024
 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 9di0.cif.gz
9di0.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb9di0.ent.gz
pdb9di0.ent.gz PDB形式
PDB形式 9di0.json.gz
9di0.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 9di0_validation.pdf.gz
9di0_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 9di0_full_validation.pdf.gz
9di0_full_validation.pdf.gz 9di0_validation.xml.gz
9di0_validation.xml.gz 9di0_validation.cif.gz
9di0_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/di/9di0
https://data.pdbj.org/pub/pdb/validation_reports/di/9di0 ftp://data.pdbj.org/pub/pdb/validation_reports/di/9di0
ftp://data.pdbj.org/pub/pdb/validation_reports/di/9di0 リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: KIF18A, OK/SW-cl.108 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: KIF18A, OK/SW-cl.108 / 発現宿主: 




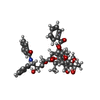



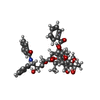


 試料調製
試料調製 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 電子顕微鏡撮影
電子顕微鏡撮影
 FIELD EMISSION GUN / 加速電圧: 200 kV / 照射モード: OTHER
FIELD EMISSION GUN / 加速電圧: 200 kV / 照射モード: OTHER 解析
解析 ムービー
ムービー コントローラー
コントローラー









 PDBj
PDBj





















