+ データを開く
データを開く
- 基本情報
基本情報
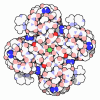
| 登録情報 | データベース: PDB / ID: 8vtb | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | SthK R120A R124A in the presence of PIP2 and cAMP | ||||||
 要素 要素 | Transcriptional regulator, Crp/Fnr family | ||||||
 キーワード キーワード | TRANSPORT PROTEIN / cyclic-nucleotide binding / potassium channel / lipid modulation | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報intracellularly cyclic nucleotide-activated monoatomic cation channel activity / protein-containing complex binding / membrane 類似検索 - 分子機能 | ||||||
| 生物種 |  Spirochaeta thermophila (バクテリア) Spirochaeta thermophila (バクテリア) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.5 Å | ||||||
 データ登録者 データ登録者 | Schmidpeter, P.A.M. / Thon, O. / Nimigean, C.M. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: PIP2 inhibits pore opening of the cyclic nucleotide-gated channel SthK. 著者: Oliver Thon / Zhihan Wang / Philipp A M Schmidpeter / Crina M Nimigean /   要旨: The signaling lipid phosphatidylinositol-4,5-bisphosphate (PIP2) regulates many ion channels. It inhibits eukaryotic cyclic nucleotide-gated (CNG) channels while activating their relatives, the ...The signaling lipid phosphatidylinositol-4,5-bisphosphate (PIP2) regulates many ion channels. It inhibits eukaryotic cyclic nucleotide-gated (CNG) channels while activating their relatives, the hyperpolarization-activated and cyclic nucleotide-modulated (HCN) channels. The prokaryotic SthK channel from Spirochaeta thermophila shares features with CNG and HCN channels and is an established model for this channel family. Here, we show SthK activity is inhibited by PIP2. A cryo-EM structure of SthK in nanodiscs reveals a PIP2-fitting density coordinated by arginine and lysine residues from the S4 helix and the C-linker, located between voltage-sensing and pore domains of adjacent subunits. Mutation of two arginine residues weakens PIP2 inhibition with the double mutant displaying insensitivity to PIP2. We propose that PIP2 inhibits SthK by gluing S4 and S6 together, stabilizing a resting channel conformation. The PIP2 binding site is partially conserved in CNG channels suggesting the possibility of a similar inhibition mechanism in the eukaryotic homologs. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8vtb.cif.gz 8vtb.cif.gz | 339.9 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8vtb.ent.gz pdb8vtb.ent.gz | 274.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8vtb.json.gz 8vtb.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/vt/8vtb https://data.pdbj.org/pub/pdb/validation_reports/vt/8vtb ftp://data.pdbj.org/pub/pdb/validation_reports/vt/8vtb ftp://data.pdbj.org/pub/pdb/validation_reports/vt/8vtb | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  43522MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 50588.918 Da / 分子数: 4 / 変異: R120A R124A / 由来タイプ: 組換発現 由来: (組換発現)  Spirochaeta thermophila (バクテリア) Spirochaeta thermophila (バクテリア)遺伝子: Spith_0644 / 発現宿主:  #2: 化合物 | ChemComp-CMP / #3: 化合物 | ChemComp-PCW / 研究の焦点であるリガンドがあるか | N | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: tetrameric SthK R120A R124A protein / タイプ: COMPLEX 詳細: SthK R120A R124A in complex with cAMP reconstituted into MSP1E3 nanodiscs containing PIP2 Entity ID: #1 / 由来: RECOMBINANT | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 0.2 MDa / 実験値: NO | ||||||||||||||||||||
| 由来(天然) | 生物種:  Spirochaeta thermophila (バクテリア) Spirochaeta thermophila (バクテリア) | ||||||||||||||||||||
| 由来(組換発現) | 生物種:  | ||||||||||||||||||||
| 緩衝液 | pH: 7.4 | ||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||
| 試料 | 濃度: 7.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: nanodisc reconstitution was carried out in the presence of DOPC, POPG, and PIP2 | ||||||||||||||||||||
| 試料支持 | グリッドの材料: GOLD / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: UltrAuFoil R1.2/1.3 | ||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 298 K / 詳細: 30 s incubation 2 s blotting blot force -4 |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 105000 X / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 500 nm |
| 試料ホルダ | 凍結剤: NITROGEN |
| 撮影 | 電子線照射量: 56.64 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 1799891 | ||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C4 (4回回転対称) | ||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 431535 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: FLEXIBLE FIT / 空間: REAL | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6CJQ Accession code: 6CJQ / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー





 PDBj
PDBj