| 登録情報 | データベース: PDB / ID: 8u0q
|
|---|
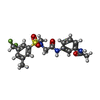
| タイトル | Co-crystal structure of optimized analog TDI-13537 provided new insights into the potency determinants of the sulfonamide inhibitor series |
|---|
 要素 要素 | Dihydrolipoyl dehydrogenase |
|---|
 キーワード キーワード | OXIDOREDUCTASE/OXIDOREDUCTASE INHIBITOR / virtual screening / tuberculosis / mycobacteria / lipoamide dehydrogenase / inhibitor / OXIDOREDUCTASE / OXIDOREDUCTASE-OXIDOREDUCTASE INHIBITOR complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
Cell redox homeostasis / dihydrolipoyl dehydrogenase / dihydrolipoyl dehydrogenase (NADH) activity / NADH binding / disulfide oxidoreductase activity / pyruvate dehydrogenase complex / 2-oxoglutarate metabolic process / pyruvate metabolic process / zymogen binding / oxidoreductase activity, acting on NAD(P)H, quinone or similar compound as acceptor ...Cell redox homeostasis / dihydrolipoyl dehydrogenase / dihydrolipoyl dehydrogenase (NADH) activity / NADH binding / disulfide oxidoreductase activity / pyruvate dehydrogenase complex / 2-oxoglutarate metabolic process / pyruvate metabolic process / zymogen binding / oxidoreductase activity, acting on NAD(P)H, quinone or similar compound as acceptor / antioxidant activity / Prevention of phagosomal-lysosomal fusion / cell redox homeostasis / flavin adenine dinucleotide binding / extracellular region / plasma membrane / cytosol類似検索 - 分子機能 Dihydrolipoamide dehydrogenase / : / Pyridine nucleotide-disulphide oxidoreductase, class I / Pyridine nucleotide-disulphide oxidoreductase, class I, active site / Pyridine nucleotide-disulphide oxidoreductases class-I active site. / Pyridine nucleotide-disulphide oxidoreductase, dimerisation domain / Pyridine nucleotide-disulphide oxidoreductase, dimerisation domain / FAD/NAD-linked reductase, dimerisation domain superfamily / FAD/NAD(P)-binding domain / Pyridine nucleotide-disulphide oxidoreductase / FAD/NAD(P)-binding domain superfamily類似検索 - ドメイン・相同性 FLAVIN-ADENINE DINUCLEOTIDE / Chem-U4I / Dihydrolipoyl dehydrogenase類似検索 - 構成要素 |
|---|
| 生物種 |   Mycobacterium tuberculosis (結核菌) Mycobacterium tuberculosis (結核菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.69 Å 分子置換 / 解像度: 1.69 Å |
|---|
 データ登録者 データ登録者 | Dementiev, A.A. / Michino, M. / Vendome, J. / Ginn, J. / Bryk, R. / Olland, A. |
|---|
| 資金援助 | 1件 |
|---|
 引用 引用 |  ジャーナル: Acs Bio Med Chem Au / 年: 2023 ジャーナル: Acs Bio Med Chem Au / 年: 2023
タイトル: Shape-Based Virtual Screening of a Billion-Compound Library Identifies Mycobacterial Lipoamide Dehydrogenase Inhibitors.
著者: Michino, M. / Beautrait, A. / Boyles, N.A. / Nadupalli, A. / Dementiev, A. / Sun, S. / Ginn, J. / Baxt, L. / Suto, R. / Bryk, R. / Jerome, S.V. / Huggins, D.J. / Vendome, J. |
|---|
| 履歴 | | 登録 | 2023年8月29日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2024年1月3日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2024年11月13日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature
Item: _pdbx_entry_details.has_protein_modification |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.69 Å
分子置換 / 解像度: 1.69 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Acs Bio Med Chem Au / 年: 2023
ジャーナル: Acs Bio Med Chem Au / 年: 2023 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 8u0q.cif.gz
8u0q.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb8u0q.ent.gz
pdb8u0q.ent.gz PDB形式
PDB形式 8u0q.json.gz
8u0q.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 8u0q_validation.pdf.gz
8u0q_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 8u0q_full_validation.pdf.gz
8u0q_full_validation.pdf.gz 8u0q_validation.xml.gz
8u0q_validation.xml.gz 8u0q_validation.cif.gz
8u0q_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/u0/8u0q
https://data.pdbj.org/pub/pdb/validation_reports/u0/8u0q ftp://data.pdbj.org/pub/pdb/validation_reports/u0/8u0q
ftp://data.pdbj.org/pub/pdb/validation_reports/u0/8u0q F&H 検索
F&H 検索 リンク
リンク 集合体
集合体
 要素
要素

 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  CLSI
CLSI  / ビームライン: 08ID-1 / 波長: 0.95367 Å
/ ビームライン: 08ID-1 / 波長: 0.95367 Å 解析
解析 分子置換 / 解像度: 1.69→45.53 Å / SU ML: 0.2775 / 交差検証法: FREE R-VALUE / σ(F): 1.33 / 位相誤差: 23.1476
分子置換 / 解像度: 1.69→45.53 Å / SU ML: 0.2775 / 交差検証法: FREE R-VALUE / σ(F): 1.33 / 位相誤差: 23.1476  ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj