+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8s59 | |||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the active dodecameric Methanosarcina mazei glutamine synthetase. | |||||||||||||||||||||||||||||||||
 要素 要素 | Glutamine synthetase | |||||||||||||||||||||||||||||||||
 キーワード キーワード | CYTOSOLIC PROTEIN / Glutamine synthetases / nitrogen metabolism / ammonium assimilation / cryo-EM | |||||||||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報glutamine synthetase / glutamine biosynthetic process / glutamine synthetase activity / ATP binding / metal ion binding / cytoplasm 類似検索 - 分子機能 | |||||||||||||||||||||||||||||||||
| 生物種 |  Methanosarcina mazei Go1 (古細菌) Methanosarcina mazei Go1 (古細菌) | |||||||||||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.39 Å | |||||||||||||||||||||||||||||||||
 データ登録者 データ登録者 | Kumar, A. / Schuller, J.M. / Schmitz, R.A. | |||||||||||||||||||||||||||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2025 ジャーナル: Elife / 年: 2025タイトル: 2-oxoglutarate triggers assembly of active dodecameric glutamine synthetase. 著者: Eva Herdering / Tristan Reif-Trauttmansdorff / Anuj Kumar / Tim Habenicht / Georg Hochberg / Stefan Bohn / Jan Schuller / Ruth Anne Schmitz /  要旨: Glutamine synthetases (GS) are central enzymes essential for the nitrogen metabolism across all domains of life. Consequently, they have been extensively studied for more than half a century. Based ...Glutamine synthetases (GS) are central enzymes essential for the nitrogen metabolism across all domains of life. Consequently, they have been extensively studied for more than half a century. Based on the ATP-dependent ammonium assimilation generating glutamine, GS expression and activity are strictly regulated in all organisms. In the methanogenic archaeon , it has been shown that the metabolite 2-oxoglutarate (2-OG) directly induces the GS activity. Besides, modulation of the activity by interaction with small proteins (GlnK and sP26) has been reported. Here, we show that the strong activation of GS (GlnA) by 2-OG is based on the 2-OG dependent dodecamer assembly of GlnA by using mass photometry (MP) and single particle cryo-electron microscopy (cryo-EM) analysis of purified strep-tagged GlnA. The dodecamer assembly from dimers occurred without any detectable intermediate oligomeric state and was not affected in the presence of GlnK. The 2.39 Å cryo-EM structure of the dodecameric complex in the presence of 12.5 mM 2-OG demonstrated that 2-OG is binding between two monomers. Thereby, 2-OG appears to induce the dodecameric assembly in a cooperative way. Furthermore, the active site is primed by an allosteric interaction cascade caused by 2-OG-binding towards an adaption of an open active state conformation. In the presence of additional glutamine, strong feedback inhibition of GS activity was observed. Since glutamine dependent disassembly of the dodecamer was excluded by MP, feedback inhibition most likely relies on the binding of glutamine to the catalytic site. Based on our findings, we propose that under nitrogen limitation the induction of GS into a catalytically active dodecamer is not affected by GlnK and crucially depends on the presence of 2-OG. #1:  ジャーナル: Elife / 年: 2024 ジャーナル: Elife / 年: 2024タイトル: Cryo-EM structure of the active dodecameric Methanosarcina mazei glutamine synthetase. 著者: Kumar, A. / Schuller, J.M. / Schmitz, R.A. | |||||||||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8s59.cif.gz 8s59.cif.gz | 1.1 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8s59.ent.gz pdb8s59.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  8s59.json.gz 8s59.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8s59_validation.pdf.gz 8s59_validation.pdf.gz | 1.8 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8s59_full_validation.pdf.gz 8s59_full_validation.pdf.gz | 1.8 MB | 表示 | |
| XML形式データ |  8s59_validation.xml.gz 8s59_validation.xml.gz | 135.1 KB | 表示 | |
| CIF形式データ |  8s59_validation.cif.gz 8s59_validation.cif.gz | 231 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/s5/8s59 https://data.pdbj.org/pub/pdb/validation_reports/s5/8s59 ftp://data.pdbj.org/pub/pdb/validation_reports/s5/8s59 ftp://data.pdbj.org/pub/pdb/validation_reports/s5/8s59 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  19730MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
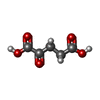
| #1: タンパク質 | 分子量: 50525.371 Da / 分子数: 12 / 由来タイプ: 組換発現 / 由来: (組換発現)  Methanosarcina mazei Go1 (古細菌) / 遺伝子: glnA1, MM_0964 / 発現宿主: Methanosarcina mazei Go1 (古細菌) / 遺伝子: glnA1, MM_0964 / 発現宿主:  #2: 化合物 | ChemComp-AKG / #3: 水 | ChemComp-HOH / | 研究の焦点であるリガンドがあるか | Y | Has protein modification | N | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Glutamine synthetases from Methanosarcina mazei / タイプ: COMPLEX / Entity ID: #1 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 値: 55 kDa/nm / 実験値: YES |
| 由来(天然) | 生物種:  Methanosarcina mazei Go1 (古細菌) Methanosarcina mazei Go1 (古細菌) |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE-PROPANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 顕微鏡 | モデル: TFS TALOS |
|---|---|
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 300 nm |
| 撮影 | 電子線照射量: 55 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) |
- 解析
解析
| EMソフトウェア | 名称: PHENIX / カテゴリ: モデル精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.39 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 800000 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj