+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8anw | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Poliovirus type 3 (strain Saukett) stabilised virus-like particle (PV3 SC8). | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | VIRUS LIKE PARTICLE / Capsid protein | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont genome entry into host cell via pore formation in plasma membrane / viral capsid / host cell cytoplasm / symbiont-mediated suppression of host gene expression / virion attachment to host cell / structural molecule activity 類似検索 - 分子機能 | ||||||
| 生物種 |  Human poliovirus 3 (ポリオウイルス) Human poliovirus 3 (ポリオウイルス) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.7 Å | ||||||
 データ登録者 データ登録者 | Bahar, M.W. / Fry, E.E. / Stuart, D.I. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Viruses / 年: 2022 ジャーナル: Viruses / 年: 2022タイトル: Production and Characterisation of Stabilised PV-3 Virus-like Particles Using . 著者: Lee Sherry / Keith Grehan / Jessica J Swanson / Mohammad W Bahar / Claudine Porta / Elizabeth E Fry / David I Stuart / David J Rowlands / Nicola J Stonehouse /  要旨: Following the success of global vaccination programmes using the live-attenuated oral and inactivated poliovirus vaccines (OPV and IPV), wild poliovirus (PV) is now only endemic in Afghanistan and ...Following the success of global vaccination programmes using the live-attenuated oral and inactivated poliovirus vaccines (OPV and IPV), wild poliovirus (PV) is now only endemic in Afghanistan and Pakistan. However, the continued use of these vaccines poses potential risks to the eradication of PV. The production of recombinant PV virus-like particles (VLPs), which lack the viral genome offer great potential as next-generation vaccines for the post-polio world. We have previously reported production of PV VLPs using , however, these VLPs were in the non-native conformation (C Ag), which would not produce effective protection against PV. Here, we build on this work and show that it is possible to produce wt PV-3 and thermally stabilised PV-3 (referred to as PV-3 SC8) VLPs in the native conformation (D Ag) using . We show that the PV-3 SC8 VLPs provide a much-improved D:C antigen ratio as compared to wt PV-3, whilst exhibiting greater thermostability than the current IPV vaccine. Finally, we determine the cryo-EM structure of the yeast-derived PV-3 SC8 VLPs and compare this to previously published PV-3 D Ag structures, highlighting the similarities between these recombinantly expressed VLPs and the infectious virus, further emphasising their potential as a next-generation vaccine candidate for PV. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8anw.cif.gz 8anw.cif.gz | 143.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8anw.ent.gz pdb8anw.ent.gz | 108 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8anw.json.gz 8anw.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8anw_validation.pdf.gz 8anw_validation.pdf.gz | 1.7 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8anw_full_validation.pdf.gz 8anw_full_validation.pdf.gz | 1.7 MB | 表示 | |
| XML形式データ |  8anw_validation.xml.gz 8anw_validation.xml.gz | 42.6 KB | 表示 | |
| CIF形式データ |  8anw_validation.cif.gz 8anw_validation.cif.gz | 61.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/an/8anw https://data.pdbj.org/pub/pdb/validation_reports/an/8anw ftp://data.pdbj.org/pub/pdb/validation_reports/an/8anw ftp://data.pdbj.org/pub/pdb/validation_reports/an/8anw | HTTPS FTP |
-関連構造データ
| 関連構造データ |  15543MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
- 要素
要素
| #1: タンパク質 | 分子量: 33562.785 Da / 分子数: 1 / 変異: VP1 T105M, VP1 F132L / 由来タイプ: 組換発現 由来: (組換発現)  Human poliovirus 3 (ポリオウイルス) Human poliovirus 3 (ポリオウイルス)細胞株 (発現宿主): PichiaPink / 発現宿主:  Komagataella pastoris (菌類) / 参照: UniProt: Q84895 Komagataella pastoris (菌類) / 参照: UniProt: Q84895 |
|---|---|
| #2: タンパク質 | 分子量: 37623.023 Da / 分子数: 1 / 変異: VP2 L18I, VP2 L215M, VP2 D241E, VP4 T67A / 由来タイプ: 組換発現 詳細: Sequence is given for the VP0 polypeptide. Mutations are numbered according to sequence numbering for mature polypeptides VP2 and VP4. 由来: (組換発現)  Human poliovirus 3 (ポリオウイルス) Human poliovirus 3 (ポリオウイルス)細胞株 (発現宿主): PichiaPink / 発現宿主:  Komagataella pastoris (菌類) / 参照: UniProt: Q84895 Komagataella pastoris (菌類) / 参照: UniProt: Q84895 |
| #3: タンパク質 | 分子量: 26315.100 Da / 分子数: 1 / 変異: VP3 H19Y, VP3 L85F / 由来タイプ: 組換発現 由来: (組換発現)  Human poliovirus 3 (ポリオウイルス) Human poliovirus 3 (ポリオウイルス)細胞株 (発現宿主): PichiaPink / 発現宿主:  Komagataella pastoris (菌類) / 参照: UniProt: Q84895 Komagataella pastoris (菌類) / 参照: UniProt: Q84895 |
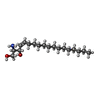
| #4: 化合物 | ChemComp-SPH / |
| 研究の焦点であるリガンドがあるか | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Human poliovirus 3 / タイプ: VIRUS 詳細: Recombinantly expressed virus-like particle of PV3 (strain Saukett). Entity ID: #1-#3 / 由来: RECOMBINANT | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 5.85 MDa / 実験値: NO | ||||||||||||
| 由来(天然) | 生物種:  Human poliovirus 3 (ポリオウイルス) / 株: Saukett Human poliovirus 3 (ポリオウイルス) / 株: Saukett | ||||||||||||
| 由来(組換発現) | 生物種:  Komagataella pastoris (菌類) / 細胞: PichiaPink Komagataella pastoris (菌類) / 細胞: PichiaPink | ||||||||||||
| ウイルスについての詳細 | 中空か: YES / エンベロープを持つか: NO / 単離: SEROTYPE / タイプ: VIRUS-LIKE PARTICLE | ||||||||||||
| 天然宿主 | 生物種: Homo sapiens | ||||||||||||
| ウイルス殻 | 名称: Virus shell 1 / 直径: 310 nm / 三角数 (T数): 1 | ||||||||||||
| 緩衝液 | pH: 7 / 詳細: 1 x DPBS, 20 mM EDTA, pH 7.0 | ||||||||||||
| 緩衝液成分 |
| ||||||||||||
| 試料 | 濃度: 0.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: Virus-like particle purified by sucrose density gradient purification from Pichia pastoris cells. | ||||||||||||
| 試料支持 | 詳細: The specific type of grid used was Ultra-thin carbon support film, 3nm - on lacey carbon AGS187-4 from Agar Scientific. グリッドの材料: COPPER / グリッドのサイズ: 400 divisions/in. / グリッドのタイプ: EMS Lacey Carbon | ||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE-PROPANE / 湿度: 100 % / 凍結前の試料温度: 277.15 K 詳細: Double blotting with 4 ul of sample, followed by 4 second blot, before plunging. |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 165000 X / 倍率(補正後): 60975 X / 最大 デフォーカス(公称値): 2400 nm / 最小 デフォーカス(公称値): 900 nm / Cs: 2.7 mm / C2レンズ絞り径: 100 µm / アライメント法: COMA FREE |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 3 sec. / 電子線照射量: 35 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 撮影したグリッド数: 1 / 実像数: 3717 / 詳細: Pixel sampling of 0.82 A/pixel. |
| 電子光学装置 | エネルギーフィルター名称: GIF Quantum LS / エネルギーフィルタースリット幅: 20 eV |
| 画像スキャン | サンプリングサイズ: 5 µm / 動画フレーム数/画像: 20 / 利用したフレーム数/画像: 1-20 |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: (1.19.2_4158:phenix.real_space_refine) / 分類: 精密化 | ||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||
| 画像処理 | 詳細: Pixels size was 0.82 A/pixel | ||||||||||||||||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 10744 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: I (正20面体型対称) | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 2712 / アルゴリズム: BACK PROJECTION 詳細: Final reconstruction was sharpened with Post-processing in RELION using an inverse B-factor of -69.1 Angstroms. クラス平均像の数: 2 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL / Target criteria: Correlation coefficient 詳細: Initial model was rigid body fitted using UCSF chimera and Coot. Global minimization and B-factor refinement was performed in real space using phenix_real.space.refine. | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6Z6W Accession code: 6Z6W / Source name: PDB / タイプ: experimental model | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | 交差検証法: THROUGHOUT | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 57.31 Å2 / Biso mean: 13.0392 Å2 / Biso min: 5.18 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj