+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7zv2 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | HUMAN PRMT5:MEP50 Crystal Structure With MTA and Fragment Bound | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSFERASE / MTAP / methyl transferase / fragment-based lead discovery / FBDD | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of adenylate cyclase-inhibiting dopamine receptor signaling pathway / peptidyl-arginine N-methylation / oocyte axis specification / type II protein arginine methyltransferase / protein-arginine omega-N symmetric methyltransferase activity / peptidyl-arginine methylation / Golgi ribbon formation / negative regulation of epithelial cell proliferation involved in prostate gland development / secretory columnal luminar epithelial cell differentiation involved in prostate glandular acinus development / histone H4R3 methyltransferase activity ...positive regulation of adenylate cyclase-inhibiting dopamine receptor signaling pathway / peptidyl-arginine N-methylation / oocyte axis specification / type II protein arginine methyltransferase / protein-arginine omega-N symmetric methyltransferase activity / peptidyl-arginine methylation / Golgi ribbon formation / negative regulation of epithelial cell proliferation involved in prostate gland development / secretory columnal luminar epithelial cell differentiation involved in prostate glandular acinus development / histone H4R3 methyltransferase activity / : / epithelial cell proliferation involved in prostate gland development / protein-arginine N-methyltransferase activity / methylosome / positive regulation of mRNA splicing, via spliceosome / methyl-CpG binding / endothelial cell activation / histone H3 methyltransferase activity / histone methyltransferase activity / regulation of mitotic nuclear division / negative regulation of gene expression via chromosomal CpG island methylation / Cul4B-RING E3 ubiquitin ligase complex / E-box binding / histone methyltransferase complex / positive regulation of oligodendrocyte differentiation / negative regulation of cell differentiation / spliceosomal snRNP assembly / ribonucleoprotein complex binding / regulation of ERK1 and ERK2 cascade / ubiquitin-like ligase-substrate adaptor activity / liver regeneration / regulation of signal transduction by p53 class mediator / methyltransferase activity / circadian regulation of gene expression / DNA-templated transcription termination / Regulation of TP53 Activity through Methylation / RMTs methylate histone arginines / protein polyubiquitination / p53 binding / transcription corepressor activity / snRNP Assembly / ubiquitin-dependent protein catabolic process / transcription coactivator activity / chromatin remodeling / protein heterodimerization activity / positive regulation of cell population proliferation / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / chromatin / Golgi apparatus / nucleoplasm / identical protein binding / nucleus / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.01 Å 分子置換 / 解像度: 2.01 Å | ||||||
 データ登録者 データ登録者 | Ahmad, M.U. / Koelmel, W. / Arkhipova, V. / Lawson, J.D. / Smith, C.R. / Gunn, R.J. | ||||||
| 資金援助 | 1件
| ||||||
 引用 引用 |  ジャーナル: Rsc Med Chem / 年: 2022 ジャーナル: Rsc Med Chem / 年: 2022タイトル: Fragment optimization and elaboration strategies - the discovery of two lead series of PRMT5/MTA inhibitors from five fragment hits. 著者: Smith, C.R. / Kulyk, S. / Ahmad, M.U.D. / Arkhipova, V. / Christensen, J.G. / Gunn, R.J. / Ivetac, A. / Ketcham, J.M. / Kuehler, J. / Lawson, J.D. / Thomas, N.C. / Wang, X. / Marx, M.A. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7zv2.cif.gz 7zv2.cif.gz | 208 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7zv2.ent.gz pdb7zv2.ent.gz | 159.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7zv2.json.gz 7zv2.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/zv/7zv2 https://data.pdbj.org/pub/pdb/validation_reports/zv/7zv2 ftp://data.pdbj.org/pub/pdb/validation_reports/zv/7zv2 ftp://data.pdbj.org/pub/pdb/validation_reports/zv/7zv2 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  7uy1C  7uyfC  7zupC  7zuqC  7zuuC  7zuyC  7zvlC  7zvuC  8csgC  8ctbC  5emlS S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 73763.625 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: PRMT5, HRMT1L5, IBP72, JBP1, SKB1 Homo sapiens (ヒト) / 遺伝子: PRMT5, HRMT1L5, IBP72, JBP1, SKB1発現宿主:  参照: UniProt: O14744, type II protein arginine methyltransferase |
|---|---|
| #2: タンパク質 | 分子量: 37862.406 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: WDR77, MEP50, WD45, HKMT1069, Nbla10071 Homo sapiens (ヒト) / 遺伝子: WDR77, MEP50, WD45, HKMT1069, Nbla10071発現宿主:  参照: UniProt: Q9BQA1 |
-非ポリマー , 4種, 236分子 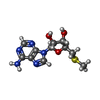




| #3: 化合物 | ChemComp-MTA / | ||
|---|---|---|---|
| #4: 化合物 | ChemComp-UNL / 分子数: 1 / 由来タイプ: 合成 / タイプ: SUBJECT OF INVESTIGATION | ||
| #5: 化合物 | | #6: 水 | ChemComp-HOH / | |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.91 Å3/Da / 溶媒含有率: 57.72 % |
|---|---|
| 結晶化 | 温度: 281 K / 手法: 蒸気拡散法, シッティングドロップ法 詳細: 16% PEG3350, 100 mM Na citrate pH 5.4, 100mM Carboxylic acids |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  Diamond Diamond  / ビームライン: I03 / 波長: 0.9198 Å / ビームライン: I03 / 波長: 0.9198 Å |
| 検出器 | タイプ: DECTRIS EIGER2 XE 16M / 検出器: PIXEL / 日付: 2021年7月3日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.9198 Å / 相対比: 1 |
| 反射 | 解像度: 2.01→109.71 Å / Num. obs: 46129 / % possible obs: 93.4 % / Observed criterion σ(I): 1.7 / 冗長度: 11.7 % / CC1/2: 0.99 / Net I/σ(I): 13.2 |
| 反射 シェル | 解像度: 2.01→2.15 Å / Num. unique obs: 2455 / CC1/2: 0.76 / % possible all: 81.9 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 5EML 解像度: 2.01→109.71 Å / Cor.coef. Fo:Fc: 0.925 / Cor.coef. Fo:Fc free: 0.893 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R: 0.096 / ESU R Free: 0.062 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS U VALUES : REFINED INDIVIDUALLY
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: MASK | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 112.82 Å2 / Biso mean: 33.111 Å2 / Biso min: 18.1 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 2.01→109.71 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.01→2.06 Å
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj




