+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7w5o | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of ERK2 with an allosteric inhibitor | ||||||
 要素 要素 | Mitogen-activated protein kinase 1 | ||||||
 キーワード キーワード | TRANSFERASE / protein kinase / allosteric inhibitor / activation loop | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報phospho-PLA2 pathway / Signaling by MAPK mutants / RAF-independent MAPK1/3 activation / Suppression of apoptosis / Gastrin-CREB signalling pathway via PKC and MAPK / Signaling by Activin / cardiac neural crest cell development involved in heart development / caveolin-mediated endocytosis / ERKs are inactivated / cytosine metabolic process ...phospho-PLA2 pathway / Signaling by MAPK mutants / RAF-independent MAPK1/3 activation / Suppression of apoptosis / Gastrin-CREB signalling pathway via PKC and MAPK / Signaling by Activin / cardiac neural crest cell development involved in heart development / caveolin-mediated endocytosis / ERKs are inactivated / cytosine metabolic process / Signaling by MAP2K mutants / Signaling by NODAL / response to epidermal growth factor / RSK activation / Golgi Cisternae Pericentriolar Stack Reorganization / Regulation of the apoptosome activity / positive regulation of macrophage proliferation / regulation of cellular pH / outer ear morphogenesis / Signaling by LTK in cancer / regulation of Golgi inheritance / labyrinthine layer blood vessel development / ERBB signaling pathway / mammary gland epithelial cell proliferation / trachea formation / Negative feedback regulation of MAPK pathway / regulation of early endosome to late endosome transport / regulation of stress-activated MAPK cascade / IFNG signaling activates MAPKs / Frs2-mediated activation / ERBB2-ERBB3 signaling pathway / MAPK1 (ERK2) activation / positive regulation of macrophage chemotaxis / Activation of the AP-1 family of transcription factors / regulation of cytoskeleton organization / ERK/MAPK targets / RUNX2 regulates osteoblast differentiation / response to exogenous dsRNA / face development / positive regulation of telomere maintenance / lung morphogenesis / Recycling pathway of L1 / pseudopodium / Bergmann glial cell differentiation / androgen receptor signaling pathway / Advanced glycosylation endproduct receptor signaling / thyroid gland development / steroid hormone receptor signaling pathway / negative regulation of cell differentiation / RHO GTPases Activate NADPH Oxidases / MAP kinase activity / regulation of ossification / RHO GTPases Activate WASPs and WAVEs / Estrogen-dependent nuclear events downstream of ESR-membrane signaling / Regulation of HSF1-mediated heat shock response / JUN kinase activity / mitogen-activated protein kinase / Signal attenuation / progesterone receptor signaling pathway / Estrogen-stimulated signaling through PRKCZ / phosphatase binding / Schwann cell development / Growth hormone receptor signaling / positive regulation of peptidyl-threonine phosphorylation / stress-activated MAPK cascade / Nuclear events stimulated by ALK signaling in cancer / NPAS4 regulates expression of target genes / phosphotyrosine residue binding / myelination / RNA polymerase II CTD heptapeptide repeat kinase activity / Transcriptional and post-translational regulation of MITF-M expression and activity / NCAM signaling for neurite out-growth / ERK1 and ERK2 cascade / cellular response to amino acid starvation / insulin-like growth factor receptor signaling pathway / lipopolysaccharide-mediated signaling pathway / ESR-mediated signaling / thymus development / Regulation of PTEN gene transcription / Signal transduction by L1 / peptidyl-threonine phosphorylation / B cell receptor signaling pathway / FCGR3A-mediated phagocytosis / FCERI mediated MAPK activation / response to nicotine / Negative regulation of FGFR3 signaling / Negative regulation of FGFR2 signaling / Negative regulation of FGFR4 signaling / Downregulation of SMAD2/3:SMAD4 transcriptional activity / Negative regulation of FGFR1 signaling / positive regulation of cholesterol biosynthetic process / long-term synaptic potentiation / SMAD2/SMAD3:SMAD4 heterotrimer regulates transcription / Spry regulation of FGF signaling / Signaling by high-kinase activity BRAF mutants / MAP2K and MAPK activation / regulation of protein stability / Oncogene Induced Senescence / caveola / Regulation of actin dynamics for phagocytic cup formation 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.35 Å 分子置換 / 解像度: 2.35 Å | ||||||
 データ登録者 データ登録者 | Yoshida, M. / Kinoshita, T. | ||||||
| 資金援助 | 1件
| ||||||
 引用 引用 |  ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2022 ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2022タイトル: Identification of a novel target site for ATP-independent ERK2 inhibitors. 著者: Yoshida, M. / Nagao, H. / Sugiyama, H. / Sawa, M. / Kinoshita, T. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7w5o.cif.gz 7w5o.cif.gz | 181.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7w5o.ent.gz pdb7w5o.ent.gz | 128.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7w5o.json.gz 7w5o.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7w5o_validation.pdf.gz 7w5o_validation.pdf.gz | 1.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7w5o_full_validation.pdf.gz 7w5o_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  7w5o_validation.xml.gz 7w5o_validation.xml.gz | 35.1 KB | 表示 | |
| CIF形式データ |  7w5o_validation.cif.gz 7w5o_validation.cif.gz | 46.1 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/w5/7w5o https://data.pdbj.org/pub/pdb/validation_reports/w5/7w5o ftp://data.pdbj.org/pub/pdb/validation_reports/w5/7w5o ftp://data.pdbj.org/pub/pdb/validation_reports/w5/7w5o | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4qp1S S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 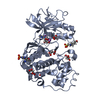
| ||||||||||||
| 2 | 
| ||||||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 2分子 AB
| #1: タンパク質 | 分子量: 42310.410 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: MAPK1, ERK2, PRKM1, PRKM2 / プラスミド: pGEX6p-1 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: MAPK1, ERK2, PRKM1, PRKM2 / プラスミド: pGEX6p-1 / 発現宿主:  |
|---|
-非ポリマー , 8種, 133分子 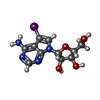


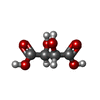









| #2: 化合物 | ChemComp-5ID / ( | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| #3: 化合物 | ChemComp-MLA / #4: 化合物 | #5: 化合物 | ChemComp-NA / | #6: 化合物 | #7: 化合物 | ChemComp-TAR / | #8: 化合物 | ChemComp-6GI / | #9: 水 | ChemComp-HOH / | |
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.78 Å3/Da / 溶媒含有率: 55.74 % |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7 / 詳細: Tacsimate, HEPES, PEGMME5000 |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SPring-8 SPring-8  / ビームライン: BL44XU / 波長: 0.9 Å / ビームライン: BL44XU / 波長: 0.9 Å |
| 検出器 | タイプ: DECTRIS EIGER X 16M / 検出器: PIXEL / 日付: 2020年7月4日 |
| 放射 | モノクロメーター: mirrrors / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.9 Å / 相対比: 1 |
| 反射 | 解像度: 2.35→49.32 Å / Num. obs: 46821 / % possible obs: 99.8 % / 冗長度: 13.2 % / Biso Wilson estimate: 55.87 Å2 / CC1/2: 0.99 / Rmerge(I) obs: 0.179 / Net I/σ(I): 99.9 |
| 反射 シェル | 解像度: 2.35→2.43 Å / Num. unique obs: 40848 / CC1/2: 0.62 / % possible all: 99.43 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 4qp1 解像度: 2.35→49.32 Å / SU ML: 0.3648 / 交差検証法: FREE R-VALUE / σ(F): 1.34 / 位相誤差: 31.559 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 68.79 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.35→49.32 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
|
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj







































