+ データを開く
データを開く
- 基本情報
基本情報
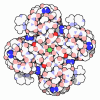
| 登録情報 | データベース: PDB / ID: 7tj6 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SthK open state, cAMP-bound in the presence of POPA | ||||||||||||
 要素 要素 | Putative transcriptional regulator, Crp/Fnr family | ||||||||||||
 キーワード キーワード | TRANSPORT PROTEIN / cyclic nucleotide-gated channel / lipid modulation / pacemaker channel | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||||||||
| 生物種 |   Spirochaeta thermophila DSM 6578 (バクテリア) Spirochaeta thermophila DSM 6578 (バクテリア) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | ||||||||||||
 データ登録者 データ登録者 | Schmidpeter, P.A. / Nimigean, C.M. | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2022 ジャーナル: Nat Struct Mol Biol / 年: 2022タイトル: Anionic lipids unlock the gates of select ion channels in the pacemaker family. 著者: Philipp A M Schmidpeter / Di Wu / Jan Rheinberger / Paul M Riegelhaupt / Haiping Tang / Carol V Robinson / Crina M Nimigean /    要旨: Lipids play important roles in regulating membrane protein function, but the molecular mechanisms used are elusive. Here we investigated how anionic lipids modulate SthK, a bacterial pacemaker ...Lipids play important roles in regulating membrane protein function, but the molecular mechanisms used are elusive. Here we investigated how anionic lipids modulate SthK, a bacterial pacemaker channel homolog, and HCN2, whose activity contributes to pacemaking in the heart and brain. Using SthK allowed the reconstitution of purified channels in controlled lipid compositions for functional and structural assays that are not available for the eukaryotic channels. We identified anionic lipids bound tightly to SthK and their exact binding locations and determined that they potentiate channel activity. Cryo-EM structures in the most potentiating lipids revealed an open state and identified a nonannular lipid bound with its headgroup near an intersubunit salt bridge that clamps the intracellular channel gate shut. Breaking this conserved salt bridge abolished lipid modulation in SthK and eukaryotic HCN2 channels, indicating that anionic membrane lipids facilitate channel opening by destabilizing these interactions. Our findings underline the importance of state-dependent protein-lipid interactions. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7tj6.cif.gz 7tj6.cif.gz | 293.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7tj6.ent.gz pdb7tj6.ent.gz | 236.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7tj6.json.gz 7tj6.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7tj6_validation.pdf.gz 7tj6_validation.pdf.gz | 1.9 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7tj6_full_validation.pdf.gz 7tj6_full_validation.pdf.gz | 2 MB | 表示 | |
| XML形式データ |  7tj6_validation.xml.gz 7tj6_validation.xml.gz | 64.9 KB | 表示 | |
| CIF形式データ |  7tj6_validation.cif.gz 7tj6_validation.cif.gz | 90.1 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/tj/7tj6 https://data.pdbj.org/pub/pdb/validation_reports/tj/7tj6 ftp://data.pdbj.org/pub/pdb/validation_reports/tj/7tj6 ftp://data.pdbj.org/pub/pdb/validation_reports/tj/7tj6 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  25917MC  7tj5C  7tktC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 51118.574 Da / 分子数: 4 / 由来タイプ: 組換発現 由来: (組換発現)   Spirochaeta thermophila DSM 6578 (バクテリア) Spirochaeta thermophila DSM 6578 (バクテリア)株: ATCC 700085 / DSM 6578 / Z-1203 / 遺伝子: Spith_0644 / 発現宿主:  #2: 化合物 | ChemComp-CMP / #3: 化合物 | ChemComp-D21 / ( 研究の焦点であるリガンドがあるか | Y | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: open conformation of SthK bound to cAMP / タイプ: COMPLEX 詳細: SthK was reconstituted into nanodiscs containing POPA lipids. Entity ID: #1 / 由来: RECOMBINANT | |||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | |||||||||||||||||||||||||
| 由来(天然) | 生物種:   Spirochaeta thermophila (strain ATCC 700085 / DSM 6578 / Z-1203) (バクテリア) Spirochaeta thermophila (strain ATCC 700085 / DSM 6578 / Z-1203) (バクテリア) | |||||||||||||||||||||||||
| 由来(組換発現) | 生物種:  | |||||||||||||||||||||||||
| 緩衝液 | pH: 7.4 | |||||||||||||||||||||||||
| 緩衝液成分 |
| |||||||||||||||||||||||||
| 試料 | 濃度: 8 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: WT SthK in MSP1E3 nanodiscs composed of 3:1 DOPC:POPA | |||||||||||||||||||||||||
| 試料支持 | グリッドの材料: GOLD / グリッドのタイプ: UltrAuFoil R1.2/1.3 | |||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 298.15 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 105000 X / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 1000 nm / Cs: 2.7 mm |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 2.6 sec. / 電子線照射量: 50.812 e/Å2 / 検出モード: COUNTING / フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 5684 |
| 電子光学装置 | エネルギーフィルター名称: GIF Bioquantum / エネルギーフィルタースリット幅: 20 eV |
| 画像スキャン | 動画フレーム数/画像: 50 / 利用したフレーム数/画像: 1-50 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 1561870 | ||||||||||||||||||||||||||||
| 対称性 | 点対称性: C4 (4回回転対称) | ||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.9 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 202148 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: FLEXIBLE FIT / 空間: REAL | ||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6VY0 Accession code: 6VY0 / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー





 PDBj
PDBj