登録情報 データベース : PDB / ID : 7t1bタイトル Rev1 Ternary Complex with rCTP and Ca2+ DNA (5'-D(*AP*TP*CP*GP*CP*TP*AP*CP*CP*AP*CP*AP*CP*CP*CP*C)-3')DNA (5'-D(P*GP*GP*GP*GP*TP*GP*TP*GP*GP*TP*AP*G)-3')DNA repair protein REV1 キーワード / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Saccharomyces cerevisiae (パン酵母)synthetic construct (人工物) 手法 / / 解像度 : 1.75 Å データ登録者 Freudenthal, B.D. / Weaver, T.M. 資金援助 組織 認可番号 国 National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS)
ジャーナル : Nat Commun / 年 : 2022タイトル : Mechanism of nucleotide discrimination by the translesion synthesis polymerase Rev1.著者 : Weaver, T.M. / Click, T.H. / Khoang, T.H. / Todd Washington, M. / Agarwal, P.K. / Freudenthal, B.D. 履歴 登録 2021年12月1日 登録サイト / 処理サイト 改定 1.0 2022年5月25日 Provider / タイプ 改定 1.1 2022年6月8日 Group / カテゴリ / citation_authorItem _citation.country / _citation.journal_abbrev ... _citation.country / _citation.journal_abbrev / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year 改定 1.2 2023年10月18日 Group / Refinement descriptionカテゴリ / chem_comp_bond / pdbx_initial_refinement_model
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  分子置換 / 解像度: 1.75 Å
分子置換 / 解像度: 1.75 Å  データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: Nat Commun / 年: 2022
ジャーナル: Nat Commun / 年: 2022 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 7t1b.cif.gz
7t1b.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb7t1b.ent.gz
pdb7t1b.ent.gz PDB形式
PDB形式 7t1b.json.gz
7t1b.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 7t1b_validation.pdf.gz
7t1b_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 7t1b_full_validation.pdf.gz
7t1b_full_validation.pdf.gz 7t1b_validation.xml.gz
7t1b_validation.xml.gz 7t1b_validation.cif.gz
7t1b_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/t1/7t1b
https://data.pdbj.org/pub/pdb/validation_reports/t1/7t1b ftp://data.pdbj.org/pub/pdb/validation_reports/t1/7t1b
ftp://data.pdbj.org/pub/pdb/validation_reports/t1/7t1b リンク
リンク 集合体
集合体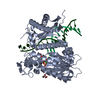
 要素
要素







 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 回転陽極 / タイプ: RIGAKU MICROMAX-007 HF / 波長: 1.54 Å
回転陽極 / タイプ: RIGAKU MICROMAX-007 HF / 波長: 1.54 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー







 PDBj
PDBj











































