[English] 日本語
 Yorodumi
Yorodumi- PDB-7odb: Crystal structure of bovine Hsc70(aa1-554)E213A/D214A in complex ... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7odb | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of bovine Hsc70(aa1-554)E213A/D214A in complex with triazine-derivative | ||||||
 Components Components | Heat shock cognate 71 kDa protein | ||||||
 Keywords Keywords | CHAPERONE | ||||||
| Function / homology |  Function and homology information Function and homology informationRegulation of HSF1-mediated heat shock response / Attenuation phase / HSF1-dependent transactivation / Protein methylation / GABA synthesis, release, reuptake and degradation / PKR-mediated signaling / mRNA Splicing - Major Pathway / synaptic vesicle uncoating / HSP90 chaperone cycle for steroid hormone receptors (SHR) in the presence of ligand / protein targeting to lysosome involved in chaperone-mediated autophagy ...Regulation of HSF1-mediated heat shock response / Attenuation phase / HSF1-dependent transactivation / Protein methylation / GABA synthesis, release, reuptake and degradation / PKR-mediated signaling / mRNA Splicing - Major Pathway / synaptic vesicle uncoating / HSP90 chaperone cycle for steroid hormone receptors (SHR) in the presence of ligand / protein targeting to lysosome involved in chaperone-mediated autophagy / AUF1 (hnRNP D0) binds and destabilizes mRNA / clathrin coat disassembly / Clathrin-mediated endocytosis / Neutrophil degranulation / non-chaperonin molecular chaperone ATPase / Prp19 complex / heat shock protein binding / protein folding chaperone / RNA splicing / spliceosomal complex / ATP-dependent protein folding chaperone / mRNA processing / melanosome / protein refolding / presynapse / protein-macromolecule adaptor activity / ribonucleoprotein complex / lysosomal membrane / negative regulation of DNA-templated transcription / nucleolus / ATP hydrolysis activity / ATP binding / nucleus / plasma membrane / cytoplasm / cytosol Similarity search - Function | ||||||
| Biological species |  | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.662 Å MOLECULAR REPLACEMENT / Resolution: 1.662 Å | ||||||
 Authors Authors | Zehe, M. / Grimm, C. / Sotriffer, C. | ||||||
 Citation Citation |  Journal: Acs Chem.Biol. / Year: 2024 Journal: Acs Chem.Biol. / Year: 2024Title: Combined In-Solution Fragment Screening and Crystallographic Binding-Mode Analysis with a Two-Domain Hsp70 Construct. Authors: Zehe, M. / Kehrein, J. / Schollmayer, C. / Plank, C. / Kovacs, H. / Merino Asumendi, E. / Holzgrabe, U. / Grimm, C. / Sotriffer, C. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7odb.cif.gz 7odb.cif.gz | 264.1 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7odb.ent.gz pdb7odb.ent.gz | 187.4 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7odb.json.gz 7odb.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/od/7odb https://data.pdbj.org/pub/pdb/validation_reports/od/7odb ftp://data.pdbj.org/pub/pdb/validation_reports/od/7odb ftp://data.pdbj.org/pub/pdb/validation_reports/od/7odb | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  6h54C  7o6rC  7oddC  7odiC  7plkC  4fl9S C: citing same article ( S: Starting model for refinement |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 60978.867 Da / Num. of mol.: 1 / Mutation: E213A, D214A Source method: isolated from a genetically manipulated source Source: (gene. exp.)   |
|---|
-Non-polymers , 5 types, 449 molecules 


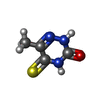





| #2: Chemical | ChemComp-EPE / | ||||||
|---|---|---|---|---|---|---|---|
| #3: Chemical | | #4: Chemical | #5: Chemical | ChemComp-V8Q / | #6: Water | ChemComp-HOH / | |
-Details
| Has ligand of interest | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.31 Å3/Da / Density % sol: 46.67 % |
|---|---|
| Crystal grow | Temperature: 291 K / Method: microbatch / pH: 7.5 Details: PEG 8000, TMAO. potassium chloride, HEPES-NaOH, glycerol |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  PETRA III, EMBL c/o DESY PETRA III, EMBL c/o DESY  / Beamline: P13 (MX1) / Wavelength: 0.9763 Å / Beamline: P13 (MX1) / Wavelength: 0.9763 Å |
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: May 31, 2019 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.9763 Å / Relative weight: 1 |
| Reflection | Resolution: 1.66→85.4 Å / Num. obs: 64069 / % possible obs: 97.5 % / Redundancy: 4.9 % / Biso Wilson estimate: 26.61 Å2 / CC1/2: 0.999 / Rrim(I) all: 0.06 / Net I/σ(I): 14.33 |
| Reflection shell | Resolution: 1.66→1.76 Å / Mean I/σ(I) obs: 1.17 / Num. unique obs: 8985 / CC1/2: 0.686 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 4FL9 Resolution: 1.662→64.61 Å / SU ML: 0.2345 / Cross valid method: FREE R-VALUE / σ(F): 1.34 / Phase error: 24.3356 / Stereochemistry target values: CDL v1.2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 34.22 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.662→64.61 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller


 PDBj
PDBj




