| Entry | Database: PDB / ID: 7ahm
|
|---|
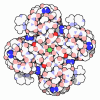
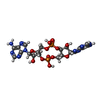
| Title | Low-resolution structure of the K+/H+ antiporter subunit KhtT in complex with c-di-AMP |
|---|
 Components Components | K(+)/H(+) antiporter subunit KhtT |
|---|
 Keywords Keywords | TRANSPORT PROTEIN / Regulatory protein of K+/H+ antiporter / c-di-AMP binding protein |
|---|
| Function / homology |  Function and homology information Function and homology information
Potassium/proton antiporter subunit KhtT / : / K(+)/H(+) antiporter subunit KhtT, N-terminal domain / : / Regulator of K+ conductance, C-terminal domain / Regulator of K+ conductance, C-terminal / Regulator of K+ conductance, C-terminal domain superfamily / TrkA-C domain / RCK C-terminal domain profile. / Alpha-Beta Plaits ...Potassium/proton antiporter subunit KhtT / : / K(+)/H(+) antiporter subunit KhtT, N-terminal domain / : / Regulator of K+ conductance, C-terminal domain / Regulator of K+ conductance, C-terminal / Regulator of K+ conductance, C-terminal domain superfamily / TrkA-C domain / RCK C-terminal domain profile. / Alpha-Beta Plaits / 2-Layer Sandwich / Alpha BetaSimilarity search - Domain/homology |
|---|
| Biological species |   Bacillus subtilis (bacteria) Bacillus subtilis (bacteria) |
|---|
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 3.14 Å MOLECULAR REPLACEMENT / Resolution: 3.14 Å |
|---|
 Authors Authors | Cereija, T.B. / Guerra, J.P. / Morais-Cabral, J.H. |
|---|
| Funding support |  Portugal, 1items Portugal, 1items | Organization | Grant number | Country |
|---|
| Fundacao para a Ciencia e a Tecnologia | POCI-01-0145-FEDER-029863(PTDC/BIA-BQM/29863/2017) |  Portugal Portugal |
|
|---|
 Citation Citation |  Journal: Proc.Natl.Acad.Sci.USA / Year: 2021 Journal: Proc.Natl.Acad.Sci.USA / Year: 2021
Title: c-di-AMP, a likely master regulator of bacterial K + homeostasis machinery, activates a K + exporter.
Authors: Cereija, T.B. / Guerra, J.P.L. / Jorge, J.M.P. / Morais-Cabral, J.H. |
|---|
| History | | Deposition | Sep 24, 2020 | Deposition site: PDBE / Processing site: PDBE |
|---|
| Revision 1.0 | Mar 31, 2021 | Provider: repository / Type: Initial release |
|---|
| Revision 1.1 | Apr 7, 2021 | Group: Database references / Category: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.pdbx_database_id_DOI / _citation.title / _citation.year / _citation_author.identifier_ORCID / _citation_author.name |
|---|
| Revision 1.2 | Apr 14, 2021 | Group: Database references / Category: citation / Item: _citation.pdbx_database_id_PubMed / _citation.title |
|---|
| Revision 1.3 | Jan 31, 2024 | Group: Data collection / Database references / Refinement description
Category: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 Yorodumi
Yorodumi Open data
Open data Basic information
Basic information Components
Components Keywords
Keywords Function and homology information
Function and homology information
 X-RAY DIFFRACTION /
X-RAY DIFFRACTION /  SYNCHROTRON /
SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 3.14 Å
MOLECULAR REPLACEMENT / Resolution: 3.14 Å  Authors
Authors Portugal, 1items
Portugal, 1items  Citation
Citation Journal: Proc.Natl.Acad.Sci.USA / Year: 2021
Journal: Proc.Natl.Acad.Sci.USA / Year: 2021 Structure visualization
Structure visualization Molmil
Molmil Jmol/JSmol
Jmol/JSmol Downloads & links
Downloads & links Download
Download 7ahm.cif.gz
7ahm.cif.gz PDBx/mmCIF format
PDBx/mmCIF format pdb7ahm.ent.gz
pdb7ahm.ent.gz PDB format
PDB format 7ahm.json.gz
7ahm.json.gz PDBx/mmJSON format
PDBx/mmJSON format Other downloads
Other downloads https://data.pdbj.org/pub/pdb/validation_reports/ah/7ahm
https://data.pdbj.org/pub/pdb/validation_reports/ah/7ahm ftp://data.pdbj.org/pub/pdb/validation_reports/ah/7ahm
ftp://data.pdbj.org/pub/pdb/validation_reports/ah/7ahm



 Links
Links Assembly
Assembly

 Components
Components

 X-RAY DIFFRACTION / Number of used crystals: 1
X-RAY DIFFRACTION / Number of used crystals: 1  Sample preparation
Sample preparation SYNCHROTRON / Site:
SYNCHROTRON / Site:  ALBA
ALBA  / Beamline: XALOC / Wavelength: 0.97926 Å
/ Beamline: XALOC / Wavelength: 0.97926 Å Processing
Processing MOLECULAR REPLACEMENT
MOLECULAR REPLACEMENT Movie
Movie Controller
Controller












 PDBj
PDBj