+ データを開く
データを開く
- 基本情報
基本情報
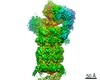
| 登録情報 | データベース: PDB / ID: 6wjd | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SA-like state of human 26S Proteasome with non-cleavable M1-linked hexaubiquitin and E3 ubiquitin ligase E6AP/UBE3A | ||||||||||||
 要素 要素 |
| ||||||||||||
 キーワード キーワード | HYDROLASE/PROTEIN BINDING / 26S protease / ubiquitin / complex / subunit / HYDROLASE-PROTEIN BINDING complex | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報thyrotropin-releasing hormone receptor binding / nuclear proteasome complex / host-mediated perturbation of viral transcription / positive regulation of inclusion body assembly / Impaired BRCA2 translocation to the nucleus / Impaired BRCA2 binding to SEM1 (DSS1) / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; オメガペプチターゼ / proteasome accessory complex / integrator complex / purine ribonucleoside triphosphate binding ...thyrotropin-releasing hormone receptor binding / nuclear proteasome complex / host-mediated perturbation of viral transcription / positive regulation of inclusion body assembly / Impaired BRCA2 translocation to the nucleus / Impaired BRCA2 binding to SEM1 (DSS1) / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; オメガペプチターゼ / proteasome accessory complex / integrator complex / purine ribonucleoside triphosphate binding / meiosis I / proteasome regulatory particle / cytosolic proteasome complex / positive regulation of proteasomal protein catabolic process / proteasome-activating activity / proteasome regulatory particle, lid subcomplex / proteasome regulatory particle, base subcomplex / metal-dependent deubiquitinase activity / protein K63-linked deubiquitination / negative regulation of programmed cell death / Regulation of ornithine decarboxylase (ODC) / Proteasome assembly / Cross-presentation of soluble exogenous antigens (endosomes) / proteasome core complex / Homologous DNA Pairing and Strand Exchange / Defective homologous recombination repair (HRR) due to BRCA1 loss of function / Defective HDR through Homologous Recombination Repair (HRR) due to PALB2 loss of BRCA1 binding function / Defective HDR through Homologous Recombination Repair (HRR) due to PALB2 loss of BRCA2/RAD51/RAD51C binding function / Resolution of D-loop Structures through Synthesis-Dependent Strand Annealing (SDSA) / Somitogenesis / Resolution of D-loop Structures through Holliday Junction Intermediates / K63-linked deubiquitinase activity / Impaired BRCA2 binding to RAD51 / proteasome binding / transcription factor binding / regulation of protein catabolic process / myofibril / proteasome storage granule / Presynaptic phase of homologous DNA pairing and strand exchange / general transcription initiation factor binding / blastocyst development / polyubiquitin modification-dependent protein binding / immune system process / protein deubiquitination / NF-kappaB binding / proteasome endopeptidase complex / endopeptidase activator activity / proteasome core complex, beta-subunit complex / proteasome assembly / mRNA export from nucleus / threonine-type endopeptidase activity / proteasome core complex, alpha-subunit complex / enzyme regulator activity / regulation of proteasomal protein catabolic process / Maturation of protein E / inclusion body / Maturation of protein E / ER Quality Control Compartment (ERQC) / Myoclonic epilepsy of Lafora / FLT3 signaling by CBL mutants / Prevention of phagosomal-lysosomal fusion / IRAK2 mediated activation of TAK1 complex / Alpha-protein kinase 1 signaling pathway / Glycogen synthesis / IRAK1 recruits IKK complex / IRAK1 recruits IKK complex upon TLR7/8 or 9 stimulation / Endosomal Sorting Complex Required For Transport (ESCRT) / Membrane binding and targetting of GAG proteins / Negative regulation of FLT3 / Regulation of TBK1, IKKε (IKBKE)-mediated activation of IRF3, IRF7 / PTK6 Regulates RTKs and Their Effectors AKT1 and DOK1 / Regulation of TBK1, IKKε-mediated activation of IRF3, IRF7 upon TLR3 ligation / Constitutive Signaling by NOTCH1 HD Domain Mutants / IRAK2 mediated activation of TAK1 complex upon TLR7/8 or 9 stimulation / NOTCH2 Activation and Transmission of Signal to the Nucleus / TICAM1,TRAF6-dependent induction of TAK1 complex / TICAM1-dependent activation of IRF3/IRF7 / APC/C:Cdc20 mediated degradation of Cyclin B / Downregulation of ERBB4 signaling / Regulation of FZD by ubiquitination / APC-Cdc20 mediated degradation of Nek2A / p75NTR recruits signalling complexes / InlA-mediated entry of Listeria monocytogenes into host cells / TRAF6 mediated IRF7 activation in TLR7/8 or 9 signaling / TRAF6-mediated induction of TAK1 complex within TLR4 complex / Regulation of pyruvate metabolism / NF-kB is activated and signals survival / Regulation of innate immune responses to cytosolic DNA / Downregulation of ERBB2:ERBB3 signaling / Pexophagy / NRIF signals cell death from the nucleus / VLDLR internalisation and degradation / Regulation of PTEN localization / TBP-class protein binding / proteolysis involved in protein catabolic process / proteasome complex / Activated NOTCH1 Transmits Signal to the Nucleus / Regulation of BACH1 activity / Synthesis of active ubiquitin: roles of E1 and E2 enzymes / MAP3K8 (TPL2)-dependent MAPK1/3 activation 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.8 Å | ||||||||||||
 データ登録者 データ登録者 | Chen, X. / Walters, K.J. | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2020 ジャーナル: Structure / 年: 2020タイトル: Cryo-EM Reveals Unanchored M1-Ubiquitin Chain Binding at hRpn11 of the 26S Proteasome. 著者: Xiang Chen / Zachary Dorris / Dan Shi / Rick K Huang / Htet Khant / Tara Fox / Natalia de Val / Dewight Williams / Ping Zhang / Kylie J Walters /  要旨: The 26S proteasome is specialized for regulated protein degradation and formed by a dynamic regulatory particle (RP) that caps a hollow cylindrical core particle (CP) where substrates are proteolyzed. ...The 26S proteasome is specialized for regulated protein degradation and formed by a dynamic regulatory particle (RP) that caps a hollow cylindrical core particle (CP) where substrates are proteolyzed. Its diverse substrates unify as proteasome targets by ubiquitination. We used cryogenic electron microscopy (cryo-EM) to study how human 26S proteasome interacts with M1-linked hexaubiquitin (M1-Ub) unanchored to a substrate and E3 ubiquitin ligase E6AP/UBE3A. Proteasome structures are available with model substrates extending through the RP ATPase ring and substrate-conjugated K63-linked ubiquitin chains present at inhibited deubiquitinating enzyme hRpn11 and the nearby ATPase hRpt4/hRpt5 coiled coil. In this study, we find M1-Ub at the hRpn11 site despite the absence of conjugated substrate, indicating that ubiquitin binding at this location does not require substrate interaction with the RP. Moreover, unanchored M1-Ub binds to this hRpn11 site of the proteasome with the CP gating residues in both the closed and opened conformational states. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6wjd.cif.gz 6wjd.cif.gz | 2.2 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6wjd.ent.gz pdb6wjd.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  6wjd.json.gz 6wjd.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6wjd_validation.pdf.gz 6wjd_validation.pdf.gz | 1.3 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6wjd_full_validation.pdf.gz 6wjd_full_validation.pdf.gz | 1.4 MB | 表示 | |
| XML形式データ |  6wjd_validation.xml.gz 6wjd_validation.xml.gz | 295.8 KB | 表示 | |
| CIF形式データ |  6wjd_validation.cif.gz 6wjd_validation.cif.gz | 478.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/wj/6wjd https://data.pdbj.org/pub/pdb/validation_reports/wj/6wjd ftp://data.pdbj.org/pub/pdb/validation_reports/wj/6wjd ftp://data.pdbj.org/pub/pdb/validation_reports/wj/6wjd | HTTPS FTP |
-関連構造データ
| 関連構造データ |  21691MC  6wjnC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10401 (タイトル: SA-like and SD-like states of human 26S Proteasome with non-cleavable M1-linked hexaubiquitin and E3 ubiquitin ligase E6AP/UBE3A EMPIAR-10401 (タイトル: SA-like and SD-like states of human 26S Proteasome with non-cleavable M1-linked hexaubiquitin and E3 ubiquitin ligase E6AP/UBE3AData size: 330.3 Data #1: Motion-corrected single frame micrographs of human 26S Proteasome with non-cleavable M1-linked hexaubiquitin and E3 ubiquitin ligase E6AP/UBE3A [micrographs - single frame]) |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-26S proteasome non-ATPase regulatory subunit ... , 11種, 11分子 UVWXYZabcdf
| #1: タンパク質 | 分子量: 105958.234 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q99460 Homo sapiens (ヒト) / 参照: UniProt: Q99460 |
|---|---|
| #2: タンパク質 | 分子量: 61066.500 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: O43242 Homo sapiens (ヒト) / 参照: UniProt: O43242 |
| #3: タンパク質 | 分子量: 52979.359 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: O00232 Homo sapiens (ヒト) / 参照: UniProt: O00232 |
| #4: タンパク質 | 分子量: 47526.688 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: O00231 Homo sapiens (ヒト) / 参照: UniProt: O00231 |
| #5: タンパク質 | 分子量: 45592.285 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q15008 Homo sapiens (ヒト) / 参照: UniProt: Q15008 |
| #6: タンパク質 | 分子量: 37086.441 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P51665 Homo sapiens (ヒト) / 参照: UniProt: P51665 |
| #7: タンパク質 | 分子量: 42995.359 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q9UNM6 Homo sapiens (ヒト) / 参照: UniProt: Q9UNM6 |
| #8: タンパク質 | 分子量: 40781.590 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P55036 Homo sapiens (ヒト) / 参照: UniProt: P55036 |
| #9: タンパク質 | 分子量: 34488.824 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) Homo sapiens (ヒト)参照: UniProt: O00487, 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; オメガペプチターゼ |
| #10: タンパク質 | 分子量: 39536.676 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P48556 Homo sapiens (ヒト) / 参照: UniProt: P48556 |
| #12: タンパク質 | 分子量: 100313.625 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q13200 Homo sapiens (ヒト) / 参照: UniProt: Q13200 |
-タンパク質 , 2種, 2分子 eu
| #11: タンパク質 | 分子量: 8284.611 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P60896 Homo sapiens (ヒト) / 参照: UniProt: P60896 |
|---|---|
| #19: タンパク質 | 分子量: 8576.831 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P0CG48 Homo sapiens (ヒト) / 参照: UniProt: P0CG48 |
-26S proteasome regulatory subunit ... , 6種, 6分子 ABCDEF
| #13: タンパク質 | 分子量: 48700.805 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P35998 Homo sapiens (ヒト) / 参照: UniProt: P35998 |
|---|---|
| #14: タンパク質 | 分子量: 49260.504 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P62191 Homo sapiens (ヒト) / 参照: UniProt: P62191 |
| #15: タンパク質 | 分子量: 44852.121 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P62195 Homo sapiens (ヒト) / 参照: UniProt: P62195 |
| #16: タンパク質 | 分子量: 47426.141 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P43686 Homo sapiens (ヒト) / 参照: UniProt: P43686 |
| #17: タンパク質 | 分子量: 45867.027 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: A0A087X2I1 Homo sapiens (ヒト) / 参照: UniProt: A0A087X2I1 |
| #18: タンパク質 | 分子量: 49266.457 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P17980 Homo sapiens (ヒト) / 参照: UniProt: P17980 |
-Proteasome subunit alpha type- ... , 7種, 14分子 GgHhIiJjKkLlMm
| #20: タンパク質 | 分子量: 27301.262 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P60900, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P60900, proteasome endopeptidase complex#21: タンパク質 | 分子量: 25796.338 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P25787, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P25787, proteasome endopeptidase complex#22: タンパク質 | 分子量: 29394.648 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P25789, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P25789, proteasome endopeptidase complex#23: タンパク質 | 分子量: 27798.695 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: O14818, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: O14818, proteasome endopeptidase complex#24: タンパク質 | 分子量: 26304.779 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P28066, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P28066, proteasome endopeptidase complex#25: タンパク質 | 分子量: 30150.277 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P25786, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P25786, proteasome endopeptidase complex#26: タンパク質 | 分子量: 28338.057 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P25788, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P25788, proteasome endopeptidase complex |
|---|
-Proteasome subunit beta type- ... , 7種, 14分子 NnOoPpQqRrSsTt
| #27: タンパク質 | 分子量: 25246.455 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P28072, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P28072, proteasome endopeptidase complex#28: タンパク質 | 分子量: 29869.223 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q99436, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: Q99436, proteasome endopeptidase complex#29: タンパク質 | 分子量: 22841.701 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P49720, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P49720, proteasome endopeptidase complex#30: タンパク質 | 分子量: 22864.277 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P49721, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P49721, proteasome endopeptidase complex#31: タンパク質 | 分子量: 28379.053 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P28074, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P28074, proteasome endopeptidase complex#32: タンパク質 | 分子量: 26391.201 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P20618, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P20618, proteasome endopeptidase complex#33: タンパク質 | 分子量: 29099.986 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P28070, proteasome endopeptidase complex Homo sapiens (ヒト) / 参照: UniProt: P28070, proteasome endopeptidase complex |
|---|
-非ポリマー , 4種, 12分子 






| #34: 化合物 | ChemComp-ZN / | ||||
|---|---|---|---|---|---|
| #35: 化合物 | ChemComp-AGS / #36: 化合物 | ChemComp-MG / #37: 化合物 | |
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Human 26S Proteasome with non-cleavable M1-linked hexaubiquitin and E3 ubiquitin ligase E6AP/UBE3A タイプ: COMPLEX / Entity ID: #1-#33 / 由来: NATURAL | |||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||||||||||||||||||||||||||||
| 緩衝液 | pH: 7.5 詳細: 50 mM Tris, pH 7.5, 50 mM NaCl, 1.5 mM ATP-gamma-S, 5 mM MgCl2, 2 mM DTT, 10 uM zinc sulfate | |||||||||||||||||||||||||||||||||||
| 緩衝液成分 |
| |||||||||||||||||||||||||||||||||||
| 試料 | 濃度: 1 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | |||||||||||||||||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 200 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 | |||||||||||||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 291.15 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 0.2 sec. / 電子線照射量: 36.64 e/Å2 / 検出モード: SUPER-RESOLUTION フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 撮影したグリッド数: 1 / 実像数: 6216 |
| 画像スキャン | 動画フレーム数/画像: 40 / 利用したフレーム数/画像: 1-40 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 1050369 | ||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 4.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 37698 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL | ||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6MSD Accession code: 6MSD / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj



























