+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6rks | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | E. coli DNA Gyrase - DNA binding and cleavage domain in State 1 without TOPRIM insertion | ||||||||||||
 要素 要素 |
| ||||||||||||
 キーワード キーワード | ISOMERASE / Complex / DNA Gyrase / Inhibitor / DNA BINDING PROTEIN | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of DNA-templated DNA replication / DNA topoisomerase type II (double strand cut, ATP-hydrolyzing) activity / DNA topoisomerase type II (double strand cut, ATP-hydrolyzing) complex / DNA negative supercoiling activity / DNA topoisomerase (ATP-hydrolysing) / DNA topological change / ATP-dependent activity, acting on DNA / DNA-templated DNA replication / chromosome / response to xenobiotic stimulus ...negative regulation of DNA-templated DNA replication / DNA topoisomerase type II (double strand cut, ATP-hydrolyzing) activity / DNA topoisomerase type II (double strand cut, ATP-hydrolyzing) complex / DNA negative supercoiling activity / DNA topoisomerase (ATP-hydrolysing) / DNA topological change / ATP-dependent activity, acting on DNA / DNA-templated DNA replication / chromosome / response to xenobiotic stimulus / response to antibiotic / DNA-templated transcription / DNA binding / ATP binding / metal ion binding / identical protein binding / membrane / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||||||||
| 生物種 |   | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4 Å | ||||||||||||
 データ登録者 データ登録者 | Vanden Broeck, A. / Lamour, V. | ||||||||||||
| 資金援助 |  フランス, 3件 フランス, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019タイトル: Cryo-EM structure of the complete E. coli DNA gyrase nucleoprotein complex. 著者: Arnaud Vanden Broeck / Christophe Lotz / Julio Ortiz / Valérie Lamour /  要旨: DNA gyrase is an essential enzyme involved in the homeostatic control of DNA supercoiling and the target of successful antibacterial compounds. Despite extensive studies, a detailed architecture of ...DNA gyrase is an essential enzyme involved in the homeostatic control of DNA supercoiling and the target of successful antibacterial compounds. Despite extensive studies, a detailed architecture of the full-length DNA gyrase from the model organism E. coli is still missing. Herein, we report the complete structure of the E. coli DNA gyrase nucleoprotein complex trapped by the antibiotic gepotidacin, using phase-plate single-particle cryo-electron microscopy. Our data unveil the structural and spatial organization of the functional domains, their connections and the position of the conserved GyrA-box motif. The deconvolution of two states of the DNA-binding/cleavage domain provides a better understanding of the allosteric movements of the enzyme complex. The local atomic resolution in the DNA-bound area reaching up to 3.0 Å enables the identification of the antibiotic density. Altogether, this study paves the way for the cryo-EM determination of gyrase complexes with antibiotics and opens perspectives for targeting conformational intermediates. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6rks.cif.gz 6rks.cif.gz | 323.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6rks.ent.gz pdb6rks.ent.gz | 235.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6rks.json.gz 6rks.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6rks_validation.pdf.gz 6rks_validation.pdf.gz | 923.3 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6rks_full_validation.pdf.gz 6rks_full_validation.pdf.gz | 933.1 KB | 表示 | |
| XML形式データ |  6rks_validation.xml.gz 6rks_validation.xml.gz | 49.1 KB | 表示 | |
| CIF形式データ |  6rks_validation.cif.gz 6rks_validation.cif.gz | 74.9 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rk/6rks https://data.pdbj.org/pub/pdb/validation_reports/rk/6rks ftp://data.pdbj.org/pub/pdb/validation_reports/rk/6rks ftp://data.pdbj.org/pub/pdb/validation_reports/rk/6rks | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4909MC  4910C  4912C  4913C  4914C  4915C  6rkuC  6rkvC  6rkwC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
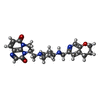
| #1: タンパク質 | 分子量: 97088.586 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   参照: UniProt: P0AES4, DNA topoisomerase (ATP-hydrolysing) #2: タンパク質 | 分子量: 90073.922 Da / 分子数: 2 / 由来タイプ: 組換発現 / 詳細: GyrB subunit DNA Binding and cleavage domain / 由来: (組換発現)  遺伝子: gyrB, acrB, cou, himB, hisU, nalC, parA, pcbA, b3699, JW5625 発現宿主:  参照: UniProt: P0AES6, DNA topoisomerase (ATP-hydrolysing) #3: DNA鎖 | 分子量: 4288.818 Da / 分子数: 2 / 由来タイプ: 合成 / 由来: (合成)  #4: DNA鎖 | 分子量: 5506.578 Da / 分子数: 2 / 由来タイプ: 合成 / 由来: (合成)  #5: 化合物 | ChemComp-JHN / ( | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| |||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 単位: MEGADALTONS / 実験値: NO | |||||||||||||||||||||||||||||||||||
| 由来(天然) |
| |||||||||||||||||||||||||||||||||||
| 由来(組換発現) |
| |||||||||||||||||||||||||||||||||||
| 緩衝液 | pH: 8 | |||||||||||||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | |||||||||||||||||||||||||||||||||||
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 130000 X / 最大 デフォーカス(公称値): 800 nm / 最小 デフォーカス(公称値): 300 nm / Cs: 0.01 mm |
| 撮影 | 電子線照射量: 50 e/Å2 / 検出モード: SUPER-RESOLUTION フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
| 電子光学装置 | エネルギーフィルタースリット幅: 20 eV / 位相板: VOLTA PHASE PLATE |
| 画像スキャン | 動画フレーム数/画像: 40 / 利用したフレーム数/画像: 3-40 |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.12_2829: / 分類: 精密化 | ||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 1572962 | ||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C2 (2回回転対称) | ||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 60548 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||
| 原子モデル構築 | 空間: REAL | ||||||||||||||||||||||||||||||||
| 原子モデル構築 | 3D fitting-ID: 1 / Accession code: 3NUH / Initial refinement model-ID: 1 / PDB-ID: 3NUH / Source name: PDB / タイプ: experimental model
| ||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj