| 登録情報 | データベース: PDB / ID: 6jck
|
|---|
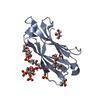
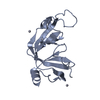
| タイトル | Complex structure of Axin-DIX and Dvl2-DIX |
|---|
 要素 要素 | - Axin-1
- Segment polarity protein dishevelled homolog DVL-2
|
|---|
 キーワード キーワード | SIGNALING PROTEIN / Wnt signalling |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
beta-catenin destruction complex assembly / Negative regulation of TCF-dependent signaling by DVL-interacting proteins / convergent extension involved in neural plate elongation / armadillo repeat domain binding / segment specification / head development / WNT5A-dependent internalization of FZD4 / cell development / positive regulation of neuron projection arborization / axial mesoderm formation ...beta-catenin destruction complex assembly / Negative regulation of TCF-dependent signaling by DVL-interacting proteins / convergent extension involved in neural plate elongation / armadillo repeat domain binding / segment specification / head development / WNT5A-dependent internalization of FZD4 / cell development / positive regulation of neuron projection arborization / axial mesoderm formation / dorsal/ventral axis specification / non-canonical Wnt signaling pathway / cochlea morphogenesis / clathrin-coated endocytic vesicle / WNT5:FZD7-mediated leishmania damping / post-anal tail morphogenesis / beta-catenin destruction complex / APC truncation mutants have impaired AXIN binding / AXIN missense mutants destabilize the destruction complex / Truncations of AMER1 destabilize the destruction complex / Signaling by Hippo / frizzled binding / Beta-catenin phosphorylation cascade / Signaling by GSK3beta mutants / CTNNB1 S33 mutants aren't phosphorylated / CTNNB1 S37 mutants aren't phosphorylated / CTNNB1 S45 mutants aren't phosphorylated / CTNNB1 T41 mutants aren't phosphorylated / I-SMAD binding / PCP/CE pathway / Wnt signalosome / WNT mediated activation of DVL / Disassembly of the destruction complex and recruitment of AXIN to the membrane / epigenetic programming in the zygotic pronuclei / negative regulation of protein metabolic process / Wnt signaling pathway, planar cell polarity pathway / aggresome / positive regulation of ubiquitin-dependent protein catabolic process / nucleocytoplasmic transport / RUNX1 regulates transcription of genes involved in WNT signaling / RUNX1 regulates estrogen receptor mediated transcription / small GTPase-mediated signal transduction / negative regulation of fat cell differentiation / heart looping / positive regulation of transforming growth factor beta receptor signaling pathway / SMAD binding / outflow tract morphogenesis / R-SMAD binding / negative regulation of transcription elongation by RNA polymerase II / lateral plasma membrane / canonical Wnt signaling pathway / positive regulation of signal transduction by p53 class mediator / ubiquitin-like ligase-substrate adaptor activity / cytoplasmic microtubule organization / signaling adaptor activity / positive regulation of protein ubiquitination / protein serine/threonine kinase binding / protein serine/threonine kinase activator activity / cell periphery / regulation of actin cytoskeleton organization / TCF dependent signaling in response to WNT / neural tube closure / Asymmetric localization of PCP proteins / Degradation of DVL / Degradation of AXIN / sensory perception of sound / RHO GTPases Activate Formins / negative regulation of canonical Wnt signaling pathway / beta-catenin binding / positive regulation of JNK cascade / Degradation of beta-catenin by the destruction complex / small GTPase binding / apical part of cell / protein polyubiquitination / p53 binding / positive regulation of protein catabolic process / intracellular protein localization / Cargo recognition for clathrin-mediated endocytosis / regulation of cell population proliferation / positive regulation of proteasomal ubiquitin-dependent protein catabolic process / Clathrin-mediated endocytosis / heart development / microtubule cytoskeleton / protein-containing complex assembly / cytoplasmic vesicle / cell cortex / Estrogen-dependent gene expression / molecular adaptor activity / in utero embryonic development / proteasome-mediated ubiquitin-dependent protein catabolic process / protein-macromolecule adaptor activity / Ub-specific processing proteases / nuclear body / protein domain specific binding / negative regulation of gene expression / apoptotic process / ubiquitin protein ligase binding / regulation of DNA-templated transcription / protein kinase binding / nucleolus類似検索 - 分子機能 Ribosomal Protein L25; Chain P - #130 / Dishevelled-2 / Axin beta-catenin binding / Axin-1/2, tankyrase-binding domain / Axin-like / Axin beta-catenin binding motif / Axin-1 tankyrase binding domain / Dishevelled protein domain / Dishevelled family / Dishevelled C-terminal ...Ribosomal Protein L25; Chain P - #130 / Dishevelled-2 / Axin beta-catenin binding / Axin-1/2, tankyrase-binding domain / Axin-like / Axin beta-catenin binding motif / Axin-1 tankyrase binding domain / Dishevelled protein domain / Dishevelled family / Dishevelled C-terminal / Dishevelled specific domain / Segment polarity protein dishevelled (Dsh) C terminal / Dishevelled-related protein / DIX domain / RGS, subdomain 1/3 / DIX domain superfamily / DIX domain / DIX domain profile. / Domain present in Dishevelled and axin / Ribosomal Protein L25; Chain P / Regulator of G protein signaling domain / Domain found in Dishevelled, Egl-10, and Pleckstrin (DEP) / DEP domain profile. / Domain found in Dishevelled, Egl-10, and Pleckstrin / DEP domain / RGS domain / RGS domain profile. / Regulator of G protein signalling domain / RGS, subdomain 2 / RGS domain superfamily / PDZ domain / PDZ domain profile. / Domain present in PSD-95, Dlg, and ZO-1/2. / PDZ domain / PDZ superfamily / Ubiquitin-like domain superfamily / Winged helix DNA-binding domain superfamily / Winged helix-like DNA-binding domain superfamily / Beta Barrel / Mainly Beta類似検索 - ドメイン・相同性 Segment polarity protein dishevelled homolog DVL-2 / Axin-1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.09 Å 分子置換 / 解像度: 3.09 Å |
|---|
 データ登録者 データ登録者 | Yamanishi, K. / Shibata, N. |
|---|
| 資金援助 |  日本, 2件 日本, 2件 | 組織 | 認可番号 | 国 |
|---|
| Ministry of Education, Culture, Sports, Science and Technology (Japan) | 23121526 |  日本 日本 | | Ministry of Education, Culture, Sports, Science and Technology (Japan) | 25121731 |  日本 日本 |
|
|---|
 引用 引用 |  ジャーナル: Sci.Signal. / 年: 2019 ジャーナル: Sci.Signal. / 年: 2019
タイトル: A direct heterotypic interaction between the DIX domains of Dishevelled and Axin mediates signaling to beta-catenin.
著者: Yamanishi, K. / Fiedler, M. / Terawaki, S.I. / Higuchi, Y. / Bienz, M. / Shibata, N. |
|---|
| 履歴 | | 登録 | 2019年1月29日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2020年1月15日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年11月22日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 3.09 Å
分子置換 / 解像度: 3.09 Å  データ登録者
データ登録者 日本, 2件
日本, 2件  引用
引用 ジャーナル: Sci.Signal. / 年: 2019
ジャーナル: Sci.Signal. / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6jck.cif.gz
6jck.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6jck.ent.gz
pdb6jck.ent.gz PDB形式
PDB形式 6jck.json.gz
6jck.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/jc/6jck
https://data.pdbj.org/pub/pdb/validation_reports/jc/6jck ftp://data.pdbj.org/pub/pdb/validation_reports/jc/6jck
ftp://data.pdbj.org/pub/pdb/validation_reports/jc/6jck リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: AXIN1, AXIN / プラスミド: pCold-GST / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: AXIN1, AXIN / プラスミド: pCold-GST / 発現宿主: 
 Homo sapiens (ヒト) / 遺伝子: DVL2 / プラスミド: pCold-GST / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: DVL2 / プラスミド: pCold-GST / 発現宿主: 
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SPring-8
SPring-8  / ビームライン: BL44XU / 波長: 0.9 Å
/ ビームライン: BL44XU / 波長: 0.9 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj










