| 登録情報 | データベース: PDB / ID: 6hvi
|
|---|
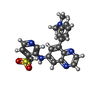
| タイトル | Human PFKFB3 in complex with a N-Aryl 6-Aminoquinoxaline inhibitor 2 |
|---|
 要素 要素 | 6-phosphofructo-2-kinase/fructose-2,6-bisphosphatase 3 |
|---|
 キーワード キーワード | TRANSFERASE / kinase / complex / metabolism / cancer |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
6-phosphofructo-2-kinase / 6-phosphofructo-2-kinase activity / fructose 2,6-bisphosphate metabolic process / fructose-2,6-bisphosphate 2-phosphatase / fructose-2,6-bisphosphate 2-phosphatase activity / Regulation of glycolysis by fructose 2,6-bisphosphate metabolism / glial cell differentiation / fructose metabolic process / motor behavior / glycolytic process ...6-phosphofructo-2-kinase / 6-phosphofructo-2-kinase activity / fructose 2,6-bisphosphate metabolic process / fructose-2,6-bisphosphate 2-phosphatase / fructose-2,6-bisphosphate 2-phosphatase activity / Regulation of glycolysis by fructose 2,6-bisphosphate metabolism / glial cell differentiation / fructose metabolic process / motor behavior / glycolytic process / apoptotic process / nucleoplasm / ATP binding / cytosol類似検索 - 分子機能 Fructose-2,6-bisphosphatase / 6-phosphofructo-2-kinase / 6-phosphofructo-2-kinase / Phosphoglycerate/bisphosphoglycerate mutase, active site / Phosphoglycerate mutase family phosphohistidine signature. / Phosphoglycerate mutase family / Phosphoglycerate mutase-like / Histidine phosphatase superfamily, clade-1 / Histidine phosphatase superfamily (branch 1) / Histidine phosphatase superfamily ...Fructose-2,6-bisphosphatase / 6-phosphofructo-2-kinase / 6-phosphofructo-2-kinase / Phosphoglycerate/bisphosphoglycerate mutase, active site / Phosphoglycerate mutase family phosphohistidine signature. / Phosphoglycerate mutase family / Phosphoglycerate mutase-like / Histidine phosphatase superfamily, clade-1 / Histidine phosphatase superfamily (branch 1) / Histidine phosphatase superfamily / P-loop containing nucleotide triphosphate hydrolases / Rossmann fold / P-loop containing nucleoside triphosphate hydrolase / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 6-O-phosphono-beta-D-fructofuranose / CITRATE ANION / Chem-GV5 / PYROPHOSPHATE 2- / 6-phosphofructo-2-kinase/fructose-2,6-bisphosphatase 3類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.96 Å 分子置換 / 解像度: 1.96 Å |
|---|
 データ登録者 データ登録者 | Banaszak, K. / Sowinska, M. / Gondela, A. / Fabritius, C.H. / Nowak, M. |
|---|
| 資金援助 | 1件 | 組織 | 認可番号 | 国 |
|---|
| European Regional Development Fund | POIG.01.04.00-12-120/12-00 | |
|
|---|
 引用 引用 |  ジャーナル: ChemMedChem / 年: 2019 ジャーナル: ChemMedChem / 年: 2019
タイトル: Discovery and Structure-Activity Relationships of N-Aryl 6-Aminoquinoxalines as Potent PFKFB3 Kinase Inhibitors.
著者: Boutard, N. / Bialas, A. / Sabiniarz, A. / Guzik, P. / Banaszak, K. / Biela, A. / Bien, M. / Buda, A. / Bugaj, B. / Cieluch, E. / Cierpich, A. / Dudek, L. / Eggenweiler, H.M. / Fogt, J. / ...著者: Boutard, N. / Bialas, A. / Sabiniarz, A. / Guzik, P. / Banaszak, K. / Biela, A. / Bien, M. / Buda, A. / Bugaj, B. / Cieluch, E. / Cierpich, A. / Dudek, L. / Eggenweiler, H.M. / Fogt, J. / Gaik, M. / Gondela, A. / Jakubiec, K. / Jurzak, M. / Kitlinska, A. / Kowalczyk, P. / Kujawa, M. / Kwiecinska, K. / Les, M. / Lindemann, R. / Maciuszek, M. / Mikulski, M. / Niedziejko, P. / Obara, A. / Pawlik, H. / Rzymski, T. / Sieprawska-Lupa, M. / Sowinska, M. / Szeremeta-Spisak, J. / Stachowicz, A. / Tomczyk, M.M. / Wiklik, K. / Wloszczak, L. / Ziemianska, S. / Zarebski, A. / Brzozka, K. / Nowak, M. / Fabritius, C.H. |
|---|
| 履歴 | | 登録 | 2018年10月11日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2018年11月14日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2019年1月16日 | Group: Data collection / Database references
カテゴリ: citation / citation_author / pdbx_database_proc
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation.year / _citation_author.name |
|---|
| 改定 1.2 | 2020年7月29日 | Group: Data collection / Derived calculations / Structure summary
カテゴリ: chem_comp / entity ...chem_comp / entity / pdbx_chem_comp_identifier / pdbx_entity_nonpoly / struct_site / struct_site_gen
Item: _chem_comp.mon_nstd_flag / _chem_comp.name ..._chem_comp.mon_nstd_flag / _chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_entity_nonpoly.name
解説: Carbohydrate remediation / Provider: repository / タイプ: Remediation |
|---|
| 改定 1.3 | 2024年5月15日 | Group: Data collection / Database references / Structure summary
カテゴリ: chem_comp / chem_comp_atom ...chem_comp / chem_comp_atom / chem_comp_bond / database_2
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.96 Å
分子置換 / 解像度: 1.96 Å  データ登録者
データ登録者 引用
引用 ジャーナル: ChemMedChem / 年: 2019
ジャーナル: ChemMedChem / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6hvi.cif.gz
6hvi.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6hvi.ent.gz
pdb6hvi.ent.gz PDB形式
PDB形式 6hvi.json.gz
6hvi.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6hvi_validation.pdf.gz
6hvi_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6hvi_full_validation.pdf.gz
6hvi_full_validation.pdf.gz 6hvi_validation.xml.gz
6hvi_validation.xml.gz 6hvi_validation.cif.gz
6hvi_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/hv/6hvi
https://data.pdbj.org/pub/pdb/validation_reports/hv/6hvi ftp://data.pdbj.org/pub/pdb/validation_reports/hv/6hvi
ftp://data.pdbj.org/pub/pdb/validation_reports/hv/6hvi リンク
リンク 集合体
集合体
 要素
要素

 Homo sapiens (ヒト) / 遺伝子: PFKFB3 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: PFKFB3 / 発現宿主: 






 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  BESSY
BESSY  / ビームライン: 14.1 / 波長: 0.91841 Å
/ ビームライン: 14.1 / 波長: 0.91841 Å 分子置換
分子置換 解析
解析 分子置換 / 解像度: 1.96→47.77 Å / Cor.coef. Fo:Fc: 0.956 / Cor.coef. Fo:Fc free: 0.947 / SU B: 2.998 / SU ML: 0.083 / SU R Cruickshank DPI: 0.1174 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R: 0.117 / ESU R Free: 0.111
分子置換 / 解像度: 1.96→47.77 Å / Cor.coef. Fo:Fc: 0.956 / Cor.coef. Fo:Fc free: 0.947 / SU B: 2.998 / SU ML: 0.083 / SU R Cruickshank DPI: 0.1174 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R: 0.117 / ESU R Free: 0.111  ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj



















