登録情報 データベース : PDB / ID : 5z5qタイトル Nukacin ISK-1 in active state Lantibiotic nukacin キーワード / 機能・相同性 / / / / / / 生物種 Staphylococcus warneri (バクテリア)手法 / データ登録者 Kohda, D. / Fujinami, D. ジャーナル : Commun Biol / 年 : 2018タイトル : The lantibiotic nukacin ISK-1 exists in an equilibrium between active and inactive lipid-II binding states.著者 : Fujinami, D. / Mahin, A.A. / Elsayed, K.M. / Islam, M.R. / Nagao, J.I. / Roy, U. / Momin, S. / Zendo, T. / Kohda, D. / Sonomoto, K. 履歴 登録 2018年1月19日 登録サイト / 処理サイト 改定 1.0 2018年11月28日 Provider / タイプ 改定 1.1 2023年6月14日 Group / Database references / Otherカテゴリ / pdbx_database_status / pdbx_nmr_spectrometerItem _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data / _pdbx_nmr_spectrometer.model 改定 2.0 2024年7月10日 Group Data collection / Database references ... Data collection / Database references / Derived calculations / Polymer sequence カテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / entity_poly / struct_conn Item / _entity_poly.pdbx_seq_one_letter_code_can / _struct_conn.pdbx_leaving_atom_flag
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
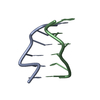
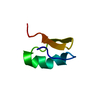
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Staphylococcus warneri (バクテリア)
Staphylococcus warneri (バクテリア) データ登録者
データ登録者 引用
引用 ジャーナル: Commun Biol / 年: 2018
ジャーナル: Commun Biol / 年: 2018 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5z5q.cif.gz
5z5q.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5z5q.ent.gz
pdb5z5q.ent.gz PDB形式
PDB形式 5z5q.json.gz
5z5q.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/z5/5z5q
https://data.pdbj.org/pub/pdb/validation_reports/z5/5z5q ftp://data.pdbj.org/pub/pdb/validation_reports/z5/5z5q
ftp://data.pdbj.org/pub/pdb/validation_reports/z5/5z5q
 リンク
リンク 集合体
集合体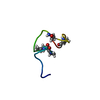
 要素
要素 Staphylococcus warneri (バクテリア) / 参照: UniProt: Q9KWM4
Staphylococcus warneri (バクテリア) / 参照: UniProt: Q9KWM4 試料調製
試料調製 解析
解析 CYANA / 開発者: Guntert P. / 分類: 精密化
CYANA / 開発者: Guntert P. / 分類: 精密化 ムービー
ムービー コントローラー
コントローラー



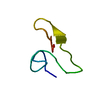

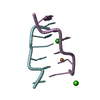
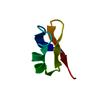


 PDBj
PDBj